Emilia Wójtowicz. Markery molekularne i ich wykorzystanie w hodowli roślin
|
|
|
- Halina Majewska
- 8 lat temu
- Przeglądów:
Transkrypt
1 Emilia Wójtowicz Markery molekularne i ich wykorzystanie w hodowli roślin W pracach genetyczno hodowlanych wykorzystuje się różne typy markerów (wyznaczników), pozwalających na szybką identyfikacje genotypów, co znacznie skraca cykl hodowlany i obniża koszty. Należą do nich markery morfologiczne, cytologiczne, oraz stosowane w ostatnich latach coraz częściej markery molekularne. Markery molekularne mają przewagę nad pozostałymi, gdyż umożliwiają identyfikację różnic i podobieństw niezależnie od wieku badanych obiektów. Do analiz wystarczają bardzo małe próbki materiału, zatem nie ma potrzeby niszczenia całego organizmu. Poza tym markery molekularne dziedziczą się zgodnie z genetyką mendlowską i nie podlegają wpływom środowiska. Pierwszymi wykorzystywanymi markerami molekularnym były różne formy białek strukturalnych i funkcjonalnych (izoenzymy) (Bednarek i Chwedorzewska, 2001). Umożliwiają one badanie struktury genetycznej populacji, oszacowanie stopnia heterozygotyczności i polimorfizmu, analizę stopnia podobieństwa genetycznego, jak również potwierdzenie czystości genetycznej lub mieszańcowości (Masojć, 2007). Jednak niewielka liczba loci izoenzymatycznych jest utrudnieniem w ich szerszym zastosowaniu (Broda, 2000). W ciągu ostatnich lat największego znaczenia nabrały markery DNA (Bednarek i Chwedorzewska, 2001). Są to fragmenty kwasu deoksyrybonukleinowego uzyskane w formie prążków na żelach lub membranach, będące efektem końcowym reakcji enzymatycznych lub hybrydyzacji (Wolko i in., 1999). Markery DNA odgrywają obecnie zasadniczą rolę we wszystkich aspektach hodowli roślin, od identyfikacji genów odpowiedzialnych za określone cechy do kierowania programami krzyżowań (Schulman, 2007). Przegląd technik RFLP (Restriction Fragment Length Polymorphism) Jedną z pierwszych metod, która umożliwiła identyfikację markerów DNA była technika analizy polimorfizmu fragmentów restrykcyjnych - RFLP (Masojć, 2007). Metoda ta opiera się na zróżnicowanym rozmieszczeniu w genomie specyficznych sekwencji DNA o długości 4-6 nukleotydów, rozpoznawanych i przecinanych przez specyficzne enzymy restrykcyjne. Powstałe po cięciu fragmenty hybrydyzują z wyznakowaną radioaktywnie sondą molekularną (Bostein i in., 1980). Polimorfizm markerów RFLP może wynikać ze zmian sekwencji nukleotydów w miejscach restrykcyjnych oraz z modyfikacji we fragmentach ulegających hybrydyzacji z sondą (Wolko i Kruszka, 1997). Metoda ta była używana do mapowania genomów (Malyshev i in. 2003), lokalizacji QTL (Jordan i in., 2004) oraz analizy pokrewieństwa genetycznego (Bautsta i in. 2001).
2 Markery VNTR (Variable Number of Tandem Repeats) Markery VNTR oparte są na analizie sekwencji minisatelitarnych powtarzających się motywów sekwencyjnych o długości pz, występujących w genomach (Nybom i Kraft, 1995). Motywy te wykazują duże zróżnicowanie pod względem długości, która zależy od liczby powtórzeń podstawowego motywu (Masojć, 2007). Polimorfizm minisatelitarnych loci wykrywany jest poprzez trawienie DNA enzymami restrykcyjnymi, które rozpoznają sekwencje otaczające te regiony. Dalsze etapy analizy przebiegają z zastosowaniem sond, komplementarnych do minisatelitarnego DNA, a w końcowym wyniku uzyskuje się profile molekularne, unikalne dla analizowanego osobnika (Sztuba Solińska, 2005). Opracowanie łańcuchowej reakcji polimerazy PCR (Polymerase Chain Reaction) stworzyło możliwość powstania kolejnych metod analizy molekularnej. RAPD (Random Amplified Polymorphic DNA) Markery RAPD bazują na reakcji PCR z wykorzystaniem krótkiego (9-11 nukleotydów) startera o przypadkowej sekwencji (Williams i in., 1990). Startery przyłączają się w wielu miejscach badanego DNA prowadząc do amplifikacji kilku lub kilkunastu różnych fragmentów (Wolko i in., 2001). Polimorfizm markerów RAPD wynika z mutacji miejsc przyłączania starterów oraz z inercji/delecji w obrębie powielanych podczas PCR fragmentów. Ze względu na dużą liczbę różnych sekwencji starterów metoda ta stała się szczególnie przydatna do poszukiwania markerów ważnych cech użytkowych (Masojć, 2007). Jej wadą jest wysoka wrażliwość na zmiany warunków reakcji (Devos i Gale, 1992), jak również dominujący charakter dziedziczenia uzyskanych markerów - nie umożliwiają rozróżnienia osobników hetero- i homozygotycznych (Wolko i in.,1997). SCAR (Sequence Characterized Amplified Region) Sposobem odróżnienia homo- i heterozygot jest przekształcenie markerów RAPD sprzężonych z konkretną cechą na markery SCAR (Paran i Michelmore, 1993). Jest to zadanie pracochłonne i wymaga dużego nakładu kosztów, jednak umożliwia otrzymanie specyficznych dla danej cechy markerów. Ich uzyskanie polega na wycięciu produktu RAPD z żelu i jego zsekwencjonowaniu, a następnie zaprojektowaniu na podstawie otrzymanej sekwencji specyficznych starterów o długości nukleotydów. Startery te uczestniczą w amplifikacji jednego fragmentu o długości odpowiadającej wyjściowemu odcinkowi DNA (Masojć, 2007). Powielanie DNA przy użyciu tych markerów jest bardziej specyficzne i prowadzi do poprawy powtarzalności reakcji PCR (Nair i in. 1996). Technika ta była wykorzystywana m.in. do identyfikacji genów determinujących płeć papai (Deputy i in., 2002). SSR (Simple Sequence Repeat) Markery SSR zwane również markerami mikrosatelitarnymi, bazują na obecności w genomie sekwencji mikrosateliatrnych, w których motyw powtarzalny ma długość 1-4
3 nukleotydów. Każdy odcinek mikrosatelitarny sąsiaduje z unikatowymi sekwencjami, które wykorzystuje się do projektowania specyficznych starterów, wiążących się po obu stronach mikrosatelity (Masojć, 2007). Zaletą markerów SSR jest ujawnianie wysokiego polimorfizmu oraz kodominujący sposób dziedziczenia (Koreth i in., 1996). W związku z tym markery te znalazły szerokie zastosowanie w mapowaniu genomów, identyfikacji odmian, określaniu stopnia heterozygotyczności oraz jako markery cech o znaczeniu rolniczym (Powell i in., 1996). ISSR (Inter Simple Sequence Repeat) W metodzie ISSR amplifikacji ulega fragment DNA obecny pomiędzy dwoma identycznymi sekwencjami mikrosatelitarnmi, skierowanymi w przeciwnych kierunkach. W technice tej używany jest jeden starter o długości nukleotydów. Startery mogą być zakotwiczone na końcu 3 albo 5. Oznacza to obecność kilku dowolnych nukleotydów (Zietkiewicz i in., 1994), co gwarantuje ich przyłączanie do końców sekwencji mikrosatelitarnej na matrycowym DNA. Gdy używany jest starter niezakotwiczony ma on tendencję do poślizgów na matrycy DNA, co prowadzi do powstawania smug między prążkami na żelu (Pradeep - Reedy i in., 2002). ISSR jest prostą, szybką, wydajną techniką i charakteryzuje się wysoką powtarzalnością (Zietkiewicz i in., 1994). Markery ISSR mają charakter dominujący (Gupta i in., 1994), jednak w niektórych przypadkach mogą segregować w sposób kodominujący, a zatem umożliwiać rozróżnienie homozygot i heterozygot (Wu i in., 1994). Były one z powodzeniem wykorzystywane do oceny polimorfizmu (Bornet i Branchard, 2004), jak również do mapowania (Kojima i in., 1999). SNP (Single Nucleotide Polymorphism) Technika SNP polega na amplifikacji fragmentu genomu za pomocą reakcji PCR a następnie sekwencjonowaniu powstałego produktu. Po zsekwencjonowaniu fragmentów należących do różnych osobników porównuje się je ze sobą w celu identyfikacji różnic w sekwencji (miejsc SNP). Markery te pozwalają na wykrycie polimorfizmu pojedynczego nukleotydu w obrębie całej sekwencji analizowanego fragmentu DNA (Brookes, 1999). Wadą tej metody jest wysoki koszt analiz, natomiast ogromną zaletą możliwość obserwacji bardzo dużego polimorfizmu analizowanej sekwencji na poziomie pojedynczych nukleotydów (Alberts i in., 2002). Metoda SNP jest wykorzystywana m.in. do identyfikacji mutacji punktowych (Tyrka i in., 2004). AFLP (Amplified Fragmeny Leght Polymorphism) Techniki generujące tzw. markery mieszane wykorzystują właściwości zarówno enzymów restrykcyjnych, jak i reakcji PCR (Bednarek i Chwedorzewska, 2001). Do tej grupy należą markery AFLP (Vos i in., 1995).W metodzie tej wyizolowany i oczyszczony DNA trawi się dwoma enzymami restrykcyjnymi. Jeden z nich rozpoznaje sekwencje dłuższe i dlatego przecina DNA rzadziej, drugi rozpoznaje krótsze fragmenty - cięcia restrykcyjne wprowadzane są częściej (Morgante i Vogel, 1994). Otrzymane produkty liguje się z tzw.
4 adaptorami, czyli fragmentami dwuniciowego DNA o określonej sekwencji, które posiadają lepkie końce komplementarne do miejsc restrykcyjnych. Następnie przeprowadza się wstępną reakcję PCR (Paglia i Morgante, 1998), z użyciem starterów komplementarnych do sekwencji adaptorów i miejsc restrykcyjnych oraz zawierającymi jeden selektywny nukleotyd na końcu 3. W celu ograniczenia liczby generowanych produktów w kolejnym etapie amplifikacji selektywnej stosuje się startery o takiej samej sekwencji jak w poprzednim, ale posiadają one 2-4 nukleotydy selektywne na końcu 3 (Masojć, 2007). System ten był on wykorzystywany zarówno w mapowaniu (Singrun i in., 2004) jak określaniu stopnia zróżnicowania genetycznego genomów roślin(vos i in.,1995). SAMPL (Selectively Amplified Microsatelite Polimorphic Loci) SAMPL to system markerów molekularnych, który łączy elementy metody SSR i AFLP. Początkowe etapy przebiegają tak samo jak w technice AFLP. Otrzymane po wstępnej amplifikacji fragmenty DNA stanowią matrycę dla właściwej reakcji PCR. Używane są w niej dwa startery: jeden wiążący się z końcem fragmentu zawierającego sekwencję rozpoznawaną przez rzadziej tnący enzym, drugi komplementarny do sekwencji DNA mikrosatelitarnego. Dzięki zastosowaniu takiej kombinacji powielane są odcinki DNA pochodzące od fragmentów zawierających sekwencję pomiędzy dwoma enzymami, enzymem a mikrosatelitą oraz dwoma mikrosatelitami. Markery SAMPL mogą dziedziczyć się w sposób dominujący lub kodominujący (Tosti i Negri, 2002) i są wykorzystywane m.in. do identyfikacji polimorfizmu sekwencji mikrosatelitarnych (Morgante i Vogel, 1994). CAPS (Clevaed Amplified Polymorphic Sequence) Technika CAPS (Konieczny i Ausubei, 1993) jest oparta na reakcji PCR połączonej z trawieniem restrykcyjnym. Pierwszy etap to klasyczna reakcja PCR, do której startery konstruowane są na podstawie znanych sekwencji. Amplifikowany produkt jest następnie trawiony jednym lub kilkoma enzymami restrykcyjnymi i rozdzielany na żelu agarozowym. System CAPS jest alternatywnie określony jako PCR-RFLP i służy do identyfikacji zmienności w sekwencji DNA, gdy amplifikowane fragmenty DNA nie dają się rozróżnić pod względem długości. Pozwala na rozróżnienie alleli hetero- i homozygotycznych (Sztuba- Solińska, 2005). Wykorzystywane były często do identyfikacji genów warunkujących określone cechy (Chełkowski i in., 2003; Varshney i in., 2004) oraz do oceny zróżnicowania genetycznego (Barth i in., 2002). Markery molekularne są wykorzystywane w hodowli roślin głównie do: - określania stopnia podobieństwa materiałów wyjściowych - rejestracji nowych odmian wzór prążków służy do identyfikacji odmiany co ułatwia ochronę praw autorskich - ustalania genetycznej czystości nasion i jednorodności klonów - eliminowania z kolekcji (banków genów) powtarzających się genotypów zarejestrowanych pod różnymi nazwami.
5 - prowadzenia selekcji w oparciu o markery sprzężone z cechami ważnymi pod względem gospodarczym Dobre markery molekularne powinny być jednocześnie wysoce informatywne i wiarygodne, a koszty ich otrzymania powinny być możliwie jak najmniejsze. Powinny zatem cechować się silnym polimorfizmem, kodominującym charakterem dziedziczenia, wysoką frekwencją i równomiernym rozłożeniem w genomie, dużą powtarzalnością oraz prostą i szybką metodą wykrywania. Dodatkowo powinny wykazywać neutralność selekcyjną (czyli brak sprzężenia z niekorzystnymi genami) (Masojć, 2007). Markery molekularne stały się niezbędnym narzędziem w nowoczesnej hodowli roślin. Stosowane są w kolejnych etapach tworzenia nowych odmian roślin uprawnych, których prawidłowy przebieg umożliwia powodzenie prowadzonych prac hodowlanych (Sztuba Solińska, 2005). Piśmiennictwo: 1. Alberts, B., Johnson, A., Lewis, J., Raff, R., Roberts, K., and Walker, P. (2002). Molecular Biology of the Cell, 4th ed. Garland Publishing, New York. 2. Barth S., Melchinger A. R., Lubberstedt T., Genetic diversity in Arabidopsis thaliana L. Heynh. Investigated by cleaved amplification polymorphic sequence (CAPS) and inter-simple sequence repeat (ISSR) markers. Mol. Ecol. 11, Bautista N. S., Solis R., Kamijima O., Ishii T., RAPD, RFLP and SSLP analyses of phylogenetic relationships between cultivated and wild species of rice. Genes Genet. Syst. 76, Bednarek P.T., Chwedorzewska K Markery molekularne, ich charakterystyka genetyczna oraz wybrane zastosowania w analizie genetycznej roślin. Biotechnologia 1(52): Bornet B., Branchard M Use of ISSR fingerprints to detect microsatellites and genetic diversity in several related Brassica taxa and Arabidopsis thaliana. Hereditas 140: Bostein D., White R.L., Skolnick M., Davis R.W Constructions of genetic linkage map in man using restriction fragment length polymorphisms. Am. J. Hum. Genet. 32: Broda Z Diagnostyka molekularna w badaniach zmienności genetycznej roślin. Hodowla roślin i nasiennictwo 4: Brookes A. J., The essence of SNPs. Gene 234,
6 9. Chełkowski J., Golka L., Stępień Ł., Application of STS markers for leaf rust resistance genes in near-isogenic lines of spring wheat cv. Thatcher. J. Appl. Genet. 44, Deputy J. C., Ming R., Ma H., Liu Z., Fitch M. M.,Wang M., Manshardt R., Stiles J. I , Molecular markers for sex determination in papaya (Carica papaya L.). Theor. Appl. Genet. 106, Devos K.M., Gale M.D The use of random amplified polymorfic DNA markers in wheat. Theor. Appl. Genet. 84: Gupta M., Chyi Y.S., Romero - Severson J., Owen J.L Amplification of DNA markers from evolutionarily diverse genomes using single primers of simple - sequence repeats. Theor. Appl. Genet. 89: Jordan D. R., Casu R. E., Besse P., CarrollB. C., Berding N., Mcintyre C. L., Markers associated with stalk number and suckering in sugarcane, colocate with tillering and rhizomatousness QTLs in sorgium. Genome 47, Kojima T., Nagaoka T., Noda K., OgiharaY., 1998.Genetic linkage map of ISSR and RAPD markers in Einkorn wheat in relation to that of markers. Theor. Appl. Genet., 96, Konieczny, A., and Ausubei, F.M A procedure for mapping Arabidopsis mutations using co-dominant ecotype-specific PCR based markers. Plant J. 4: Koreth J., O Leary J. J., McGee J. O., Microsatellites and PCR genomic analysis. J. Path.178: Malyshev S. V., Korzun V. N., Zaben kova K. I., Voilokov, A. V., Berner A., Kartel N. A., Comparitive molecular-genetic mapping of genomes of ryse (Secale cereale L.) and other cereals. Tsitol. Genet. 37, Masojć P Ustalanie tożsamości genetycznej. Biotechnologia roślin, Red. 19. Morgante M., Vogel J., Compound microsatellite primers for the detection of genetic polymorphisms U.S. Patent Appl 08/ Nair S., Kumar A., Srivastava M. N., Mohan M., PCR- based DNA marjers linced to a gall midge resistance gene Gm4t has potential for marker-aided selection in rice. Theor. Appl. Genet. 92: Nybom, H. & Kraft, T Application of DNA fingerprinting to the taxonomy of European blackberry species. Electrophoresis 16:
7 22. Paglia G., Morgante M., (1998), Molecular Breeding, 4, Paran I, Michelmore RW Development of reliable PCR-based markers linked to downy resistance genes in lettuce. Theor Appl Genet 85: Powell W., Machray G., Provan J Polymorphism revealed by simple sequence repeats. Trends Pl. Science. 1: Pradeep Redy M., Sarla N., Siddiq E.A Inter simple sequence repeat (ISSR) polymorphism and its applications in plant breeding. Euphytica 128: 26. Schulman A.H Molecular markers to assess genetic diversity. Euphytica 158: Sinrun CH., Hsam S. L., Zeller F. J., Wenzel G., MohlerV., Localization of a novel recessive powdery mildew resistance gene from commo wheat line RD30 in the terminal region of chromosome 7AL. Theor. Appl. Genet. 109, Sztuba Solińska J Systemy markerów molekularnych i ich zastosowanie w hodowli roślin. Kosmos 54: Tosti N., Negri V., (2002), Genome, 45, Tyrka M., Błaszczyk L., ChełkowskiI J., Lind V., Kramer I., Weilepp M., Wiśniewska H., Ordon F., Development of the single nucleotide polymorphism marker of the wheat Lr1 leaf rust resistance gene. Cell. Mol. Biol. Lett. 9, Varshney A., Mohapatra T., Sharma R. P., Development and validation of CAPS and AFLP markers for white rust resistance gene in Brassica juncea. Theor. Appl. Genet. 109, Vos P., Hogers R., Bleeker M., Reijans M., van de Lee T., Hornes M., Frijters A., Plot J., Peleman J., Kupier M., Zebau M AFLP a new technique for DNA fingerprinting. Nucl. Acids Res.23: Williams J.G.K., Kubelik A.R., Livak K. J., Rafalski J. A, Tingey S.V DNA polymorphisms amplified by arbitrary primers are useful as genetic markcrs. Nucl. Acid. Res. 18: Wolko B., Irzykowska L., Święcicki W. K AFLP i SSR systemy markerowe przydatne w hodowli roślin. Postępy Nauk Rolniczych 2: Wolko B., Kruszka K Markery molekularne w badaniach zmienności genetycznej roślin. Postępy Nauk Rolniczych 3.
8 36. Wolko Ł., Witułka-Wall H., Siemieniako B.,Wolko B., Słomki R Poszukiwanie markerów cech użytkowych metodą RAPD-PCR. Przykłady analiz DNA. Red.R. Słomski. Poznań Zietkiewicz E., Rafalski A., Labuda D Genome fingerprinting by simple sequence repeat (SSR) - anchored polymerase chain reaction amplification. Genomics 20:
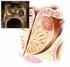
Transformacja pośrednia składa się z trzech etapów:
 Transformacja pośrednia składa się z trzech etapów: 1. Otrzymanie pożądanego odcinka DNA z materiału genetycznego dawcy 2. Wprowadzenie obcego DNA do wektora 3. Wprowadzenie wektora, niosącego w sobie
Transformacja pośrednia składa się z trzech etapów: 1. Otrzymanie pożądanego odcinka DNA z materiału genetycznego dawcy 2. Wprowadzenie obcego DNA do wektora 3. Wprowadzenie wektora, niosącego w sobie
Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych
 Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych Wstęp teoretyczny Technika RAPD (ang. Random Amplification of Polymorphic DNA) opiera się na prostej reakcji PCR, przeprowadzanej na genomowym
Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych Wstęp teoretyczny Technika RAPD (ang. Random Amplification of Polymorphic DNA) opiera się na prostej reakcji PCR, przeprowadzanej na genomowym
GENOMIKA. MAPOWANIE GENOMÓW MAPY GENOMICZNE
 GENOMIKA. MAPOWANIE GENOMÓW MAPY GENOMICZNE Bioinformatyka, wykład 3 (21.X.2008) krzysztof_pawlowski@sggw.waw.pl tydzień temu Gen??? Biologiczne bazy danych historia Biologiczne bazy danych najważniejsze
GENOMIKA. MAPOWANIE GENOMÓW MAPY GENOMICZNE Bioinformatyka, wykład 3 (21.X.2008) krzysztof_pawlowski@sggw.waw.pl tydzień temu Gen??? Biologiczne bazy danych historia Biologiczne bazy danych najważniejsze
Metody badania polimorfizmu/mutacji DNA. Aleksandra Sałagacka Pracownia Diagnostyki Molekularnej i Farmakogenomiki Uniwersytet Medyczny w Łodzi
 Metody badania polimorfizmu/mutacji DNA Aleksandra Sałagacka Pracownia Diagnostyki Molekularnej i Farmakogenomiki Uniwersytet Medyczny w Łodzi Mutacja Mutacja (łac. mutatio zmiana) - zmiana materialnego
Metody badania polimorfizmu/mutacji DNA Aleksandra Sałagacka Pracownia Diagnostyki Molekularnej i Farmakogenomiki Uniwersytet Medyczny w Łodzi Mutacja Mutacja (łac. mutatio zmiana) - zmiana materialnego
JOANNA SZTUBA-SOLIŃSKA
 Tom 54 2005 Numer 2 3 (267 268) Strony 227 239 JOANNA SZTUBA-SOLIŃSKA Instytut Hodowli i Aklimatyzacji Roślin Oddział Bydgoszcz Al. Powstańców Wielkopolskich 10, 85-090 Bydgoszcz e-mail: j.sztuba@ihar.bydgoszcz.pl
Tom 54 2005 Numer 2 3 (267 268) Strony 227 239 JOANNA SZTUBA-SOLIŃSKA Instytut Hodowli i Aklimatyzacji Roślin Oddział Bydgoszcz Al. Powstańców Wielkopolskich 10, 85-090 Bydgoszcz e-mail: j.sztuba@ihar.bydgoszcz.pl
Markery molekularne Autor tekstu: Michał Łuczak. Przegląd najbardziej popularnych technik
 Markery molekularne Autor tekstu: Michał Łuczak Przegląd najbardziej popularnych technik W ciągu ostatniego ćwierćwiecza nastąpił olbrzymi postęp w zrozumieniu wielu procesów zachodzących we wszystkich
Markery molekularne Autor tekstu: Michał Łuczak Przegląd najbardziej popularnych technik W ciągu ostatniego ćwierćwiecza nastąpił olbrzymi postęp w zrozumieniu wielu procesów zachodzących we wszystkich
Zastosowanie markerów RAPD do określenia podobieństwa genetycznego odmian jęczmienia ozimego (Hordeum vulgare L.)
 NR 226/227/1 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 ANETTA KUCZYŃSKA 1 JAN BOCIANOWSKI 1 PIOTR MASOJĆ 2 MARIA SURMA 1 TADEUSZ ADAMSKI 1 1 Instytut Genetyki Roślin Polskiej Akademii Nauk
NR 226/227/1 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 ANETTA KUCZYŃSKA 1 JAN BOCIANOWSKI 1 PIOTR MASOJĆ 2 MARIA SURMA 1 TADEUSZ ADAMSKI 1 1 Instytut Genetyki Roślin Polskiej Akademii Nauk
Mikrosatelitarne sekwencje DNA
 Mikrosatelitarne sekwencje DNA Małgorzata Pałucka Wykorzystanie sekwencji mikrosatelitarnych w jądrowym DNA drzew leśnych do udowodnienia pochodzenia materiału dowodowego w postępowaniu sądowym 27.09.2012
Mikrosatelitarne sekwencje DNA Małgorzata Pałucka Wykorzystanie sekwencji mikrosatelitarnych w jądrowym DNA drzew leśnych do udowodnienia pochodzenia materiału dowodowego w postępowaniu sądowym 27.09.2012
Glimmer umożliwia znalezienie regionów kodujących
 Narzędzia ułatwiające identyfikację właściwych genów GLIMMER TaxPlot Narzędzia ułatwiające amplifikację tych genów techniki PCR Primer3, Primer3plus PrimerBLAST Reverse Complement Narzędzia ułatwiające
Narzędzia ułatwiające identyfikację właściwych genów GLIMMER TaxPlot Narzędzia ułatwiające amplifikację tych genów techniki PCR Primer3, Primer3plus PrimerBLAST Reverse Complement Narzędzia ułatwiające
Genetyka, materiały dla studentów Pielęgniarstwa
 Markery genetyczne: definicja Marker genetyczny jest to cecha, która może być wykorzystana do identyfikacji osobników lub gatunków. Cechy markerów genetycznych Monogeniczny: warunkowany przez jeden gen
Markery genetyczne: definicja Marker genetyczny jest to cecha, która może być wykorzystana do identyfikacji osobników lub gatunków. Cechy markerów genetycznych Monogeniczny: warunkowany przez jeden gen
Ćwiczenie 12. Diagnostyka molekularna. Poszukiwanie SNPs Odczytywanie danych z sekwencjonowania. Prof. dr hab. Roman Zieliński
 Ćwiczenie 12 Diagnostyka molekularna. Poszukiwanie SNPs Odczytywanie danych z sekwencjonowania Prof. dr hab. Roman Zieliński 1. Diagnostyka molekularna 1.1. Pytania i zagadnienia 1.1.1. Jak definiujemy
Ćwiczenie 12 Diagnostyka molekularna. Poszukiwanie SNPs Odczytywanie danych z sekwencjonowania Prof. dr hab. Roman Zieliński 1. Diagnostyka molekularna 1.1. Pytania i zagadnienia 1.1.1. Jak definiujemy
Monitoring genetyczny populacji wilka (Canis lupus) jako nowy element monitoringu stanu populacji dużych drapieżników
 Monitoring genetyczny populacji wilka (Canis lupus) jako nowy element monitoringu stanu populacji dużych drapieżników Wojciech Śmietana Co to jest monitoring genetyczny? Monitoring genetyczny to regularnie
Monitoring genetyczny populacji wilka (Canis lupus) jako nowy element monitoringu stanu populacji dużych drapieżników Wojciech Śmietana Co to jest monitoring genetyczny? Monitoring genetyczny to regularnie
Zastosowanie nowych technologii genotypowania w nowoczesnej hodowli i bankach genów
 Zastosowanie nowych technologii genotypowania w nowoczesnej hodowli i bankach genów Jerzy H. Czembor, Bogusław Łapiński, Aleksandra Pietrusińska, Urszula Piechota Krajowe Centrum Roślinnych Zasobów Genowych
Zastosowanie nowych technologii genotypowania w nowoczesnej hodowli i bankach genów Jerzy H. Czembor, Bogusław Łapiński, Aleksandra Pietrusińska, Urszula Piechota Krajowe Centrum Roślinnych Zasobów Genowych
Polimorfizm markerów STS i SSR w obrębie linii wsobnych żyta*
 NR 244 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2007 STEFAN STOJAŁOWSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Polimorfizm markerów STS i SSR w obrębie linii wsobnych
NR 244 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2007 STEFAN STOJAŁOWSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Polimorfizm markerów STS i SSR w obrębie linii wsobnych
Identyfikacja QTL warunkujących długość liścia flagowego w dwóch populacjach mapujących żyta (Secale cereale L.)
 NR 250 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2008 PAWEŁ MILCZARSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Identyfikacja QTL warunkujących długość liścia flagowego
NR 250 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2008 PAWEŁ MILCZARSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Identyfikacja QTL warunkujących długość liścia flagowego
mikrosatelitarne, minisatelitarne i polimorfizm liczby kopii
 Zawartość 139371 1. Wstęp zarys historii genetyki, czyli od genetyki klasycznej do genomiki 2. Chromosomy i podziały jądra komórkowego 2.1. Budowa chromosomu 2.2. Barwienie prążkowe chromosomów 2.3. Mitoza
Zawartość 139371 1. Wstęp zarys historii genetyki, czyli od genetyki klasycznej do genomiki 2. Chromosomy i podziały jądra komórkowego 2.1. Budowa chromosomu 2.2. Barwienie prążkowe chromosomów 2.3. Mitoza
Charakterystyka markerów SAMPL i ich wykorzystanie w badaniach genomów roœlinnych
 PRACE PRZEGL DOWE Charakterystyka markerów SAMPL i ich wykorzystanie w badaniach genomów roœlinnych Aneta Hromada, Monika Rakoczy-Trojanowska Katedra Genetyki, Hodowli i Biotechnologii Roœlin, Szko³a G³ówna
PRACE PRZEGL DOWE Charakterystyka markerów SAMPL i ich wykorzystanie w badaniach genomów roœlinnych Aneta Hromada, Monika Rakoczy-Trojanowska Katedra Genetyki, Hodowli i Biotechnologii Roœlin, Szko³a G³ówna
Klonowanie molekularne Kurs doskonalący. Zakład Geriatrii i Gerontologii CMKP
 Klonowanie molekularne Kurs doskonalący Zakład Geriatrii i Gerontologii CMKP Etapy klonowania molekularnego 1. Wybór wektora i organizmu gospodarza Po co klonuję (do namnożenia DNA [czy ma być metylowane
Klonowanie molekularne Kurs doskonalący Zakład Geriatrii i Gerontologii CMKP Etapy klonowania molekularnego 1. Wybór wektora i organizmu gospodarza Po co klonuję (do namnożenia DNA [czy ma być metylowane
Markery molekularne w badaniach rzepaku (Brassica napus L.) I. Przegląd stosowanych technik
 ROŚLINY OLEISTE OILSEED CROPS 34 (2): 129-150 2013 Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin Państwowy Instytut Badawczy, Oddział w Poznaniu Autor korespondencyjny M. Matuszczak, e-mail:
ROŚLINY OLEISTE OILSEED CROPS 34 (2): 129-150 2013 Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin Państwowy Instytut Badawczy, Oddział w Poznaniu Autor korespondencyjny M. Matuszczak, e-mail:
MARKERY MIKROSATELITARNE
 MARKERY MIKROSATELITARNE Badania laboratoryjne prowadzone w Katedrze Genetyki i Ogólnej Hodowli Zwierząt SGGW w ramach monitoringu genetycznego wykorzystują analizę genetyczną markerów mikrosatelitarnych.
MARKERY MIKROSATELITARNE Badania laboratoryjne prowadzone w Katedrze Genetyki i Ogólnej Hodowli Zwierząt SGGW w ramach monitoringu genetycznego wykorzystują analizę genetyczną markerów mikrosatelitarnych.
Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu
 Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Autor: dr Mirosława Staniaszek
 Zakład Hodowli Roślin Ogrodniczych Pracownia Genetyki i Hodowli Roślin Warzywnych Fot. J. Sobolewski Procedura identyfikacji genu Frl warunkującego odporność pomidora na Fusarium oxysporum f.sp. radicis-lycopersici
Zakład Hodowli Roślin Ogrodniczych Pracownia Genetyki i Hodowli Roślin Warzywnych Fot. J. Sobolewski Procedura identyfikacji genu Frl warunkującego odporność pomidora na Fusarium oxysporum f.sp. radicis-lycopersici
Analiza podobieństwa genetycznego odmian orkiszu (Triticum aestivum ssp. spelta L.) za pomocą markerów RAPD
 NR 252 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2009 SYLWIA OKOŃ 1 EDYTA PACZOS-GRZĘDA 1 PIOTR KRASKA 2 EWA KWIECIŃSKA-POPPE 2 EDWARD PAŁYS 2 1 Instytut Genetyki, Hodowli I Biotechnologii Roślin,
NR 252 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2009 SYLWIA OKOŃ 1 EDYTA PACZOS-GRZĘDA 1 PIOTR KRASKA 2 EWA KWIECIŃSKA-POPPE 2 EDWARD PAŁYS 2 1 Instytut Genetyki, Hodowli I Biotechnologii Roślin,
Jaki koń jest nie każdy widzi - genomika populacji polskich ras koni
 Jaki koń jest nie każdy widzi - genomika populacji polskich ras koni Gurgul A., Jasielczuk I., Semik-Gurgul E., Pawlina-Tyszko K., Szmatoła T., Bugno-Poniewierska M. Instytut Zootechniki PIB Zakład Biologii
Jaki koń jest nie każdy widzi - genomika populacji polskich ras koni Gurgul A., Jasielczuk I., Semik-Gurgul E., Pawlina-Tyszko K., Szmatoła T., Bugno-Poniewierska M. Instytut Zootechniki PIB Zakład Biologii
Ocena zróżnicowania genetycznego materiałów kolekcyjnych pszenżyta ozimego. stabilny pod względem cech plonotwórczych,
 13 Polish Journal of Agronomy 2014, 16, 13 18 Ocena zróżnicowania genetycznego materiałów kolekcyjnych pszenżyta ozimego stabilnych pod względem cech plonotwórczych Aneta Kramek, Sylwia Okoń Instytut Genetyki,
13 Polish Journal of Agronomy 2014, 16, 13 18 Ocena zróżnicowania genetycznego materiałów kolekcyjnych pszenżyta ozimego stabilnych pod względem cech plonotwórczych Aneta Kramek, Sylwia Okoń Instytut Genetyki,
POSZUKIWANIE POLIMORFICZNYCH MARKERÓW ZDEFINIOWANYCH SEKWENCYJNIE W POPULACJI GROCHU CARNEVAL X MP1401
 Fragm. Agron. 29(4) 2012, 87 94 POSZUKIWANIE POLIMORFICZNYCH MARKERÓW ZDEFINIOWANYCH SEKWENCYJNIE W POPULACJI GROCHU CARNEVAL X Michał Knopkiewicz, Magdalena Gawłowska, Wojciech Święcicki Instytut Genetyki
Fragm. Agron. 29(4) 2012, 87 94 POSZUKIWANIE POLIMORFICZNYCH MARKERÓW ZDEFINIOWANYCH SEKWENCYJNIE W POPULACJI GROCHU CARNEVAL X Michał Knopkiewicz, Magdalena Gawłowska, Wojciech Święcicki Instytut Genetyki
Wprowadzenie do genetyki sądowej. Materiały biologiczne. Materiały biologiczne: prawidłowe zabezpieczanie śladów
 Wprowadzenie do genetyki sądowej 2013 Pracownia Genetyki Sądowej Katedra i Zakład Medycyny Sądowej Materiały biologiczne Inne: włosy z cebulkami, paznokcie możliwa degradacja - tkanki utrwalone w formalinie/parafinie,
Wprowadzenie do genetyki sądowej 2013 Pracownia Genetyki Sądowej Katedra i Zakład Medycyny Sądowej Materiały biologiczne Inne: włosy z cebulkami, paznokcie możliwa degradacja - tkanki utrwalone w formalinie/parafinie,
Sekwencjonowanie nowej generacji i rozwój programów selekcyjnych w akwakulturze ryb łososiowatych
 Sekwencjonowanie nowej generacji i rozwój programów selekcyjnych w akwakulturze ryb łososiowatych Konrad Ocalewicz Zakład Biologii i Ekologii Morza, Instytut Oceanografii, Wydział Oceanografii i Geografii,
Sekwencjonowanie nowej generacji i rozwój programów selekcyjnych w akwakulturze ryb łososiowatych Konrad Ocalewicz Zakład Biologii i Ekologii Morza, Instytut Oceanografii, Wydział Oceanografii i Geografii,
Zastosowanie techniki AFLP w połączeniu z BSA do identyfikacji markerów sprzężonych z cechą karłowatości u żyta
 NR 226/227/1 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 HELENA KUBICKA RENATA LEWANDOWSKA Ogród Botaniczny Centrum Zachowania Różnorodności Biologicznej PAN, Warszawa Zastosowanie techniki
NR 226/227/1 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 HELENA KUBICKA RENATA LEWANDOWSKA Ogród Botaniczny Centrum Zachowania Różnorodności Biologicznej PAN, Warszawa Zastosowanie techniki
Farmakogenetyka Biotechnologia Medyczna I o
 ĆWICZENIE 2 Oznaczanie polimorfizmu cytochromu CYP2D6 za pomocą tradycyjnych metod biologii molekularnej: PCR-RFLP I. Łańcuchowa reakcja polimerazy PCR (polymerase chain reaction) Technika PCR rozwinęła
ĆWICZENIE 2 Oznaczanie polimorfizmu cytochromu CYP2D6 za pomocą tradycyjnych metod biologii molekularnej: PCR-RFLP I. Łańcuchowa reakcja polimerazy PCR (polymerase chain reaction) Technika PCR rozwinęła
Markery DNA oparte na retrotranspozonach
 Wiadomości Botaniczne 50(3/4): 15 24, 2006 Markery DNA oparte na retrotranspozonach Wojciech BIENIEK BIENIEK W. 2006. Retrotransposon-based DNA markers. Wiadomości Botaniczne 50(3/4): 15 24. Retrotransposons
Wiadomości Botaniczne 50(3/4): 15 24, 2006 Markery DNA oparte na retrotranspozonach Wojciech BIENIEK BIENIEK W. 2006. Retrotransposon-based DNA markers. Wiadomości Botaniczne 50(3/4): 15 24. Retrotransposons
Markery klasy II -Polimorfizm fragmentów DNA (na ogół niekodujących): - RFLP - VNTR - RAPD
 Marker genetyczny- polimorficzna cecha jakościowa organizmu, którą charakteryzuje proste dziedziczenie (mendlowskie) oraz którą można dokładnie identyfikować metodami analitycznymi. Markery klasy I - Antygeny
Marker genetyczny- polimorficzna cecha jakościowa organizmu, którą charakteryzuje proste dziedziczenie (mendlowskie) oraz którą można dokładnie identyfikować metodami analitycznymi. Markery klasy I - Antygeny
Tematyka zajęć z biologii
 Tematyka zajęć z biologii klasy: I Lp. Temat zajęć Zakres treści 1 Zapoznanie z przedmiotowym systemem oceniania, wymaganiami edukacyjnymi i podstawą programową Podstawowe zagadnienia materiału nauczania
Tematyka zajęć z biologii klasy: I Lp. Temat zajęć Zakres treści 1 Zapoznanie z przedmiotowym systemem oceniania, wymaganiami edukacyjnymi i podstawą programową Podstawowe zagadnienia materiału nauczania
ANNALES UMCS VOL. LXX (4) SECTIO E AGRICULTURA 2015
 ANNALES UMCS VOL. LXX (4) SECTIO E AGRICULTURA 2015 1 Katedra Technologii Mięsa i Zarządzania Jakością, Uniwersytet Przyrodniczy w Lublinie, Skromna 8, 20-704 Lublin, e-mail: keska.paulina@wp.pl 2 Instytut
ANNALES UMCS VOL. LXX (4) SECTIO E AGRICULTURA 2015 1 Katedra Technologii Mięsa i Zarządzania Jakością, Uniwersytet Przyrodniczy w Lublinie, Skromna 8, 20-704 Lublin, e-mail: keska.paulina@wp.pl 2 Instytut
Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1
 Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1 1 Zakład Genetyki i Hodowli Roślin Korzeniowych, Pracownia Biotechnologii, Instytut Hodowli i Aklimatyzacji
Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1 1 Zakład Genetyki i Hodowli Roślin Korzeniowych, Pracownia Biotechnologii, Instytut Hodowli i Aklimatyzacji
Biologia Molekularna z Biotechnologią ===============================================================================================
 Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Przedmiot: Katedra Biologii Molekularnej Biologia
Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Przedmiot: Katedra Biologii Molekularnej Biologia
Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV
 Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV Cel ćwiczenia Określenie podatności na zakażenie wirusem HIV poprzez detekcję homo lub heterozygotyczności
Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV Cel ćwiczenia Określenie podatności na zakażenie wirusem HIV poprzez detekcję homo lub heterozygotyczności
PL B1. UNIWERSYTET PRZYRODNICZY W LUBLINIE, Lublin, PL BUP 26/11
 PL 214501 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 214501 (13) B1 (21) Numer zgłoszenia: 391458 (51) Int.Cl. C12Q 1/68 (2006.01) C12N 15/29 (2006.01) Urząd Patentowy Rzeczypospolitej Polskiej
PL 214501 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 214501 (13) B1 (21) Numer zgłoszenia: 391458 (51) Int.Cl. C12Q 1/68 (2006.01) C12N 15/29 (2006.01) Urząd Patentowy Rzeczypospolitej Polskiej
Zastosowanie metod RAPD i ISSR do oceny podobieństwa genetycznego greckich form Dasypyrum villosum (L.) P. Candargy
 NR 253 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2009 AGNIESZKA GRĄDZIELEWSKA EDYTA PACZOS-GRZĘDA DANIELA GRUSZECKA Instytut Genetyki, Hodowli i Biotechnologii Roślin Uniwersytet Przyrodniczy w
NR 253 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2009 AGNIESZKA GRĄDZIELEWSKA EDYTA PACZOS-GRZĘDA DANIELA GRUSZECKA Instytut Genetyki, Hodowli i Biotechnologii Roślin Uniwersytet Przyrodniczy w
Mitochondrialna Ewa;
 Mitochondrialna Ewa; jej sprzymierzeńcy i wrogowie Lien Dybczyńska Zakład genetyki, Uniwersytet Warszawski 01.05.2004 Milion lat temu Ale co dalej??? I wtedy wkracza biologia molekularna Analiza różnic
Mitochondrialna Ewa; jej sprzymierzeńcy i wrogowie Lien Dybczyńska Zakład genetyki, Uniwersytet Warszawski 01.05.2004 Milion lat temu Ale co dalej??? I wtedy wkracza biologia molekularna Analiza różnic
PL B1. UNIWERSYTET PRZYRODNICZY W LUBLINIE, Lublin, PL BUP 04/14. SYLWIA OKOŃ, Dąbrowica, PL KRZYSZTOF KOWALCZYK, Motycz, PL
 PL 220315 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 220315 (13) B1 Urząd Patentowy Rzeczypospolitej Polskiej (21) Numer zgłoszenia: 400252 (22) Data zgłoszenia: 06.08.2012 (51) Int.Cl.
PL 220315 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 220315 (13) B1 Urząd Patentowy Rzeczypospolitej Polskiej (21) Numer zgłoszenia: 400252 (22) Data zgłoszenia: 06.08.2012 (51) Int.Cl.
Mapowanie fizyczne genomów -konstrukcja map wyskalowanych w jednostkach fizycznych -najdokładniejszą mapą fizyczną genomu, o największej
 Mapowanie fizyczne genomów -konstrukcja map wyskalowanych w jednostkach fizycznych -najdokładniejszą mapą fizyczną genomu, o największej rozdzielczości jest sekwencja nukleotydowa -mapowanie fizyczne genomu
Mapowanie fizyczne genomów -konstrukcja map wyskalowanych w jednostkach fizycznych -najdokładniejszą mapą fizyczną genomu, o największej rozdzielczości jest sekwencja nukleotydowa -mapowanie fizyczne genomu
Ocena dystansu genetycznego pomiędzy liniami GMS Janpol za pomocą markerów molekularnych PCR-RAPD
 Tom XXI Rośliny Oleiste 2000 Anna Fürguth, Iwona Bartkowiak-Broda, Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Ocena dystansu genetycznego pomiędzy liniami
Tom XXI Rośliny Oleiste 2000 Anna Fürguth, Iwona Bartkowiak-Broda, Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Ocena dystansu genetycznego pomiędzy liniami
Zadanie 2.4. Cel badań:
 Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Cel badań: Celem
Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Cel badań: Celem
WYKORZYSTANIE MARKERÓW MOLEKULARNYCH W HODOWLI ODPORNOŚCIOWEJ POMIDORA NA CHOROBY POWODOWANE PRZEZ FUSARIUM OXYSPORUM
 WYKORZYSTANIE ARKERÓW OLEKULARNYCH W HODOWLI ODPORNOŚCIOWEJ POIDORA NA CHOROBY POWODOWANE PRZEZ FUSARIU OXYSPORU F.SP. LYCOPERSICI I PSEUDOONAS SYRINGAE PV. TOATO USE OF OLECULAR ARKERS IN THE BREEDING
WYKORZYSTANIE ARKERÓW OLEKULARNYCH W HODOWLI ODPORNOŚCIOWEJ POIDORA NA CHOROBY POWODOWANE PRZEZ FUSARIU OXYSPORU F.SP. LYCOPERSICI I PSEUDOONAS SYRINGAE PV. TOATO USE OF OLECULAR ARKERS IN THE BREEDING
PCR. Aleksandra Sałagacka
 PCR Aleksandra Sałagacka Reakcja PCR naśladuje proces replikacji DNA in vitro pozwala na amplifikację określonego krótkiego (kilkadziesiąt kilka tys.pz) fragmentu DNA obecnie najważniejsze narzędzie biologii
PCR Aleksandra Sałagacka Reakcja PCR naśladuje proces replikacji DNA in vitro pozwala na amplifikację określonego krótkiego (kilkadziesiąt kilka tys.pz) fragmentu DNA obecnie najważniejsze narzędzie biologii
Zadanie 2.4. Dr inż. Anna Litwiniec Dr inż. Barbara Skibowska Dr inż. Sandra Cichorz
 Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Dr inż. Anna Litwiniec
Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Dr inż. Anna Litwiniec
Mapowanie i markery molekularne
 Szkoła Główna Gospodarstwa Wiejskiego w Warszawie Mapowanie i markery molekularne mgr inż. Waldemar Skowron waldemar_skowron@sggw.pl MAPOWANIE polega na opracowaniu szczegółowych map chromosomów, które
Szkoła Główna Gospodarstwa Wiejskiego w Warszawie Mapowanie i markery molekularne mgr inż. Waldemar Skowron waldemar_skowron@sggw.pl MAPOWANIE polega na opracowaniu szczegółowych map chromosomów, które
BUDOWA I FUNKCJA GENOMU LUDZKIEGO
 BUDOWA I FUNKCJA GENOMU LUDZKIEGO Magdalena Mayer Katedra i Zakład Genetyki Medycznej UM w Poznaniu 1. Projekt poznania genomu człowieka: Cele programu: - skonstruowanie szczegółowych map fizycznych i
BUDOWA I FUNKCJA GENOMU LUDZKIEGO Magdalena Mayer Katedra i Zakład Genetyki Medycznej UM w Poznaniu 1. Projekt poznania genomu człowieka: Cele programu: - skonstruowanie szczegółowych map fizycznych i
Wprowadzenie do genetyki medycznej i sądowej
 Genetyka medyczno-sądowa Wprowadzenie do genetyki medycznej i sądowej Kierownik Pracowni Genetyki Medycznej i Sądowej Ustalanie tożsamości zwłok Identyfikacja sprawców przestępstw Identyfikacja śladów
Genetyka medyczno-sądowa Wprowadzenie do genetyki medycznej i sądowej Kierownik Pracowni Genetyki Medycznej i Sądowej Ustalanie tożsamości zwłok Identyfikacja sprawców przestępstw Identyfikacja śladów
Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu
 Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan
 Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan Klasyczna metoda PCR jest metodą jakościową, nie ilościową co np.
Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan Klasyczna metoda PCR jest metodą jakościową, nie ilościową co np.
WYSTĘPOWANIE WYBRANYCH GENÓW ODPORNOŚCI NA PARCH JABŁONI U ODMIAN I GATUNKÓW DZIKICH UŻYWANYCH W PROGRAMACH HODOWLANYCH JABŁONI.
 Roczniki Akademii Rolniczej w Poznaniu CCCLXXXIII (2007) MAŁGORZATA KORBIN, SYLWIA KELLER-PRZYBYŁKOWICZ, EDWARD ŻURAWICZ WYSTĘPOWANIE WYBRANYCH GENÓW ODPORNOŚCI NA PARCH JABŁONI U ODMIAN I GATUNKÓW DZIKICH
Roczniki Akademii Rolniczej w Poznaniu CCCLXXXIII (2007) MAŁGORZATA KORBIN, SYLWIA KELLER-PRZYBYŁKOWICZ, EDWARD ŻURAWICZ WYSTĘPOWANIE WYBRANYCH GENÓW ODPORNOŚCI NA PARCH JABŁONI U ODMIAN I GATUNKÓW DZIKICH
Zastosowanie markerów DNA do badań odmian składników mieszańcowych rzepaku
 Tom XIX Rośliny Oleiste 1998 Katarzyna Mikołajczyk, Marcin Matuszczak, Teresa Piętka Iwona Bartkowiak-Broda, Jan Krzymański Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Zastosowanie
Tom XIX Rośliny Oleiste 1998 Katarzyna Mikołajczyk, Marcin Matuszczak, Teresa Piętka Iwona Bartkowiak-Broda, Jan Krzymański Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Zastosowanie
Metody: PCR, MLPA, Sekwencjonowanie, PCR-RLFP, PCR-Multiplex, PCR-ASO
 Diagnostyka molekularna Dr n.biol. Anna Wawrocka Strategia diagnostyki genetycznej: Aberracje chromosomowe: Metody:Analiza kariotypu, FISH, acgh, MLPA, QF-PCR Gen(y) znany Metody: PCR, MLPA, Sekwencjonowanie,
Diagnostyka molekularna Dr n.biol. Anna Wawrocka Strategia diagnostyki genetycznej: Aberracje chromosomowe: Metody:Analiza kariotypu, FISH, acgh, MLPA, QF-PCR Gen(y) znany Metody: PCR, MLPA, Sekwencjonowanie,
Zastosowanie metody AFLP do analizy DNA rzepaku ozimego
 Tom XXIII Rośliny Oleiste 2002 Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Zastosowanie metody AFLP do analizy DNA rzepaku ozimego The use of AFLP method
Tom XXIII Rośliny Oleiste 2002 Marcin Matuszczak Instytut Hodowli i Aklimatyzacji Roślin, Zakład Roślin Oleistych w Poznaniu Zastosowanie metody AFLP do analizy DNA rzepaku ozimego The use of AFLP method
Anna Hawliczek-Strulak, Katarzyna Tofil, Ewa Borzęcka, Piotr Gawroński, Bernd Hackauf, Hanna Bolibok-Brągoszewska
 Zmienność zasobów ze światowych kolekcji żyta na tle współczesnych polskich i niemieckich odmian i materiałów hodowlanych na podstawie genotypowania DArTSeq Anna Hawliczek-Strulak, Katarzyna Tofil, Ewa
Zmienność zasobów ze światowych kolekcji żyta na tle współczesnych polskich i niemieckich odmian i materiałów hodowlanych na podstawie genotypowania DArTSeq Anna Hawliczek-Strulak, Katarzyna Tofil, Ewa
Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY)
 Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY) Cel ćwiczenia Amplifikacja fragmentu genu amelogeniny, znajdującego się na chromosomach X i Y, jako celu molekularnego przydatnego
Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY) Cel ćwiczenia Amplifikacja fragmentu genu amelogeniny, znajdującego się na chromosomach X i Y, jako celu molekularnego przydatnego
Dr hab.n.med. Renata Jacewicz
 GENOM CZŁOWIEKA >99 % 0,05%(100MtDNA) 65% Dr hab.n.med. Renata Jacewicz Kierownik Pracowni Genetyki Medycznej i Sądowej 3% 32% 2013 Pracownia Genetyki Medycznej i Sądowej ZMS Dojrzałe erytrocyty, trzony
GENOM CZŁOWIEKA >99 % 0,05%(100MtDNA) 65% Dr hab.n.med. Renata Jacewicz Kierownik Pracowni Genetyki Medycznej i Sądowej 3% 32% 2013 Pracownia Genetyki Medycznej i Sądowej ZMS Dojrzałe erytrocyty, trzony
PODSTAWY BIOINFORMATYKI 11 BAZA DANYCH HAPMAP
 PODSTAWY BIOINFORMATYKI 11 BAZA DANYCH HAPMAP WSTĘP 1. SNP 2. haplotyp 3. równowaga sprzężeń 4. zawartość bazy HapMap 5. przykłady zastosowań Copyright 2013, Joanna Szyda HAPMAP BAZA DANYCH HAPMAP - haplotypy
PODSTAWY BIOINFORMATYKI 11 BAZA DANYCH HAPMAP WSTĘP 1. SNP 2. haplotyp 3. równowaga sprzężeń 4. zawartość bazy HapMap 5. przykłady zastosowań Copyright 2013, Joanna Szyda HAPMAP BAZA DANYCH HAPMAP - haplotypy
1. Analiza asocjacyjna. Cechy ciągłe. Cechy binarne. Analiza sprzężeń. Runs of homozygosity. Signatures of selection
 BIOINFORMATYKA 1. Wykład wstępny 2. Bazy danych: projektowanie i struktura 3. Równowaga Hardyego-Weinberga, wsp. rekombinacji 4. Analiza asocjacyjna 5. Analiza asocjacyjna 6. Sekwencjonowanie nowej generacji
BIOINFORMATYKA 1. Wykład wstępny 2. Bazy danych: projektowanie i struktura 3. Równowaga Hardyego-Weinberga, wsp. rekombinacji 4. Analiza asocjacyjna 5. Analiza asocjacyjna 6. Sekwencjonowanie nowej generacji
Metody analizy genomu
 Metody analizy genomu 1. Mapowanie restrykcyjne. 2. Sondy do rozpoznawania DNA 3. FISH 4. Odczytanie sekwencji DNA 5. Interpretacja sekwencji DNA genomu 6. Transkryptom 7. Proteom 1. Mapy restrykcyjne
Metody analizy genomu 1. Mapowanie restrykcyjne. 2. Sondy do rozpoznawania DNA 3. FISH 4. Odczytanie sekwencji DNA 5. Interpretacja sekwencji DNA genomu 6. Transkryptom 7. Proteom 1. Mapy restrykcyjne
Hybrydyzacja kwasów nukleinowych
 Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Techniki molekularne w mikrobiologii SYLABUS A. Informacje ogólne
 Techniki molekularne w mikrobiologii A. Informacje ogólne Elementy sylabusu Nazwa jednostki prowadzącej kierunek Nazwa kierunku studiów Poziom kształcenia Profil studiów Forma studiów Rodzaj Rok studiów
Techniki molekularne w mikrobiologii A. Informacje ogólne Elementy sylabusu Nazwa jednostki prowadzącej kierunek Nazwa kierunku studiów Poziom kształcenia Profil studiów Forma studiów Rodzaj Rok studiów
Ćwiczenia 1 Wirtualne Klonowanie Prowadzący: mgr inż. Joanna Tymeck-Mulik i mgr Lidia Gaffke. Część teoretyczna:
 Uniwersytet Gdański, Wydział Biologii Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią Biologia II rok ===============================================================================================
Uniwersytet Gdański, Wydział Biologii Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią Biologia II rok ===============================================================================================
Dr hab.n.med. Renata Jacewicz
 GENOM CZŁOWIEKA >99,999% 0,0005% 65% Dr hab.n.med. Renata Jacewicz Kierownik Pracowni Genetyki Medycznej i Sądowej 3% 32% 2013 Pracownia Genetyki Medycznej i Sądowej ZMS Dojrzałe erytrocyty, trzony włosów
GENOM CZŁOWIEKA >99,999% 0,0005% 65% Dr hab.n.med. Renata Jacewicz Kierownik Pracowni Genetyki Medycznej i Sądowej 3% 32% 2013 Pracownia Genetyki Medycznej i Sądowej ZMS Dojrzałe erytrocyty, trzony włosów
Analiza podobieństwa genetycznego wybranych gatunków w rodzaju Secale
 NR 247 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2008 ZBIGNIEW BRODA DANUTA KURASIAK-POPOWSKA ALEKSANDRA KOWALSKA ANNA ĆWIKLIŃSKA Katedra Genetyki i Hodowli Roślin Akademii Rolniczej w Poznaniu
NR 247 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2008 ZBIGNIEW BRODA DANUTA KURASIAK-POPOWSKA ALEKSANDRA KOWALSKA ANNA ĆWIKLIŃSKA Katedra Genetyki i Hodowli Roślin Akademii Rolniczej w Poznaniu
TECHNIKI WYKORZYSTYWANE W DIAGNOSTYCE MOLEKULARNEJ CHORÓB JEDNOGENOWYCH TECHNIQUES USED IN MOLECULAR DIAGNOSTICS OF MONOGENIC DISORDERS
 Nowiny Lekarskie 2006, 75, 5, 486 490 ALINA LICZBAŃSKA, ANNA WOŹNIAK, ANNA WAWROCKA, MACIEJ R. KRAWCZYŃSKI TECHNIKI WYKORZYSTYWANE W DIAGNOSTYCE MOLEKULARNEJ CHORÓB JEDNOGENOWYCH TECHNIQUES USED IN MOLECULAR
Nowiny Lekarskie 2006, 75, 5, 486 490 ALINA LICZBAŃSKA, ANNA WOŹNIAK, ANNA WAWROCKA, MACIEJ R. KRAWCZYŃSKI TECHNIKI WYKORZYSTYWANE W DIAGNOSTYCE MOLEKULARNEJ CHORÓB JEDNOGENOWYCH TECHNIQUES USED IN MOLECULAR
Spis treści Część I. Genetyczne podstawy hodowli roślin 1. Molekularne podstawy dziedziczenia cech Dariusz Crzebelus, Adeta Adamus, Maria Klein
 Spis treści Część I. Genetyczne podstawy hodowli roślin 1. Molekularne podstawy dziedziczenia cech... 15 Dariusz Crzebelus, Adeta Adamus, Maria Klein 1.1. Budowa DNA i przepływ informacji genetycznej...
Spis treści Część I. Genetyczne podstawy hodowli roślin 1. Molekularne podstawy dziedziczenia cech... 15 Dariusz Crzebelus, Adeta Adamus, Maria Klein 1.1. Budowa DNA i przepływ informacji genetycznej...
Markery molekularne sprzężone z locus genu przywracającego płodność u mieszańców żyta z cytoplazmą CMS-C *
 NR 235 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2005 STEFAN STOJAŁOWSKI PAWEŁ MILCZARSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Markery molekularne sprzężone z locus
NR 235 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2005 STEFAN STOJAŁOWSKI PAWEŁ MILCZARSKI Katedra Genetyki i Hodowli Roślin Akademia Rolnicza w Szczecinie Markery molekularne sprzężone z locus
Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16
 Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16 Ćwiczenie 3 Identyfikacja genetycznie modyfikowanych roślin w produktach spożywczych - jakościowe badanie obecności
Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16 Ćwiczenie 3 Identyfikacja genetycznie modyfikowanych roślin w produktach spożywczych - jakościowe badanie obecności
OCENA RÓŻNORODNOŚCI GENETYCZNEJ PRZY POMOCY MARKERÓW MOLEKULARNYCH ZASTOSOWANIE W EKOTOKSYKOLOGII
 PISMO POLSKIEGO TOWARZYSTWA PRZYRODNIKÓW IM. KOPERNIKA WYDAWANE PRZY WSPÓŁUDZIALE: AKADEMII GÓRNICZO-HUTNICZEJ, MINISTERSTWA NAUKI I SZKOLNICTWA WYŻSZEGO, POLSKIEJ AKADEMII UMIEJĘTNOŚCI TOM 113 ZESZYT
PISMO POLSKIEGO TOWARZYSTWA PRZYRODNIKÓW IM. KOPERNIKA WYDAWANE PRZY WSPÓŁUDZIALE: AKADEMII GÓRNICZO-HUTNICZEJ, MINISTERSTWA NAUKI I SZKOLNICTWA WYŻSZEGO, POLSKIEJ AKADEMII UMIEJĘTNOŚCI TOM 113 ZESZYT
Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporno
 Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Wykonawcy: Dr
Zadanie 2.4 Poszerzanie puli genetycznej buraka cukrowego przez doskonalenie procesu gynogenezy oraz podnoszenie odporności na wirus nekrotycznego żółknięcia nerwów i tolerancji na suszę Wykonawcy: Dr
Przeglądanie bibliotek
 Przeglądanie bibliotek Czyli jak złapać (i sklonować) ciekawy gen? Klonowanie genów w oparciu o identyczność lub podobieństwo ich sekwencji do znanego już DNA Sonda homologiczna (komplementarna w 100%)
Przeglądanie bibliotek Czyli jak złapać (i sklonować) ciekawy gen? Klonowanie genów w oparciu o identyczność lub podobieństwo ich sekwencji do znanego już DNA Sonda homologiczna (komplementarna w 100%)
Mapa molekularna pszenicy (Triticum aestivum L.)*
 NR 243 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 27 PAWEŁ CZ. CZEMBOR MAGDALENA RADECKA EDWARD ARSENIUK Zakład Fitopatologii, Instytut Hodowli i Aklimatyzacji Roślin w Radzikowie Mapa molekularna
NR 243 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 27 PAWEŁ CZ. CZEMBOR MAGDALENA RADECKA EDWARD ARSENIUK Zakład Fitopatologii, Instytut Hodowli i Aklimatyzacji Roślin w Radzikowie Mapa molekularna
2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy
 Metody analizy DNA 1. Budowa DNA. 2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy 3. Klonowanie in vivo a. w bakteriach, wektory plazmidowe b. w fagach, kosmidy c. w drożdżach,
Metody analizy DNA 1. Budowa DNA. 2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy 3. Klonowanie in vivo a. w bakteriach, wektory plazmidowe b. w fagach, kosmidy c. w drożdżach,
Hodowla roślin genetyka stosowana
 Hodowla roślin genetyka stosowana Hodowla roślin jest świadomą działalnością człowieka zmierzającą do wytworzenia nowych, ulepszonych odmian oraz zachowania istniejących odmian na nie zmienionym poziomie.
Hodowla roślin genetyka stosowana Hodowla roślin jest świadomą działalnością człowieka zmierzającą do wytworzenia nowych, ulepszonych odmian oraz zachowania istniejących odmian na nie zmienionym poziomie.
Badania asocjacyjne w skali genomu (GWAS)
 Badania asocjacyjne w skali genomu (GWAS) Wstęp do GWAS Część 1 - Kontrola jakości Bioinformatyczna analiza danych Wykład 2 Dr Wioleta Drobik-Czwarno Katedra Genetyki i Ogólnej Hodowli Zwierząt Badania
Badania asocjacyjne w skali genomu (GWAS) Wstęp do GWAS Część 1 - Kontrola jakości Bioinformatyczna analiza danych Wykład 2 Dr Wioleta Drobik-Czwarno Katedra Genetyki i Ogólnej Hodowli Zwierząt Badania
WYBRANE RODZAJE REAKCJI PCR. RAPD PCR Nested PCR Multipleks PCR Allelo-specyficzny PCR Real Time PCR
 RAPD PR Nested PR Allelo-specyficzny PR Real Time PR RAPD PR (Random Amplification of Polymorphic DNA) wykorzystywany gdy nie znamy sekwencji starterów; pozwala namnożyć losowe fragmenty o różnej długości;
RAPD PR Nested PR Allelo-specyficzny PR Real Time PR RAPD PR (Random Amplification of Polymorphic DNA) wykorzystywany gdy nie znamy sekwencji starterów; pozwala namnożyć losowe fragmenty o różnej długości;
Przydatność technologii Sekwencjonowania Nowej Generacji (NGS) w kolekcjach Banków Genów Joanna Noceń Kinga Smolińska Marta Puchta Kierownik tematu:
 Przydatność technologii Sekwencjonowania Nowej Generacji (NGS) w kolekcjach Banków Genów Joanna Noceń Kinga Smolińska Marta Puchta Kierownik tematu: prof. dr hab. Jerzy H. Czembor SEKWENCJONOWANIE I generacji
Przydatność technologii Sekwencjonowania Nowej Generacji (NGS) w kolekcjach Banków Genów Joanna Noceń Kinga Smolińska Marta Puchta Kierownik tematu: prof. dr hab. Jerzy H. Czembor SEKWENCJONOWANIE I generacji
Bioinformatyczna analiza danych. Wykład 1 Dr Wioleta Drobik-Czwarno Katedra Genetyki i Ogólnej Hodowli Zwierząt
 Bioinformatyczna analiza danych Wykład 1 Dr Wioleta Drobik-Czwarno Katedra Genetyki i Ogólnej Hodowli Zwierząt Sprawy organizacyjne Prowadzący przedmiot: Dr Wioleta Drobik-Czwarno koordynator przedmiotu,
Bioinformatyczna analiza danych Wykład 1 Dr Wioleta Drobik-Czwarno Katedra Genetyki i Ogólnej Hodowli Zwierząt Sprawy organizacyjne Prowadzący przedmiot: Dr Wioleta Drobik-Czwarno koordynator przedmiotu,
Ekologia molekularna. wykład 1
 Ekologia molekularna wykład 1 Podręczniki Agnieszka Kloch Zakład Ekologii akloch@biol.uw.edu.pl CNBiCh, IV p, pok. 4.37 Egzamin: 31 stycznia,12:30, w tej sali wykład 1/2 Podręczniki DL Hartl, AG Clark
Ekologia molekularna wykład 1 Podręczniki Agnieszka Kloch Zakład Ekologii akloch@biol.uw.edu.pl CNBiCh, IV p, pok. 4.37 Egzamin: 31 stycznia,12:30, w tej sali wykład 1/2 Podręczniki DL Hartl, AG Clark
GRADIENT TEMPERATUR TOUCH DOWN PCR. Standardowy PCR RAPD- PCR. RealTime- PCR. Nested- PCR. Digital- PCR.
 Standardowy PCR RAPD- PCR Nested- PCR Multipleks- PCR Allelospecyficzny PCR Touchdown- PCR RealTime- PCR Digital- PCR In situ (slide)- PCR Metylacyjno specyficzny- PCR Assembly- PCR Inverse- PCR GRADIENT
Standardowy PCR RAPD- PCR Nested- PCR Multipleks- PCR Allelospecyficzny PCR Touchdown- PCR RealTime- PCR Digital- PCR In situ (slide)- PCR Metylacyjno specyficzny- PCR Assembly- PCR Inverse- PCR GRADIENT
Chromosomowa lokalizacja markerów tolerancyjności na glin u żyta
 NR 230 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 IWONA WIŚNIEWSKA ANDRZEJ RAFALSKI Zakład Biochemii i Fizjologii Roślin Instytut Hodowli i Aklimatyzacji Roślin, Radzików Chromosomowa lokalizacja
NR 230 BIULETYN INSTYTUTU HODOWLI I AKLIMATYZACJI ROŚLIN 2003 IWONA WIŚNIEWSKA ANDRZEJ RAFALSKI Zakład Biochemii i Fizjologii Roślin Instytut Hodowli i Aklimatyzacji Roślin, Radzików Chromosomowa lokalizacja
Dr hab. Beata Krawczyk Katedra Mikrobiologii, Politechnika Gdańska
 Narzędzia diagnostyki molekularnej w typowaniu genetycznym (genotypowaniu) Dr hab. Beata Krawczyk Katedra Mikrobiologii, Politechnika Gdańska Publikacja współfinansowana ze środków Unii Europejskiej w
Narzędzia diagnostyki molekularnej w typowaniu genetycznym (genotypowaniu) Dr hab. Beata Krawczyk Katedra Mikrobiologii, Politechnika Gdańska Publikacja współfinansowana ze środków Unii Europejskiej w
Biorafineria lignocelulozowa uwarunkowania środowiskowe, energetyczne i społeczno-ekonomiczne
 Biorafineria lignocelulozowa uwarunkowania środowiskowe, energetyczne i społeczno-ekonomiczne Praca wchodzi w skład monograficznej serii wydawniczej, wydanej w ramach Programu Strategicznego Zadanie Badawcze
Biorafineria lignocelulozowa uwarunkowania środowiskowe, energetyczne i społeczno-ekonomiczne Praca wchodzi w skład monograficznej serii wydawniczej, wydanej w ramach Programu Strategicznego Zadanie Badawcze
Tom Numer 4 (297) Strony
 Tom 61 2012 Numer 4 (297) Strony 597 602 Izabela Szućko, Magdalena Achrem, Anna Kalinka Katedra Biologii Komórki Wydział Biologii Uniwersytet Szczeciński Wąska 13 71-415 Szczecin E-mail: izabela.szucko@univ.szczecin.pl
Tom 61 2012 Numer 4 (297) Strony 597 602 Izabela Szućko, Magdalena Achrem, Anna Kalinka Katedra Biologii Komórki Wydział Biologii Uniwersytet Szczeciński Wąska 13 71-415 Szczecin E-mail: izabela.szucko@univ.szczecin.pl
Biologia medyczna, materiały dla studentów
 Zasada reakcji PCR Reakcja PCR (replikacja in vitro) obejmuje denaturację DNA, przyłączanie starterów (annealing) i syntezę nowych nici DNA (elongacja). 1. Denaturacja: rozplecenie nici DNA, temp. 94 o
Zasada reakcji PCR Reakcja PCR (replikacja in vitro) obejmuje denaturację DNA, przyłączanie starterów (annealing) i syntezę nowych nici DNA (elongacja). 1. Denaturacja: rozplecenie nici DNA, temp. 94 o
Ekologia molekularna. wykład 14. Genetyka ilościowa
 Ekologia molekularna wykład 14 Genetyka ilościowa Dziedziczenie mendlowskie wykład 14/2 Cechy wieloczynnikowe (ilościowe) wzrost masa ciała kolor skóry kolor oczu itp wykład 14/3 Rodzaje cech ilościowych
Ekologia molekularna wykład 14 Genetyka ilościowa Dziedziczenie mendlowskie wykład 14/2 Cechy wieloczynnikowe (ilościowe) wzrost masa ciała kolor skóry kolor oczu itp wykład 14/3 Rodzaje cech ilościowych
PCR - ang. polymerase chain reaction
 PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
S YLABUS MODUŁU (PRZEDMIOTU) I nformacje ogólne. Stacjonarne (s)
 Załącznik Nr 3 do Uchwały Senatu PUM 14/2012 S YLABUS MODUŁU (PRZEDMIOTU) I nformacje ogólne Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów Specjalność Poziom studiów Forma studiów Rok studiów Nazwa
Załącznik Nr 3 do Uchwały Senatu PUM 14/2012 S YLABUS MODUŁU (PRZEDMIOTU) I nformacje ogólne Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów Specjalność Poziom studiów Forma studiów Rok studiów Nazwa
ZARZĄDZANIE POPULACJAMI ZWIERZĄT
 ZARZĄDZANIE POPULACJAMI ZWIERZĄT Ćwiczenia 1 mgr Magda Kaczmarek-Okrój magda_kaczmarek_okroj@sggw.pl 1 ZAGADNIENIA struktura genetyczna populacji obliczanie frekwencji genotypów obliczanie frekwencji alleli
ZARZĄDZANIE POPULACJAMI ZWIERZĄT Ćwiczenia 1 mgr Magda Kaczmarek-Okrój magda_kaczmarek_okroj@sggw.pl 1 ZAGADNIENIA struktura genetyczna populacji obliczanie frekwencji genotypów obliczanie frekwencji alleli
KARTA KURSU (realizowanego w module specjalności) Biologia eksperymentalna i środowiskowa
 KARTA KURSU (realizowanego w module specjalności) Biologia eksperymentalna i środowiskowa Nazwa Nazwa w j. ang. Wybrane problemy biologii molekularnej kwasy nukleinowe Selected problems of molecular biology
KARTA KURSU (realizowanego w module specjalności) Biologia eksperymentalna i środowiskowa Nazwa Nazwa w j. ang. Wybrane problemy biologii molekularnej kwasy nukleinowe Selected problems of molecular biology
S YL AB US MODUŁ U ( PRZEDMIOTU) I nforma c j e ogólne. Biologia molekularna
 Załącznik Nr 3 do Uchwały Senatu PUM 14/2012 S YL AB US MODUŁ U ( PRZEDMIOTU) I nforma c j e ogólne Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów Specjalność Poziom studiów Forma studiów Rok studiów
Załącznik Nr 3 do Uchwały Senatu PUM 14/2012 S YL AB US MODUŁ U ( PRZEDMIOTU) I nforma c j e ogólne Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów Specjalność Poziom studiów Forma studiów Rok studiów
TECHNIKI ANALIZY RNA TECHNIKI ANALIZY RNA TECHNIKI ANALIZY RNA
 DNA 28SRNA 18/16S RNA 5SRNA mrna Ilościowa analiza mrna aktywność genów w zależności od wybranych czynników: o rodzaju tkanki o rodzaju czynnika zewnętrznego o rodzaju upośledzenia szlaku metabolicznego
DNA 28SRNA 18/16S RNA 5SRNA mrna Ilościowa analiza mrna aktywność genów w zależności od wybranych czynników: o rodzaju tkanki o rodzaju czynnika zewnętrznego o rodzaju upośledzenia szlaku metabolicznego
Inżynieria Genetyczna ćw. 3
 Materiały do ćwiczeń z przedmiotu Genetyka z inżynierią genetyczną D - blok Inżynieria Genetyczna ćw. 3 Instytut Genetyki i Biotechnologii, Wydział Biologii, Uniwersytet Warszawski, rok akad. 2018/2019
Materiały do ćwiczeń z przedmiotu Genetyka z inżynierią genetyczną D - blok Inżynieria Genetyczna ćw. 3 Instytut Genetyki i Biotechnologii, Wydział Biologii, Uniwersytet Warszawski, rok akad. 2018/2019
Co to jest transkryptom? A. Świercz ANALIZA DANYCH WYSOKOPRZEPUSTOWYCH 2
 ALEKSANDRA ŚWIERCZ Co to jest transkryptom? A. Świercz ANALIZA DANYCH WYSOKOPRZEPUSTOWYCH 2 Ekspresja genów http://genome.wellcome.ac.uk/doc_wtd020757.html A. Świercz ANALIZA DANYCH WYSOKOPRZEPUSTOWYCH
ALEKSANDRA ŚWIERCZ Co to jest transkryptom? A. Świercz ANALIZA DANYCH WYSOKOPRZEPUSTOWYCH 2 Ekspresja genów http://genome.wellcome.ac.uk/doc_wtd020757.html A. Świercz ANALIZA DANYCH WYSOKOPRZEPUSTOWYCH
Hybrydyzacja kwasów nukleinowych
 Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja tego genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja tego genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
S YLABUS MODUŁU (PRZEDMIOTU) I nformacje ogólne. Biologia medyczna. Nie dotyczy
 Załącznik Nr 3 do Uchwały enatu PUM 14/2012 YLABU MODUŁU (PRZEDMIOTU) Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów pecjalność Poziom studiów Forma studiów Rok studiów Nazwa modułu I nformacje
Załącznik Nr 3 do Uchwały enatu PUM 14/2012 YLABU MODUŁU (PRZEDMIOTU) Kod modułu Rodzaj modułu Wydział PUM Kierunek studiów pecjalność Poziom studiów Forma studiów Rok studiów Nazwa modułu I nformacje
Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej
 Seminarium 1 część 1 Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej Genom człowieka Genomem nazywamy całkowitą ilość DNA jaka
Seminarium 1 część 1 Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej Genom człowieka Genomem nazywamy całkowitą ilość DNA jaka
