cz. VII Metody projektowania leków i modelowanie molekularne
|
|
|
- Małgorzata Morawska
- 9 lat temu
- Przeglądów:
Transkrypt
1 Oddziaływanie leków z celami molekularnymi cz. VII Metody projektowania leków i modelowanie molekularne Prof. dr hab. Sławomir Filipek Uniwersytet Warszawski, Wydział Chemii 1 Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego znana 1D i 3D QSAR (pseudoreceptory i pola molekularne) Dopasowanie ligandów do miejsca aktywnego receptora (dokowanie) Budowa nowych ligandów ab-initio Receptor-based drug design Dynamika kompleksu receptor-ligand 1
2 Definicja farmakoforu Farmakofor trójwymiarowe ułożenie grup chemicznych wspólnych dla związków aktywnych i niezbędnych dla ich aktywności biologicznej. 3 Poszukiwanie farmakoforu Pierwsza hipoteza Wiele hipotez 4 2
3 Poszukiwanie farmakoforu Więcej związków pozwala zidentyfikować właściwą hipotezę Identyfikacja sterycznych bumps w miejscu aktywnym 5 Badanie roli grup funkcyjnych G.L. Patrick An Introduction to Medicinal Chemistry 3
4 Farmakofor przykładowy farmakofor Jak znaleźć farmakofor? Inhibitory bakteryjnego cytochromu Ograniczenia metody farmakoforów Nałożenie konformacji ze struktur krystalicznych 4
5 Przykład użycia farmakofora (giętkie ligandy) wczesny lek antydepresyjny (antagonista r. dopaminowego) neurotransmiter Użycie farmakofora do przeszukiwania baz struktur 3D związków chemicznych Poszukiwanie farmakoforów Active analog approach: kąty torsyjne wspólne dla wszystkich związków są systematycznie zmieniane. Farmakofor identifikuje się porównując tabele odległości Wspólna przestrzeń konformacyjna ligandów Reprezentacja 4-punktowego farmakofora. Związek w odbiciu zwierciadlanym może nie wiązać się celem mol. Farmakofor oparty na agoniście receptora dopaminowego D2 (pierścień nieistotny) Rozbudowany farmakofor dla antagonistów receptora serotoninowego (GPCR) 5
6 Farmakofory dodatkowe cechy Podział i kodowanie trzech cech farmakofora na ciągi bitów z zakresami odległości 1 Å - do szybkiego przeszukiwania baz danych 4-punktowy model farmakofora z dodatkowymi ograniczeniami: -Kąt między płaszczyznami -Odległość do płaszczyzny -Stożek wiązania wodorowego QSAR - Quantitative Structure-Activity Relationship Równanie Hanscha Log (1/c) = k 1 logp + k 2 +k 3 E s + k 4 P hydrofobowość (współczynnik podziału w układzie oktanol/woda) - efekty elektronowe E s - efekty steryczne 6
7 QSAR - inne zmienne (deskryptory) STRUKTURALNE: - Masa cząsteczki - Powierzchnia cząsteczki - Liczba wiązań rotowalnych - HBA, HBD -Objętość wspólna - Liczba centrów chiralnych TERMODYNAMICZNE: ELEKTRONOWE: GEOMETRYCZNE TOPOLOGICZNE - c log P - Ciepło tworzenia - Refrakcja molowa - Ładunki cząstkowe na atomach - Polaryzowalności atomowe - Moment dipolowy - Energia cząsteczki - Energia orbitalu HOMO - Energia orbitalu LUMO Zbyt duża liczba zmiennych QSAR Optymalnie: 3-5 związków na jeden parametr w równaniu QSAR 7
8 Wyznaczanie oddziaływań związków z sondami molekularnymi Sonda elektrostatyczna (ładunek punktowy H + ) tylko siły elektrostatyczne Sonda hydrofobowa (grupa metylowa atom C_sp 3 ) tylko siły van der Waalsa Sondy wieloatomowe -OH, -NH 2, -NH 3+, -COO, -COOH, H 2 O, siły van der Waalsa + siły elektrostatyczne (trzeba uwzględnić obroty sondy w celu znalezienia najlepszego oddziaływania z ligandem) 15 3D-QSAR Tabela QSAR 8
9 3D-QSAR 17 CoMFA Comparative Molecular Field Analysis Mapa oddziaływań dla sondy H + i CH 3 Korzystne: zielone - steryczne niebieskie - elstat. Niekorzystne: żółte - steryczne czerwone - elstat. 9
10 Założenia metody CoMFA Taki sam mechanizm działania (ten sam cel molekularny) Wiązanie się do tego samego miejsca aktywnego Wiązanie się w ten sam sposób Podobne efekty entropowe dla wszystkich związków (podobna giętkość związków) Podobne efekty desolwacyjne dla wszystkich związków (podobna wielkość związków i podobny stosunek powierzchni lipofilowej do hydrofilowej) 19 3D QSAR - Pseudoreceptory Używane potencjały: - Hydrofobowy - Jonowy dodatni - Jonowy ujemny - Donor wiązania H - Akceptor wiązania H - Hydrofobowy dodatni - Hydrofobowy ujemny 10
11 3D QSAR - Minireceptory Czynniki wpływające na skuteczność metod QSAR solwatacja liganda i receptora farmakokinetyka leku: ADMET absorption, distribution, metabolism, excretion, toxicity Reguła 5 Lipinskiego (pasywna absorpcja jelitowa ) związek nie będzie dobrym lekiem gdy: MW > 500 [g/mol lub Da] clog P > 5 (calculated logp) HBA (N, O) > 10 HBD (N-H, O-H) >
12 QSPR - predykcja własności ADMET SYBYL / Tripos Inc. 23 Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego znana 1D i 3D QSAR (pseudoreceptory i pola molekularne) Dopasowanie ligandów do miejsca aktywnego receptora (dokowanie) Budowa nowych ligandów ab-initio Receptor-based drug design Dynamika kompleksu receptor-ligand 12
13 Kroki w structure-based drug design Struktura 3D białka Identyfikacja miejsca aktywnego Analiza dopasowania ligand-receptor Dokowanie lub budowa nowych związków Rozdzielczość w krystalografii Rozdzielczość a gęstość elektronowa Przykład złego i dobrego kryształu Białka w krysztale mogą tworzyć kanały wodne 13
14 Identyfikacja miejsc wiążących i dokowanie ligandów Komplementarność powierzchni awidyny (fiolet) i biotyny (białe) DOCK sztywne/giętkie cząsteczki metoda Monte Carlo - ustawianie metoda MD - wygładzanie Metody optymalizacyjne znajdowania najlepszego dopasowania Genetic Algorithms Tabu Search Monte Carlo Simulated Annealing 14
15 Przykład rozbudowy ligandów Sposoby łączenia ligandów Optymalizacja struktury leku przy dwu miejscach wiązania Wykorzystanie alternatywnych sposobów wiązania leków z białkiem Przewidywanie siły wiązania ligandów Cykl termodynamiczny dla obliczania wymiany liganda w białku (FEP Free Energy Perturbation) G X + G C = G F + G Y ( G wymiany liganda ) = G X - G Y = G F - G C 15
16 Programy do dokowania ligandów AUTODOCK znakomity darmowy program Adaptacja enzymu do związanego inhibitora Phenylethanolamine N-methyltransferase (PNMT) katalizuje N-metylację norepinefryny 16
17 Indukowane dopasowanie wyjaśnia duże różnice w wiązaniu podobnych ligandów Przykłady dopasowań dla leków przeciwnowotworowych Imatinib (Gleevec) Kinaza ABL struktury krystaliczne Widoczna duża zmiana w położeniu pętli niedostępne dla większości programów dokujących (dopasowanie indukcyjne) 17
18 Analiza oddziaływań w kompleksie biotyna-streptoawidyna Silne wiązanie biotyny (witamina B7) K D mol/dm 3 (0.01 pm) Streptoawidyna jest uzyskiwana z bakterii Streptomyces avidinii. Znalazła zastosowanie w biotechnologii do oczyszczania białek (pi 7 więc nie wiąże się niespecyficznie z innymi białkami). Biotyna-awidyna nawet pm ale dla awidyny pi 10. Yasara Awidyna (antywitamina) - składnik jaj ptaków unieczynniana przez gotowanie. Budowanie ligandu de novo z fragmentów Outside in Inside out 18
19 Metoda budowania na siatce 37 Automatyczna metoda generowania struktur ligandów z fragmentów 38 19
20 G. Schneider Goethe-University, Frankfurt 39 8 głównych reguł strukturalnego projektowania leków 1. Związać ligand z głównymi punktami zaczepienia (oddziaływania HB i el-stat) 2. Wykorzystać oddziaływania hydrofobowe 3. Wykorzystać wiązania wodorowe do łańcucha głównego w białku i łańcuchów bocznych aa 20
21 8 głównych reguł projektowania leków 4. Wykorzystać oddziaływania jonowe (z naładowanymi aa) 6. Optymalizować kontakty van der Waalsa i unikać nachodzenia na siebie liganda i białka (bumps) 5. Unikać naprężeń w ligandzie i w białku 8 głównych reguł projektowania leków 7. Wykorzystać strukturalną wodę 8. Uwzględnić efekty entropowe (ligand bardziej sztywny) 21
22 Projektowanie inhibitora proteazy wirusa HIV-1 Struktura krystaliczna proteazy z ligandem DuPont Merck Projektowanie inhibitora proteazy wirusa HIV-1 Symetryczny diol Farmakofor Wynik poszukiwania w bazach danych Wymiana benzenu na cykloheksanon 22
23 Projektowanie inhibitora proteazy wirusa HIV-1 Zwiększenie pierścienia Dodatkowe podstawniki Produkt końcowy XK263 Zastosowanie dynamiki molekularnej Proteaza wirusa HIV z ligandem. Indukowane inhibitorem zamykanie klap proteazy 23
24 Modelowanie molekularne Modelowanie - elementy pola siłowego U bond bond k ( r r i i i 0i ) 2, U angle 2 ( ), angle k i i i 0i tors U k [ 1 cos( n )] U vdw tors i q q U, Coulomb i j i i i i j j i 4 0rij ij 4 ij rij 12 6, ij rij i Oddziaływania wiążące Oddziaływania niewiążące 24
25 Elementy pola siłowego Dynamika molekularna obliczenia dla jednego kroku dynamiki II zasada ruchu Newtona F(t) i = m i * a(t) i t = 1 fs = s a(t) i = F(t) i / m i Czas pojedynczego kroku a(t) i v(t) i r(t+ t) i r(t+ t) i F(t+ t) i 25
26 Długości symulacji w zależności od rodzajów ruchów Akwaporyna selektywny przepływ wody topologia białka z glicerolem Pełnoatomowa symulacja przepływu cząsteczek wody 26
27 Symulacje w środowiskach implicite Lazaridis, Proteins 2003 Im & Brooks, PNAS 2005 Mapowanie pola siłowego pełnoatomowego (all-atom) na gruboziarniste (coarse-grain) Gruboziarnista cząsteczka rozpuszczalnika mapowanie 4 to 1 (średnio) Krok czasowy obliczeń = fs Polar (P), nonpolar (N), apolar (C), charged (Q) 1-5 : low - high polarity d - donor, a - acceptor, da - both, 0 - none Marrink et al., J. Phys. Chem. B
28 Gruboziarnista reprezentacja aminokwasów Porównanie wyników symulacji: all-atom (50 ns GROMACS ffgmx) i coarse-grain (4 μs CHARMM martini) Monticelli et al., J. Chem. Theory and Comput Samorzutne tworzenie dwuwarstwy lipidowej Samoorganizacja błony DPPC ze wstawieniem białka OmpA (poryna) Samoorganizacja błony DPPC i utworzenie dimeru glikoforyny Bond & Sansom, JACS
29 Formowanie się domen z różnych rodzajów lipidów skala 5 nm 2 x 2 2 x : 0.28 : : 0.42 : 0.3 dic 16 -PC / dic 18:2 -PC / cholesterol Risselada et al. (Marrink group), PNAS 2008 Usuwanie lipidów z krwi przez granule HDL symulacja gruboziarnista AY Shih et al. (Schulten group), J. Struct. Biol
Komputerowe wspomaganie projektowanie leków
 Komputerowe wspomaganie projektowanie leków wykład V Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków wykład V Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków
 Komputerowe wspomaganie projektowanie leków wykład VI Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków wykład VI Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
QSAR i związki z innymi metodami. Karol Kamel Uniwersytet Warszawski
 QSAR i związki z innymi metodami Wstęp QSAR Quantitative Structure-Activity Relationship. Jest to metoda polegająca na znalezieniu (i analizie) zależności pomiędzy strukturą chemiczną (geometria cząsteczki,
QSAR i związki z innymi metodami Wstęp QSAR Quantitative Structure-Activity Relationship. Jest to metoda polegająca na znalezieniu (i analizie) zależności pomiędzy strukturą chemiczną (geometria cząsteczki,
Komputerowe wspomaganie projektowanie leków
 Komputerowe wspomaganie projektowanie leków wykład IV Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków wykład IV Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Wykład 3-4. Materiały z wykładów (plik PDF): http://www.biomodellab.eu/lecture/
 Wykład 3-4 Materiały z wykładów (plik PDF): http://www.biomodellab.eu/lecture/ Porównanie zakresów modelowania układów biologicznych Symulacje mezoskopowe, jedno ziarno = kilkanaście aminokwasów, ziarna
Wykład 3-4 Materiały z wykładów (plik PDF): http://www.biomodellab.eu/lecture/ Porównanie zakresów modelowania układów biologicznych Symulacje mezoskopowe, jedno ziarno = kilkanaście aminokwasów, ziarna
Komputerowe wspomaganie projektowanie leków
 Komputerowe wspomaganie projektowanie leków wykład VII Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków wykład VII Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Farmakofory. metody QSAR
 Farmakofory metody QSAR Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego
Farmakofory metody QSAR Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego
Komputerowe wspomaganie projektowania leków
 Komputerowe wspomaganie projektowania leków MECHANIKA MOLEKULARNA I KWANTOWA W MM korzysta się z równań wynikających z praw fizyki klasycznej i stosuje się je do jader atomów z pominięciem elektronów,
Komputerowe wspomaganie projektowania leków MECHANIKA MOLEKULARNA I KWANTOWA W MM korzysta się z równań wynikających z praw fizyki klasycznej i stosuje się je do jader atomów z pominięciem elektronów,
Dokowanie molekularne. Karol Kamel Uniwersytet Warszawski
 molekularne Wstęp Dokowanie metoda modelowania molekularnego, pozwalająca na znalezienie położenia (i konformacji) liganda w miejscu wiążącym receptora. Informacja ta pozwala na ocenę energii swobodnej
molekularne Wstęp Dokowanie metoda modelowania molekularnego, pozwalająca na znalezienie położenia (i konformacji) liganda w miejscu wiążącym receptora. Informacja ta pozwala na ocenę energii swobodnej
Oddziaływanie leków z celami molekularnymi i projektowanie leków
 Oddziaływanie leków z celami molekularnymi i projektowanie leków Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania (biomodellab.eu) Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych
Oddziaływanie leków z celami molekularnymi i projektowanie leków Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania (biomodellab.eu) Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych
Komputerowe wspomaganie projektowanie leków
 Komputerowe wspomaganie projektowanie leków wykład II Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Komputerowe wspomaganie projektowanie leków wykład II Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych Cent-III www.biomodellab.eu
Podstawy projektowania leków wykład 11
 Podstawy projektowania leków wykład 11 Łukasz Berlicki QSAR i 3D QSAR 1964, C. Hansch i T. Fujita: QSAR 1984, P. Andrews: wkład grup funkcyjnych do oddziaływania z celem molekularnym 1985, P. Goodford:
Podstawy projektowania leków wykład 11 Łukasz Berlicki QSAR i 3D QSAR 1964, C. Hansch i T. Fujita: QSAR 1984, P. Andrews: wkład grup funkcyjnych do oddziaływania z celem molekularnym 1985, P. Goodford:
Metody dokowania ligandów
 Metody dokowania ligandów Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego
Metody dokowania ligandów Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego
Podstawy projektowania leków wykład 12
 Podstawy projektowania leków wykład 12 Łukasz Berlicki Projektowanie wspomagane komputerowo Ligand-based design QSAR i 3D-QSAR Structure-based design projektowanie oparte na strukturze celu molekularnego
Podstawy projektowania leków wykład 12 Łukasz Berlicki Projektowanie wspomagane komputerowo Ligand-based design QSAR i 3D-QSAR Structure-based design projektowanie oparte na strukturze celu molekularnego
Projektowanie Nowych Chemoterapeutyków
 Jan Mazerski Katedra Technologii Leków i Biochemii Wydział Chemiczny Projektowanie Nowych Chemoterapeutyków XV. QSAR 3D QSAR w przestrzeni Rozwój metod ustalania struktury 3D dla białek i ich kompleksów.
Jan Mazerski Katedra Technologii Leków i Biochemii Wydział Chemiczny Projektowanie Nowych Chemoterapeutyków XV. QSAR 3D QSAR w przestrzeni Rozwój metod ustalania struktury 3D dla białek i ich kompleksów.
Podstawy projektowania leków wykład 10
 Podstawy projektowania leków wykład 10 Łukasz Berlicki Od eksperymentu do teorii 1964, C. Hansch i T. Fujita: QSAR 1984, P. Andrews: wkład grup funkcyjnych do oddziaływania z celem molekularnym 1985, P.
Podstawy projektowania leków wykład 10 Łukasz Berlicki Od eksperymentu do teorii 1964, C. Hansch i T. Fujita: QSAR 1984, P. Andrews: wkład grup funkcyjnych do oddziaływania z celem molekularnym 1985, P.
Bioinformatyka wykład 9
 Bioinformatyka wykład 9 14.XII.21 białkowa bioinformatyka strukturalna krzysztof_pawlowski@sggw.pl 211-1-17 1 Plan wykładu struktury białek dlaczego? struktury białek geometria i fizyka modyfikacje kowalencyjne
Bioinformatyka wykład 9 14.XII.21 białkowa bioinformatyka strukturalna krzysztof_pawlowski@sggw.pl 211-1-17 1 Plan wykładu struktury białek dlaczego? struktury białek geometria i fizyka modyfikacje kowalencyjne
Podstawy projektowania leków wykład 13
 odstawy projektowania leków wykład 13 Łukasz Berlicki rojektowanie wspomagane komputerowo rojektowanie leków oparte na strukturze często wykorzystuje metody komputerowe, aby: rzeanalizować duŝą liczbę
odstawy projektowania leków wykład 13 Łukasz Berlicki rojektowanie wspomagane komputerowo rojektowanie leków oparte na strukturze często wykorzystuje metody komputerowe, aby: rzeanalizować duŝą liczbę
Badanie długości czynników sieciujących metodami symulacji komputerowych
 Badanie długości czynników sieciujących metodami symulacji komputerowych Agnieszka Obarska-Kosińska Prof. dr hab. Bogdan Lesyng Promotorzy: Dr hab. Janusz Bujnicki Zakład Biofizyki, Instytut Fizyki Doświadczalnej,
Badanie długości czynników sieciujących metodami symulacji komputerowych Agnieszka Obarska-Kosińska Prof. dr hab. Bogdan Lesyng Promotorzy: Dr hab. Janusz Bujnicki Zakład Biofizyki, Instytut Fizyki Doświadczalnej,
Model wiązania kowalencyjnego cząsteczka H 2
 Model wiązania kowalencyjnego cząsteczka H 2 + Współrzędne elektronu i protonów Orbitale wiążący i antywiążący otrzymane jako kombinacje orbitali atomowych Orbital wiążący duża gęstość ładunku między jądrami
Model wiązania kowalencyjnego cząsteczka H 2 + Współrzędne elektronu i protonów Orbitale wiążący i antywiążący otrzymane jako kombinacje orbitali atomowych Orbital wiążący duża gęstość ładunku między jądrami
Uniwersytet Śląski w Katowicach str. 1 Wydział
 Uniwersytet Śląski w Katowicach str. 1 Kierunek i poziom studiów: Chemia II stopień Sylabus modułu: : Przedmiot C związany ze specjalnością (0310-CH-S2-003) Nazwa wariantu modułu (opcjonalnie): Chemoinformatyka
Uniwersytet Śląski w Katowicach str. 1 Kierunek i poziom studiów: Chemia II stopień Sylabus modułu: : Przedmiot C związany ze specjalnością (0310-CH-S2-003) Nazwa wariantu modułu (opcjonalnie): Chemoinformatyka
Oddziaływanie leków z celami molekularnymi i projektowanie leków
 Oddziaływanie leków z celami molekularnymi i projektowanie leków Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania (biomodellab.eu) Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych
Oddziaływanie leków z celami molekularnymi i projektowanie leków Prof. dr hab. Sławomir Filipek Grupa BIOmodelowania (biomodellab.eu) Uniwersytet Warszawski, Wydział Chemii oraz Centrum Nauk Biologiczno-Chemicznych
Strategie projektowania leków
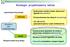 Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego znana 1D i 3D QSAR
Strategie projektowania leków Ligand-based drug design nieznana Budowanie modelu miejsc aktywnych liganda (farmakofor) Przeszukiwanie baz danych (screening) Struktura celu molekularnego znana 1D i 3D QSAR
Wykład z Chemii Ogólnej
 Wykład z Chemii Ogólnej Część 2 Budowa materii: od atomów do układów molekularnych 2.3. WIĄZANIA CHEMICZNE i ODDZIAŁYWANIA Katedra i Zakład Chemii Fizycznej Collegium Medicum w Bydgoszczy Uniwersytet Mikołaja
Wykład z Chemii Ogólnej Część 2 Budowa materii: od atomów do układów molekularnych 2.3. WIĄZANIA CHEMICZNE i ODDZIAŁYWANIA Katedra i Zakład Chemii Fizycznej Collegium Medicum w Bydgoszczy Uniwersytet Mikołaja
Rysunki pochodzą z książki Chemia medyczna, G.L. Patrick, WNT. Odwołanie do wykładu z STL
 Rysunki pochodzą z książki Chemia medyczna, G.L. Patrick, WNT Odwołanie do wykładu z STL Izolacja z surowców naturalnych jak np. rośliny, tkanki zwierzęce Lek naturalny Lek biotechnologiczny Lek syntetyczny
Rysunki pochodzą z książki Chemia medyczna, G.L. Patrick, WNT Odwołanie do wykładu z STL Izolacja z surowców naturalnych jak np. rośliny, tkanki zwierzęce Lek naturalny Lek biotechnologiczny Lek syntetyczny
Structure and Charge Density Studies of Pharmaceutical Substances in the Solid State
 Maura Malińska Wydział Chemii, Uniwersytet Warszawski Promotorzy: prof. dr hab. Krzysztof Woźniak, prof. dr hab. Andrzej Kutner Structure and Charge Density Studies of Pharmaceutical Substances in the
Maura Malińska Wydział Chemii, Uniwersytet Warszawski Promotorzy: prof. dr hab. Krzysztof Woźniak, prof. dr hab. Andrzej Kutner Structure and Charge Density Studies of Pharmaceutical Substances in the
Krystalografia. Analiza wyników rentgenowskiej analizy strukturalnej i sposób ich prezentacji
 Krystalografia Analiza wyników rentgenowskiej analizy strukturalnej i sposób ich prezentacji Opis geometrii Symetria: kryształu: grupa przestrzenna cząsteczki: grupa punktowa Parametry geometryczne współrzędne
Krystalografia Analiza wyników rentgenowskiej analizy strukturalnej i sposób ich prezentacji Opis geometrii Symetria: kryształu: grupa przestrzenna cząsteczki: grupa punktowa Parametry geometryczne współrzędne
Komputerowe wspomaganie projektowania leków
 Komputerowe wspomaganie projektowania leków MECHANIKA MOLEKULARNA I KWANTOWA W MM korzysta się z równań wynikających z praw fizyki klasycznej i stosuje się je do jader atomów z pominięciem elektronów,
Komputerowe wspomaganie projektowania leków MECHANIKA MOLEKULARNA I KWANTOWA W MM korzysta się z równań wynikających z praw fizyki klasycznej i stosuje się je do jader atomów z pominięciem elektronów,
Funkcje błon biologicznych
 Funkcje błon biologicznych Tworzenie fizycznych granic - kontrola składu komórki Selektywna przepuszczalność - transport ograniczonej liczby cząsteczek Stanowienie granic faz przekazywanie sygnałów chemicznych
Funkcje błon biologicznych Tworzenie fizycznych granic - kontrola składu komórki Selektywna przepuszczalność - transport ograniczonej liczby cząsteczek Stanowienie granic faz przekazywanie sygnałów chemicznych
ogromna liczba małych cząsteczek, doskonale elastycznych, poruszających się we wszystkich kierunkach, tory prostoliniowe, kierunek ruchu zmienia się
 CHEMIA NIEORGANICZNA Dr hab. Andrzej Kotarba Zakład Chemii Nieorganicznej Wydział Chemii I pietro p. 138 WYKŁAD - STAN GAZOWY i CHEMIA GAZÓW kinetyczna teoria gazów ogromna liczba małych cząsteczek, doskonale
CHEMIA NIEORGANICZNA Dr hab. Andrzej Kotarba Zakład Chemii Nieorganicznej Wydział Chemii I pietro p. 138 WYKŁAD - STAN GAZOWY i CHEMIA GAZÓW kinetyczna teoria gazów ogromna liczba małych cząsteczek, doskonale
Żwirki i Wigury 93, Warszawa TEL.: , FAX: , E- MAIL: Dr hab. Joanna T
 Żwirki i Wigury 93, 02-089 Warszawa TEL.: + 48 22 55 40 800, FAX: +48 22 55 40 801, E- MAIL: sekretariat@uw.edu.pl www.cent.uw.edu.pl Dr hab. Joanna Trylska, prof. UW tel. (22) 5540843 e- mail: joanna@cent.uw.edu.pl
Żwirki i Wigury 93, 02-089 Warszawa TEL.: + 48 22 55 40 800, FAX: +48 22 55 40 801, E- MAIL: sekretariat@uw.edu.pl www.cent.uw.edu.pl Dr hab. Joanna Trylska, prof. UW tel. (22) 5540843 e- mail: joanna@cent.uw.edu.pl
Dokowanie molekularne. Andrzej Bąk Instytut Chemii UŚ chemoinformatyka wykład 1
 Dokowanie molekularne Andrzej Bąk Instytut Chemii UŚ chemoinformatyka wykład 1 Zarys Oddziaływanie ligand-receptor Modelowanie struktury receptora Reprezentacja makromolekuł Opis energii oddziaływań ligand-receptor
Dokowanie molekularne Andrzej Bąk Instytut Chemii UŚ chemoinformatyka wykład 1 Zarys Oddziaływanie ligand-receptor Modelowanie struktury receptora Reprezentacja makromolekuł Opis energii oddziaływań ligand-receptor
Orbitale typu σ i typu π
 Orbitale typu σ i typu π Dwa odpowiadające sobie orbitale sąsiednich atomów tworzą kombinacje: wiążącą i antywiążącą. W rezultacie mogą powstać orbitale o rozkładzie przestrzennym dwojakiego typu: σ -
Orbitale typu σ i typu π Dwa odpowiadające sobie orbitale sąsiednich atomów tworzą kombinacje: wiążącą i antywiążącą. W rezultacie mogą powstać orbitale o rozkładzie przestrzennym dwojakiego typu: σ -
Czy poprawki ZPV do stałych ekranowania zależą od konformacji? Przypadek dimetoksymetanu
 Czy poprawki ZPV do stałych ekranowania zależą od konformacji? Przypadek dimetoksymetanu Wojciech Migda Wydział Chemii, Uniwersytet Jagielloński, Kraków Bronowice, 1-2 XII 2004 Zero-Point Vibrational Corrections
Czy poprawki ZPV do stałych ekranowania zależą od konformacji? Przypadek dimetoksymetanu Wojciech Migda Wydział Chemii, Uniwersytet Jagielloński, Kraków Bronowice, 1-2 XII 2004 Zero-Point Vibrational Corrections
Różne typy wiązań mają ta sama przyczynę: energia powstającej stabilnej cząsteczki jest mniejsza niż sumaryczna energia tworzących ją, oddalonych
 Wiązania atomowe Atomy wieloelektronowe, obsadzanie stanów elektronowych, układ poziomów energii. Przykładowe konfiguracje elektronów, gazy szlachetne, litowce, chlorowce, układ okresowy pierwiastków,
Wiązania atomowe Atomy wieloelektronowe, obsadzanie stanów elektronowych, układ poziomów energii. Przykładowe konfiguracje elektronów, gazy szlachetne, litowce, chlorowce, układ okresowy pierwiastków,
PODSTAWY CHEMII INŻYNIERIA BIOMEDYCZNA. Wykład 2
 PODSTAWY CEMII INŻYNIERIA BIOMEDYCZNA Wykład Plan wykładu II,III Woda jako rozpuszczalnik Zjawisko dysocjacji Równowaga w roztworach elektrolitów i co z tego wynika Bufory ydroliza soli Roztwory (wodne)-
PODSTAWY CEMII INŻYNIERIA BIOMEDYCZNA Wykład Plan wykładu II,III Woda jako rozpuszczalnik Zjawisko dysocjacji Równowaga w roztworach elektrolitów i co z tego wynika Bufory ydroliza soli Roztwory (wodne)-
Badanie oddziaływań związków biologicznie aktywnych z modelowymi membranami lipidowymi
 UNIWERSYTET JAGIELLOŃSKI W KRAKOWIE WYDZIAŁ CHEMII STRESZCZENIE ROZPRAWY DOKTORSKIEJ Badanie oddziaływań związków biologicznie aktywnych z modelowymi membranami lipidowymi Marcelina Gorczyca Promotorzy:
UNIWERSYTET JAGIELLOŃSKI W KRAKOWIE WYDZIAŁ CHEMII STRESZCZENIE ROZPRAWY DOKTORSKIEJ Badanie oddziaływań związków biologicznie aktywnych z modelowymi membranami lipidowymi Marcelina Gorczyca Promotorzy:
Bioinformatyka II Modelowanie struktury białek
 Bioinformatyka II Modelowanie struktury białek 1. Który spośród wymienionych szablonów wybierzesz do modelowania dla każdego z podanych przypadków? Dlaczego? Struktura krystaliczną czy NMR (to samo białko,
Bioinformatyka II Modelowanie struktury białek 1. Który spośród wymienionych szablonów wybierzesz do modelowania dla każdego z podanych przypadków? Dlaczego? Struktura krystaliczną czy NMR (to samo białko,
Wykład 5-6. leki przeciwwirusowe i przeciwnowotworowe
 Wykład 5-6 leki przeciwwirusowe i przeciwnowotworowe Budowa i działanie wirusów Wirusy RNA: grypa, rotawirus, SARS, wir. zap. wątroby A i C, Ebola, HIV Wirusy DNA: - ospa prawdziwa (smallpox), - ospa wietrzna
Wykład 5-6 leki przeciwwirusowe i przeciwnowotworowe Budowa i działanie wirusów Wirusy RNA: grypa, rotawirus, SARS, wir. zap. wątroby A i C, Ebola, HIV Wirusy DNA: - ospa prawdziwa (smallpox), - ospa wietrzna
Wydział Chemiczny Wybrzeże Wyspiańskiego 27, Wrocław. Prof. dr hab. Ilona Turowska-Tyrk Wrocław, r.
 Wydział Chemiczny Wybrzeże Wyspiańskiego 27, 50-370 Wrocław Prof. dr hab. Ilona Turowska-Tyrk Wrocław, 18.01.2016 r. Recenzja rozprawy doktorskiej mgr Pauliny Klimentowskiej pt. Krystalochemia wybranych
Wydział Chemiczny Wybrzeże Wyspiańskiego 27, 50-370 Wrocław Prof. dr hab. Ilona Turowska-Tyrk Wrocław, 18.01.2016 r. Recenzja rozprawy doktorskiej mgr Pauliny Klimentowskiej pt. Krystalochemia wybranych
Optymalizacja optymalizacji
 7 maja 2008 Wstęp Optymalizacja lokalna Optymalizacja globalna Algorytmy genetyczne Badane czasteczki Wykorzystane oprogramowanie (Algorytm genetyczny) 2 Sieć neuronowa Pochodne met-enkefaliny Optymalizacja
7 maja 2008 Wstęp Optymalizacja lokalna Optymalizacja globalna Algorytmy genetyczne Badane czasteczki Wykorzystane oprogramowanie (Algorytm genetyczny) 2 Sieć neuronowa Pochodne met-enkefaliny Optymalizacja
Podstawowe prawa opisujące właściwości gazów zostały wyprowadzone dla gazu modelowego, nazywanego gazem doskonałym (idealnym).
 Spis treści 1 Stan gazowy 2 Gaz doskonały 21 Definicja mikroskopowa 22 Definicja makroskopowa (termodynamiczna) 3 Prawa gazowe 31 Prawo Boyle a-mariotte a 32 Prawo Gay-Lussaca 33 Prawo Charlesa 34 Prawo
Spis treści 1 Stan gazowy 2 Gaz doskonały 21 Definicja mikroskopowa 22 Definicja makroskopowa (termodynamiczna) 3 Prawa gazowe 31 Prawo Boyle a-mariotte a 32 Prawo Gay-Lussaca 33 Prawo Charlesa 34 Prawo
- parametry geometryczne badanego związku: współrzędne i typy atomów, ich masy, ładunki, prędkości początkowe itp. (w NAMD plik.
 Avogadro Tworzenie i manipulacja modelami związków chemicznych. W symulacjach dynamiki molekularnej kluczowych elementem jest przygotowanie układu do symulacji tzn. stworzyć pliki wejściowe zawierające
Avogadro Tworzenie i manipulacja modelami związków chemicznych. W symulacjach dynamiki molekularnej kluczowych elementem jest przygotowanie układu do symulacji tzn. stworzyć pliki wejściowe zawierające
1. Od czego i w jaki sposób zależy szybkość reakcji chemicznej?
 Tematy opisowe 1. Od czego i w jaki sposób zależy szybkość reakcji chemicznej? 2. Omów pomiar potencjału na granicy faz elektroda/roztwór elektrolitu. Podaj przykład, omów skale potencjału i elektrody
Tematy opisowe 1. Od czego i w jaki sposób zależy szybkość reakcji chemicznej? 2. Omów pomiar potencjału na granicy faz elektroda/roztwór elektrolitu. Podaj przykład, omów skale potencjału i elektrody
Bioinformatyka wykład 11, 11.I.2011 Białkowa bioinformatyka strukturalna c.d.
 Bioinformatyka wykład 11, 11.I.2011 Białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 11.01.11 1 Dopasowanie strukturalne (alignment) odległość: d ij = (x i -x J ) 2 + (y i -y J ) 2
Bioinformatyka wykład 11, 11.I.2011 Białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 11.01.11 1 Dopasowanie strukturalne (alignment) odległość: d ij = (x i -x J ) 2 + (y i -y J ) 2
Komputerowe wspomaganie projektowania leków - QSAR
 Komputerowe wspomaganie projektowania leków - QSAR JAKIE OBIEKTY SĄ INTERESUJĄCE? Długość pojazdu wynosi 2 nm, szerokość 2nm. Pojazd porusza się na kołach złożonych z 60 atomów czystego węgla, uformowanych
Komputerowe wspomaganie projektowania leków - QSAR JAKIE OBIEKTY SĄ INTERESUJĄCE? Długość pojazdu wynosi 2 nm, szerokość 2nm. Pojazd porusza się na kołach złożonych z 60 atomów czystego węgla, uformowanych
1 i 2. Struktura elektronowa atomów, tworzenie wiązań chemicznych
 1 i 2. Struktura elektronowa atomów, tworzenie wiązań chemicznych 1 1.1. Struktura elektronowa atomów Rozkład elektronów na pierwszych czterech powłokach elektronowych 1. powłoka 2. powłoka 3. powłoka
1 i 2. Struktura elektronowa atomów, tworzenie wiązań chemicznych 1 1.1. Struktura elektronowa atomów Rozkład elektronów na pierwszych czterech powłokach elektronowych 1. powłoka 2. powłoka 3. powłoka
Wiązania chemiczne. Związek klasyfikacji ciał krystalicznych z charakterem wiązań atomowych. 5 typów wiązań
 Wiązania chemiczne Związek klasyfikacji ciał krystalicznych z charakterem wiązań atomowych 5 typów wiązań wodorowe A - H - A, jonowe ( np. KCl ) molekularne (pomiędzy atomami gazów szlachetnych i małymi
Wiązania chemiczne Związek klasyfikacji ciał krystalicznych z charakterem wiązań atomowych 5 typów wiązań wodorowe A - H - A, jonowe ( np. KCl ) molekularne (pomiędzy atomami gazów szlachetnych i małymi
Kierunek i poziom studiów: Chemia. Drugi. Sylabus modułu: Chemia kwantowa i modelowanie molekularne (0310-CH-S2-B-062)
 Uniwersytet Śląski w Katowicach str. 1 Kierunek i poziom studiów: Chemia. Drugi. Sylabus modułu: Chemia kwantowa i modelowanie molekularne (0310-CH-S2-B-062) 1. Informacje ogólne koordynator modułu dr
Uniwersytet Śląski w Katowicach str. 1 Kierunek i poziom studiów: Chemia. Drugi. Sylabus modułu: Chemia kwantowa i modelowanie molekularne (0310-CH-S2-B-062) 1. Informacje ogólne koordynator modułu dr
Bioinformatyka II Modelowanie struktury białek
 Bioinformatyka II Modelowanie struktury białek 1. Który spośród wymienionych szablonów wybierzesz do modelowania? Dlaczego? Struktura krystaliczną czy NMR (to samo białko, ta sama rozdzielczość)? Strukturę
Bioinformatyka II Modelowanie struktury białek 1. Który spośród wymienionych szablonów wybierzesz do modelowania? Dlaczego? Struktura krystaliczną czy NMR (to samo białko, ta sama rozdzielczość)? Strukturę
Temat Ocena dopuszczająca Ocena dostateczna Ocena dobra Ocena bardzo dobra Ocena celująca. Uczeń:
 Chemia - klasa I (część 2) Wymagania edukacyjne Temat Ocena dopuszczająca Ocena dostateczna Ocena dobra Ocena bardzo dobra Ocena celująca Dział 1. Chemia nieorganiczna Lekcja organizacyjna. Zapoznanie
Chemia - klasa I (część 2) Wymagania edukacyjne Temat Ocena dopuszczająca Ocena dostateczna Ocena dobra Ocena bardzo dobra Ocena celująca Dział 1. Chemia nieorganiczna Lekcja organizacyjna. Zapoznanie
Wykład przygotowany w oparciu o podręczniki:
 Slajd 1 Wykład przygotowany w oparciu o podręczniki: Organic Chemistry 4 th Edition Paula Yurkanis Bruice Slajd 2 Struktura elektronowa wiązanie chemiczne Kwasy i zasady Slajd 3 Chemia organiczna Związki
Slajd 1 Wykład przygotowany w oparciu o podręczniki: Organic Chemistry 4 th Edition Paula Yurkanis Bruice Slajd 2 Struktura elektronowa wiązanie chemiczne Kwasy i zasady Slajd 3 Chemia organiczna Związki
Struktura i funkcja białek (I mgr)
 Struktura i funkcja białek (I mgr) Dr Filip Jeleń fj@protein.pl http://www.protein.pl/ Jeremy M. Berg, John L. Tymoczko, Lubert Stryer Biochemia Carl Branden, John Tooze Introduction to Protein Structure
Struktura i funkcja białek (I mgr) Dr Filip Jeleń fj@protein.pl http://www.protein.pl/ Jeremy M. Berg, John L. Tymoczko, Lubert Stryer Biochemia Carl Branden, John Tooze Introduction to Protein Structure
Modelowanie molekularne w projektowaniu leków
 Modelowanie molekularne w projektowaniu leków Wykład I Wstęp (o czym będę a o czym nie będę mówić) Opis układu Solwent (woda z rozpuszczonymi jonami i innymi substancjami) Ligand (potencjalny lek) Makromolekuła
Modelowanie molekularne w projektowaniu leków Wykład I Wstęp (o czym będę a o czym nie będę mówić) Opis układu Solwent (woda z rozpuszczonymi jonami i innymi substancjami) Ligand (potencjalny lek) Makromolekuła
Zakład Chemii Teoretycznej i Strukturalnej
 Badania struktury i aktywności nietypowego enzymu dekapującego ze Świdrowca nagany Białko TbALPH1 zostało zidentyfikowane jako enzym dekapujący w pasożytniczym pierwotniaku, świdrowcu nagany Trypasonoma
Badania struktury i aktywności nietypowego enzymu dekapującego ze Świdrowca nagany Białko TbALPH1 zostało zidentyfikowane jako enzym dekapujący w pasożytniczym pierwotniaku, świdrowcu nagany Trypasonoma
Modelowanie rozpoznawania w układzie lek-receptor
 Modelowanie rozpoznawania w układzie lek-receptor rok model autor 1890 1958 2003 klucza i zamka (lock-and-key) komplementarność indukowanego dopasowania (induced fit) tolerancja zespołu konformacji (ensemble
Modelowanie rozpoznawania w układzie lek-receptor rok model autor 1890 1958 2003 klucza i zamka (lock-and-key) komplementarność indukowanego dopasowania (induced fit) tolerancja zespołu konformacji (ensemble
Atomy wieloelektronowe
 Wiązania atomowe Atomy wieloelektronowe, obsadzanie stanów elektronowych, układ poziomów energii. Przykładowe konfiguracje elektronów, gazy szlachetne, litowce, chlorowce, układ okresowy pierwiastków,
Wiązania atomowe Atomy wieloelektronowe, obsadzanie stanów elektronowych, układ poziomów energii. Przykładowe konfiguracje elektronów, gazy szlachetne, litowce, chlorowce, układ okresowy pierwiastków,
Bioinformatyka wykład 8, 27.XI.2012
 Bioinformatyka wykład 8, 27.XI.2012 białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 2013-01-21 1 Plan wykładu regiony nieuporządkowane sposoby przedstawienia struktur białkowych powierzchnia
Bioinformatyka wykład 8, 27.XI.2012 białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 2013-01-21 1 Plan wykładu regiony nieuporządkowane sposoby przedstawienia struktur białkowych powierzchnia
Cz. I Materiał powtórzeniowy do sprawdzianu dla klas II LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania
 Cz. I Materiał powtórzeniowy do sprawdzianu dla klas II LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania I. Elektroujemność pierwiastków i elektronowa teoria wiązań Lewisa-Kossela
Cz. I Materiał powtórzeniowy do sprawdzianu dla klas II LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania I. Elektroujemność pierwiastków i elektronowa teoria wiązań Lewisa-Kossela
Recenzja rozprawy doktorskiej mgr. Tomasza Makarewicza, pt.
 Prof. dr hab. Sławomir Filipek, Wydział Chemii, Centrum Nauk Biologiczno-Chemicznych, Uniwersytet Warszawski, ul. Pasteura 1, 02-093 Warszawa Tel. 22-55-26405, E-mail: sfilipek@chem.uw.edu.pl Warszawa,
Prof. dr hab. Sławomir Filipek, Wydział Chemii, Centrum Nauk Biologiczno-Chemicznych, Uniwersytet Warszawski, ul. Pasteura 1, 02-093 Warszawa Tel. 22-55-26405, E-mail: sfilipek@chem.uw.edu.pl Warszawa,
Wstęp do Optyki i Fizyki Materii Skondensowanej
 Wstęp do Optyki i Fizyki Materii Skondensowanej Część I: Optyka, wykład 9 wykład: Piotr Fita pokazy: Andrzej Wysmołek ćwiczenia: Anna Grochola, Barbara Piętka Wydział Fizyki Uniwersytet Warszawski 2014/15
Wstęp do Optyki i Fizyki Materii Skondensowanej Część I: Optyka, wykład 9 wykład: Piotr Fita pokazy: Andrzej Wysmołek ćwiczenia: Anna Grochola, Barbara Piętka Wydział Fizyki Uniwersytet Warszawski 2014/15
Stany skupienia materii
 Stany skupienia materii Ciała stałe - ustalony kształt i objętość - uporządkowanie dalekiego zasięgu - oddziaływania harmoniczne Ciecze -słabo ściśliwe - uporządkowanie bliskiego zasięgu -tworzą powierzchnię
Stany skupienia materii Ciała stałe - ustalony kształt i objętość - uporządkowanie dalekiego zasięgu - oddziaływania harmoniczne Ciecze -słabo ściśliwe - uporządkowanie bliskiego zasięgu -tworzą powierzchnię
Repetytorium z wybranych zagadnień z chemii
 Repetytorium z wybranych zagadnień z chemii Mol jest to liczebność materii występująca, gdy liczba cząstek (elementów) układu jest równa liczbie atomów zawartych w masie 12 g węgla 12 C (równa liczbie
Repetytorium z wybranych zagadnień z chemii Mol jest to liczebność materii występująca, gdy liczba cząstek (elementów) układu jest równa liczbie atomów zawartych w masie 12 g węgla 12 C (równa liczbie
3. Cząsteczki i wiązania
 3. Cząsteczki i wiązania Elektrony walencyjne Wiązania jonowe i kowalencyjne Wiązanie typu σ i π Hybrydyzacja Przewidywanie kształtu cząsteczek AX n Orbitale zdelokalizowane Cząsteczki związków organicznych
3. Cząsteczki i wiązania Elektrony walencyjne Wiązania jonowe i kowalencyjne Wiązanie typu σ i π Hybrydyzacja Przewidywanie kształtu cząsteczek AX n Orbitale zdelokalizowane Cząsteczki związków organicznych
Zasady obsadzania poziomów
 Zasady obsadzania poziomów Model atomu Bohra Model kwantowy atomu Fala stojąca Liczby kwantowe -główna liczba kwantowa (n = 1,2,3...) kwantuje energię elektronu (numer orbity) -poboczna liczba kwantowa
Zasady obsadzania poziomów Model atomu Bohra Model kwantowy atomu Fala stojąca Liczby kwantowe -główna liczba kwantowa (n = 1,2,3...) kwantuje energię elektronu (numer orbity) -poboczna liczba kwantowa
Ćwiczenie 4: Modelowanie reakcji chemicznych. Stan przejściowy.
 Ćwiczenie 4: Modelowanie reakcji chemicznych. Stan przejściowy. Celem ćwiczenia jest wymodelowanie przebiegu reakcji chemicznej podstawienia nukleofilowego zachodzącego zgodnie z mechanizmem SN2. Wprowadzenie:
Ćwiczenie 4: Modelowanie reakcji chemicznych. Stan przejściowy. Celem ćwiczenia jest wymodelowanie przebiegu reakcji chemicznej podstawienia nukleofilowego zachodzącego zgodnie z mechanizmem SN2. Wprowadzenie:
Chemiczne składniki komórek
 Chemiczne składniki komórek Pierwiastki chemiczne w komórkach: - makroelementy (pierwiastki biogenne) H, O, C, N, S, P Ca, Mg, K, Na, Cl >1% suchej masy - mikroelementy Fe, Cu, Mn, Mo, B, Zn, Co, J, F
Chemiczne składniki komórek Pierwiastki chemiczne w komórkach: - makroelementy (pierwiastki biogenne) H, O, C, N, S, P Ca, Mg, K, Na, Cl >1% suchej masy - mikroelementy Fe, Cu, Mn, Mo, B, Zn, Co, J, F
Bioinformatyka wykład 3.I.2008
 Bioinformatyka wykład 3.I.2008 Białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 2008-01-03 1 Plan wykładu analiza i porównywanie struktur białek. doświadczalne metody badania struktur
Bioinformatyka wykład 3.I.2008 Białkowa bioinformatyka strukturalna c.d. krzysztof_pawlowski@sggw.pl 2008-01-03 1 Plan wykładu analiza i porównywanie struktur białek. doświadczalne metody badania struktur
Cz. I Materiał powtórzeniowy do sprawdzianu dla klas I LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania
 Cz. I Materiał powtórzeniowy do sprawdzianu dla klas I LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania I. Elektroujemność pierwiastków i elektronowa teoria wiązań Lewisa-Kossela
Cz. I Materiał powtórzeniowy do sprawdzianu dla klas I LO - Wiązania chemiczne + przykładowe zadania i proponowane rozwiązania I. Elektroujemność pierwiastków i elektronowa teoria wiązań Lewisa-Kossela
( ) ρ ( ) ( ) ( ) ( ) ( ) Rozkład ładunku i momenty dipolowe cząsteczek. woda H 2 O. aceton (CH 3 ) 2 CO
 Rozkład ładunku i momenty dipolowe cząsteczek W fizyce klasycznej moment dipolowy układu ładunków oblicza się tak: i i i ( ) ρ ( ) µ = q r lub µ = ρ x, y, z r dxdydz = x, y, z r dv W teorii kwantowej moment
Rozkład ładunku i momenty dipolowe cząsteczek W fizyce klasycznej moment dipolowy układu ładunków oblicza się tak: i i i ( ) ρ ( ) µ = q r lub µ = ρ x, y, z r dxdydz = x, y, z r dv W teorii kwantowej moment
Dotyczy to zarówno istniejących już związków, jak i związków, których jeszcze dotąd nie otrzymano.
 Chemia teoretyczna to dział chemii zaliczany do chemii fizycznej, zajmujący się zagadnieniami związanymi z wiedzą chemiczną od strony teoretycznej, tj. bez wykonywania eksperymentów na stole laboratoryjnym.
Chemia teoretyczna to dział chemii zaliczany do chemii fizycznej, zajmujący się zagadnieniami związanymi z wiedzą chemiczną od strony teoretycznej, tj. bez wykonywania eksperymentów na stole laboratoryjnym.
Obliczenia chemiczne. Zakład Chemii Medycznej Pomorski Uniwersytet Medyczny
 Obliczenia chemiczne Zakład Chemii Medycznej Pomorski Uniwersytet Medyczny 1 STĘŻENIA ROZTWORÓW Stężenia procentowe Procent masowo-masowy (wagowo-wagowy) (% m/m) (% w/w) liczba gramów substancji rozpuszczonej
Obliczenia chemiczne Zakład Chemii Medycznej Pomorski Uniwersytet Medyczny 1 STĘŻENIA ROZTWORÓW Stężenia procentowe Procent masowo-masowy (wagowo-wagowy) (% m/m) (% w/w) liczba gramów substancji rozpuszczonej
Trójkąt Gibbsa Równowagi układów z ograniczoną mieszalnością składników Prawo podziału Nernsta
 Termodynamiczny opis równowag w układach trójskładnikowych 3.4.1. Trójkąt Gibbsa 3.4.2. Równowagi układów z ograniczoną mieszalnością składników 3.4.3. Prawo podziału Nernsta Układy trójskładnikowe Liczba
Termodynamiczny opis równowag w układach trójskładnikowych 3.4.1. Trójkąt Gibbsa 3.4.2. Równowagi układów z ograniczoną mieszalnością składników 3.4.3. Prawo podziału Nernsta Układy trójskładnikowe Liczba
Podstawy projektowania leków wykład 14
 Podstawy projektowania leków wykład 14 Łukasz Berlicki Korzystne właściwości leków Wysoka aktywność i selektywność Dostępność syntetyczna Brak grup chemicznie reaktywnych MoŜliwość podawania doustnego
Podstawy projektowania leków wykład 14 Łukasz Berlicki Korzystne właściwości leków Wysoka aktywność i selektywność Dostępność syntetyczna Brak grup chemicznie reaktywnych MoŜliwość podawania doustnego
Charakterystyka struktury kryształu na podstawie pliku CIF (Crystallographic Information File)
 INSTRUKCJA DO ĆWICZEŃ Charakterystyka struktury kryształu na podstawie pliku CIF (Crystallographic Information File) I. Cel ćwiczenia Głównym celem ćwiczenia jest przeprowadzenie pełnej charakterystyki
INSTRUKCJA DO ĆWICZEŃ Charakterystyka struktury kryształu na podstawie pliku CIF (Crystallographic Information File) I. Cel ćwiczenia Głównym celem ćwiczenia jest przeprowadzenie pełnej charakterystyki
Właściwości błony komórkowej
 płynność asymetria Właściwości błony komórkowej selektywna przepuszczalność Płynność i stan fazowy - ruchy rotacyjne: obrotowe wokół długiej osi cząsteczki - ruchy fleksyjne zginanie łańcucha alifatycznego
płynność asymetria Właściwości błony komórkowej selektywna przepuszczalność Płynność i stan fazowy - ruchy rotacyjne: obrotowe wokół długiej osi cząsteczki - ruchy fleksyjne zginanie łańcucha alifatycznego
Liniowe i nieliniowe własciwości optyczne chromoforów organiczych. Summer 2012, W_12
 Liniowe i nieliniowe własciwości optyczne chromoforów organiczych Powszechność SHG: Każda molekuła niecentrosymetryczna D-p-A p musi być łatwo polaryzowalna CT o niskiej energii Uporządkowanie ukierunkowanie
Liniowe i nieliniowe własciwości optyczne chromoforów organiczych Powszechność SHG: Każda molekuła niecentrosymetryczna D-p-A p musi być łatwo polaryzowalna CT o niskiej energii Uporządkowanie ukierunkowanie
Modelowanie molekularne
 Ck08 Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 10 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody
Ck08 Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 10 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody
WARSZTATY olimpijskie. Co już było: Atomy i elektrony Cząsteczki i wiązania Stechiometria Gazy, termochemia Równowaga chemiczna Kinetyka
 WARSZTATY olimpijskie Co już było: Atomy i elektrony Cząsteczki i wiązania Stechiometria Gazy, termochemia Równowaga chemiczna inetyka WARSZTATY olimpijskie Co będzie: Data Co robimy 1 XII 2016 wasy i
WARSZTATY olimpijskie Co już było: Atomy i elektrony Cząsteczki i wiązania Stechiometria Gazy, termochemia Równowaga chemiczna inetyka WARSZTATY olimpijskie Co będzie: Data Co robimy 1 XII 2016 wasy i
Projektowanie Wirtualne bloki tematyczne PW I
 Podstawowe zagadnienia egzaminacyjne Projektowanie Wirtualne - część teoretyczna Projektowanie Wirtualne bloki tematyczne PW I 1. Projektowanie wirtualne specyfika procesu projektowania wirtualnego, podstawowe
Podstawowe zagadnienia egzaminacyjne Projektowanie Wirtualne - część teoretyczna Projektowanie Wirtualne bloki tematyczne PW I 1. Projektowanie wirtualne specyfika procesu projektowania wirtualnego, podstawowe
Chemia ogólna nieorganiczna Wykład XII Kinetyka i statyka chemiczna
 Chemia ogólna nieorganiczna Wykład 10 14 XII 2016 Kinetyka i statyka chemiczna Elementy kinetyki i statyki chemicznej bada drogi przemiany substratów w produkty szybkość(v) reakcji chem. i zależność od
Chemia ogólna nieorganiczna Wykład 10 14 XII 2016 Kinetyka i statyka chemiczna Elementy kinetyki i statyki chemicznej bada drogi przemiany substratów w produkty szybkość(v) reakcji chem. i zależność od
Modelowanie molekularne
 Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 4 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody chemii
Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 4 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody chemii
Lek od pomysłu do wdrożenia
 Lek od pomysłu do wdrożenia Lek od pomysłu do wdrożenia KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU
Lek od pomysłu do wdrożenia Lek od pomysłu do wdrożenia KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU KRÓTKA HISTORIA LEKU
Bioinformatyka wykład 10.I.2008
 Bioinformatyka wykład 10.I.2008 Przewidywanie struktur białek krzysztof_pawlowski@sggw.pl 2008-01-10 1 Plan wykładu pole siłowe - opis energetyczny struktur białka proces zwijania się białek przewidywanie
Bioinformatyka wykład 10.I.2008 Przewidywanie struktur białek krzysztof_pawlowski@sggw.pl 2008-01-10 1 Plan wykładu pole siłowe - opis energetyczny struktur białka proces zwijania się białek przewidywanie
Bioinformatyka wykład 10
 Bioinformatyka wykład 10 21.XII.2010 białkowa bioinformatyka strukturalna, c.d. krzysztof_pawlowski@sggw.pl 2011-01-17 1 Regiony nieuporządkowane disordered regions trudna definicja trudne do przewidzenia
Bioinformatyka wykład 10 21.XII.2010 białkowa bioinformatyka strukturalna, c.d. krzysztof_pawlowski@sggw.pl 2011-01-17 1 Regiony nieuporządkowane disordered regions trudna definicja trudne do przewidzenia
Wykład 8. Równowaga fazowa Roztwory rzeczywiste
 Wykład 8 Równowaga fazowa Roztwory rzeczywiste Roztwory doskonałe Porównanie roztworów doskonałych i Roztwory Doskonałe rzeczywistych Roztwory Rzeczywiste Spełniają prawo Raoulta Mieszanie w warunkach
Wykład 8 Równowaga fazowa Roztwory rzeczywiste Roztwory doskonałe Porównanie roztworów doskonałych i Roztwory Doskonałe rzeczywistych Roztwory Rzeczywiste Spełniają prawo Raoulta Mieszanie w warunkach
S. Baran - Podstawy fizyki materii skondensowanej Wiązania chemiczne w ciałach stałych. Wiązania chemiczne w ciałach stałych
 Wiązania chemiczne w ciałach stałych Wiązania chemiczne w ciałach stałych typ kowalencyjne jonowe metaliczne Van der Waalsa wodorowe siła* silne silne silne pochodzenie uwspólnienie e- (pary e-) przez
Wiązania chemiczne w ciałach stałych Wiązania chemiczne w ciałach stałych typ kowalencyjne jonowe metaliczne Van der Waalsa wodorowe siła* silne silne silne pochodzenie uwspólnienie e- (pary e-) przez
Modelowanie molekularne
 Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 4 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody chemii
Modelowanie molekularne metodami chemii kwantowej Dr hab. Artur Michalak Zakład Chemii Teoretycznej Wydział Chemii UJ Wykład 4 http://www.chemia.uj.edu.pl/~michalak/mmod2007/ Podstawowe idee i metody chemii
Podczerwień bliska: cm -1 (0,7-2,5 µm) Podczerwień właściwa: cm -1 (2,5-14,3 µm) Podczerwień daleka: cm -1 (14,3-50 µm)
 SPEKTROSKOPIA W PODCZERWIENI Podczerwień bliska: 14300-4000 cm -1 (0,7-2,5 µm) Podczerwień właściwa: 4000-700 cm -1 (2,5-14,3 µm) Podczerwień daleka: 700-200 cm -1 (14,3-50 µm) WIELKOŚCI CHARAKTERYZUJĄCE
SPEKTROSKOPIA W PODCZERWIENI Podczerwień bliska: 14300-4000 cm -1 (0,7-2,5 µm) Podczerwień właściwa: 4000-700 cm -1 (2,5-14,3 µm) Podczerwień daleka: 700-200 cm -1 (14,3-50 µm) WIELKOŚCI CHARAKTERYZUJĄCE
Rzędy wiązań chemicznych
 Seminarium Magisterskie Rzędy wiązań chemicznych w ujęciu Teorii Komunikacji Opracowanie Dariusz Szczepanik Promotor Dr hab. Janusz Mrozek Rzędy wiązań chemicznych w ujęciu Teorii Komunikacji Plan prezentacji
Seminarium Magisterskie Rzędy wiązań chemicznych w ujęciu Teorii Komunikacji Opracowanie Dariusz Szczepanik Promotor Dr hab. Janusz Mrozek Rzędy wiązań chemicznych w ujęciu Teorii Komunikacji Plan prezentacji
Wiązania jonowe występują w układach złożonych z atomów skrajnie różniących się elektroujemnością.
 105 Elektronowa teoria wiązania chemicznego Cząsteczki powstają w wyniku połączenia się dwóch lub więcej atomów. Już w początkowym okresie rozwoju chemii podejmowano wysiłki zmierzające do wyjaśnienia
105 Elektronowa teoria wiązania chemicznego Cząsteczki powstają w wyniku połączenia się dwóch lub więcej atomów. Już w początkowym okresie rozwoju chemii podejmowano wysiłki zmierzające do wyjaśnienia
Podstawy termodynamiki.
 Podstawy termodynamiki. Termodynamika opisuje ogólne prawa przemian energetycznych w układach makroskopowych. Określa kierunki procesów zachodzących w przyrodzie w sposób samorzutny, jak i stanów końcowych,
Podstawy termodynamiki. Termodynamika opisuje ogólne prawa przemian energetycznych w układach makroskopowych. Określa kierunki procesów zachodzących w przyrodzie w sposób samorzutny, jak i stanów końcowych,
Ćwiczenie 14. Maria Bełtowska-Brzezinska KINETYKA REAKCJI ENZYMATYCZNYCH
 Ćwiczenie 14 aria Bełtowska-Brzezinska KINETYKA REAKCJI ENZYATYCZNYCH Zagadnienia: Podstawowe pojęcia kinetyki chemicznej (szybkość reakcji, reakcje elementarne, rząd reakcji). Równania kinetyczne prostych
Ćwiczenie 14 aria Bełtowska-Brzezinska KINETYKA REAKCJI ENZYATYCZNYCH Zagadnienia: Podstawowe pojęcia kinetyki chemicznej (szybkość reakcji, reakcje elementarne, rząd reakcji). Równania kinetyczne prostych
WIĄZANIA. Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE
 WIĄZANIA Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE Przyciąganie Wynika z elektrostatycznego oddziaływania między elektronami a dodatnimi jądrami atomowymi. Może to być
WIĄZANIA Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE Przyciąganie Wynika z elektrostatycznego oddziaływania między elektronami a dodatnimi jądrami atomowymi. Może to być
Elementy teorii powierzchni metali
 prof. dr hab. Adam Kiejna Elementy teorii powierzchni metali Wykład 4 v.16 Wiązanie metaliczne Wiązanie metaliczne Zajmujemy się tylko metalami dlatego w zasadzie interesuje nas tylko wiązanie metaliczne.
prof. dr hab. Adam Kiejna Elementy teorii powierzchni metali Wykład 4 v.16 Wiązanie metaliczne Wiązanie metaliczne Zajmujemy się tylko metalami dlatego w zasadzie interesuje nas tylko wiązanie metaliczne.
Atomy wieloelektronowe i cząsteczki
 Atomy wieloelektronowe i cząsteczki 1 Atomy wieloelektronowe Wodór ma liczbę atomową Z=1 i jest prostym atomem. Zawiera tylko jeden elektron i jeden proton stąd potencjał opisuje oddziaływanie kulombowskie
Atomy wieloelektronowe i cząsteczki 1 Atomy wieloelektronowe Wodór ma liczbę atomową Z=1 i jest prostym atomem. Zawiera tylko jeden elektron i jeden proton stąd potencjał opisuje oddziaływanie kulombowskie
3. Cząsteczki i wiązania
 20161020 3. Cząsteczki i wiązania Elektrony walencyjne Wiązania jonowe i kowalencyjne Wiązanie typu σ i π Hybrydyzacja Przewidywanie kształtu cząsteczek AX n Orbitale zdelokalizowane Cząsteczki związków
20161020 3. Cząsteczki i wiązania Elektrony walencyjne Wiązania jonowe i kowalencyjne Wiązanie typu σ i π Hybrydyzacja Przewidywanie kształtu cząsteczek AX n Orbitale zdelokalizowane Cząsteczki związków
Ligand to cząsteczka albo jon, który związany jest z jonem albo atomem centralnym.
 138 Poznanie struktury cząsteczek jest niezwykle ważnym przedsięwzięciem w chemii, ponieważ pozwala nam zrozumieć zachowanie się materii, ale także daje podstawy do praktycznego wykorzystania zdobytej
138 Poznanie struktury cząsteczek jest niezwykle ważnym przedsięwzięciem w chemii, ponieważ pozwala nam zrozumieć zachowanie się materii, ale także daje podstawy do praktycznego wykorzystania zdobytej
Elektrostatyka ŁADUNEK. Ładunek elektryczny. Dr PPotera wyklady fizyka dosw st podypl. n p. Cząstka α
 Elektrostatyka ŁADUNEK elektron: -e = -1.610-19 C proton: e = 1.610-19 C neutron: 0 C n p p n Cząstka α Ładunek elektryczny Ładunek jest skwantowany: Jednostką ładunku elektrycznego w układzie SI jest
Elektrostatyka ŁADUNEK elektron: -e = -1.610-19 C proton: e = 1.610-19 C neutron: 0 C n p p n Cząstka α Ładunek elektryczny Ładunek jest skwantowany: Jednostką ładunku elektrycznego w układzie SI jest
WIĄZANIA. Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE
 WIĄZANIA Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE 1 Przyciąganie Wynika z elektrostatycznego oddziaływania między elektronami a dodatnimi jądrami atomowymi. Może to być
WIĄZANIA Co sprawia, że ciała stałe istnieją i są stabilne? PRZYCIĄGANIE ODPYCHANIE 1 Przyciąganie Wynika z elektrostatycznego oddziaływania między elektronami a dodatnimi jądrami atomowymi. Może to być
