Małe RNA i mechanizmy epigenetycznej regulacji ekspresji genów. dr Monika Zakrzewska-Płaczek
|
|
|
- Teodor Grzybowski
- 6 lat temu
- Przeglądów:
Transkrypt
1 Małe RNA i mechanizmy epigenetycznej regulacji ekspresji genów dr Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl
2 Małe RNA (small RNAs, srnas, smrnas) srna nt wyciszanie ekspresji genów: Specyficzność wyciszenia określonych sekwencji zapewniona jest dzięki komplementarności zasad między wyciszającym srna, a RNA ulegającym wyciszeniu (gene silencing, RNA silencing) post-transkrypcyjne (post-transcriptional gene silencing, PTGS) AAAAAAAAAA degradacja mrna, inhibicja translacji transkrypcyjne (transcriptional gene silencing, TGS) epigenetyczne modyfikacje chromatyny Wyciszanie genów za pośrednictwem małych RNA odgrywa istotną rolę zarówno w regulacji ekspresji, ekspresji, jak i w zachowaniu integralności genomów organizmów żywych. Za pośrednictwem sirna wyciszane są m.in. regiony bogatej w powtórzenia DNA heterochromatyny, sekwencje transpozonowe, wirusy i inne patogeny. mirna i tasirna regulują m.in. ekspresję genów związanych z zegarem biologicznym, rozwojem, reakcją na stres. RNAP modyfikacja histonów, metylacja DNA 2
3 Białka Dicer i Argonaute (AGO): główne elementy szlaku wyciszania RNA DICER Dwuniciowy RNA (double-stranded RNA, dsrna) jest cięty przez Dicer na krótkie dwuniciowe cząsteczki RNA, które są wiązane przez jedno z białek rodziny ARGONAUTE. AGO wyciszenie 3
4 Dicer i Dicer-like Podczas biogenezy sirna i mirna, białka Dicer lub Dicer-like (DCL) tną długie dsrna lub RNA o strukturze spinki (hairpin) na fragmenty ~ 21 25nt. PAZ RIII konserwowana domena wiążąca dsrna (dsrbd- dsrna-binding domain) oddziałuje z końcem 3 dsrna 2 domeny typu RNazy III PAZ aktywność endonukleolityczna 5 P / 3 OH RIII Struktura białka Dicer umożliwia równomierne rozcinanie RNA na fragmenty o takiej samej długości. 4 MacRae, I.J., Zhou, K., Li, F., Repic, A., Brooks, A.N., Cande, W.., Adams, P.D., and Doudna, J.A. (2006) Science
5 Argonaute Białka ARGONAUTE wiążą srna i mrna PAZ oddziałuje z końcem 3 srna MID (middle) oddziałuje z nukleotydem na końcu 5 srna PAZ N te rm PIWI MID PIW I struktura podobna do RNazyH w niektórych białkach Ago: cięcie RNA zwiazanego z srna (slicer activity) Nazwa ARGONAUTE pochodzi od mutanta argonaute1 A. thaliana; który swoim kształtem przypomina ośmiornicę żeglarka (Argonauta). A. thaliana ago1 Argonauta argo 5 Bohmert, K., Camus, I., Bellini, C., Bouchez, D., Caboche, M., and Benning, C. (1998) EMBO J. Song, J.-J., Smith, S.K., Hannon, G.J., and Joshua-Tor, L. (2004) Science
6 Wyciszanie ekspresji genów sirna (small interferring RNA) -post-transkrypcyjne lub transkrypcyjne wyciszanie ekspresji genów AGO AAAn DCL AGO AGO RNAP mirna (micro RNA) -inhibicja translacji, cięcie mrna AGO AAAn DCL MIR RNAP AGO AAAn AGO AAAn mrna AAAn RNAP 6
7 PTGS: post-transkrypcyjne wyciszanie genów Klasy małych RNA: mirna (microrna) rośliny, zwierzęta, wirusy, Protista 20 25nt Drosha (u zwierząt) + Dicer Regulacja stabilności mrna (cięcie mrna), inhibicja translacji Transkrypcja przez Pol II/Pol III mirtrony pochodzące z intronów prekursorów mrna genów kodujących białka; występują u zwierząt; niezależne od Drosha sirna (small interferring RNA) większość działa in cis, za wyjątkiem tasirna exo-sirna (pochodzenia egzogennego) endo-sirna (pochodzenia endogennego) tasirna (trans-acting sirna) rośliny, grzyby, zwierzęta, Protista Dicer Transgeniczny, wirusowy lub inny egzogenny RNA Post-transkrypcyjna regulacja ekspresji genów, obrona przeciwwirusowa Post-transkrypcyjna i transkrypcyjna regulacja ekspresji genów, regulacja aktywności transpozonów rośliny, grzyby, zwierzęta, Protista ~21nt Dicer Transkrypcja dwukierunkowa lub zbieżna, wiązanie mrna z transkryptami pseudogenów o przeciwnej orientacji rośliny 21nt DCL4 TAS RNA cięte przez mirna Regulacja posttranskrypcyjna rośliny 24nt 21nt DCL2 DCL1 Transkrypcja dwukierunkowa indukowana stresem Regulacja genów odpowiedzi na stres natsirna (natural antisense transcripts-derived sirna) 21-24nt 7
8 TGS: transkrypcyjne wyciszanie genów Klasy małych RNA: sirna (small interferring RNA) endo-sirna (pochodzenia endogennego) hc-sirna (heterochromatic sirna) pirna (Piwi-interacting RNA) Dicer Transkrypcja dwukierunkowa lub zbieżna, wiązanie mrna z transkryptami pseudogenów o przeciwnej orientacji Post-transkrypcyjna i transkrypcyjna regulacja ekspresji genów, regulacja aktywności transpozonów 24-26nt DCL3 Transpozony, powtórzenia Modyfikacja chromatyny 24 30nt niezależne od Dicer Długie pierwotne transkrypty (?) Wyciszanie transpozonów, inne nieznane funkcje rośliny, grzyby, zwierzęta, Protista ~21nt rośliny, S. pombe Drosophila, C. elegans, ssaki, Danio rerio 8
9 Dicer i Argonaute u różnych organizmów Species Plantae Fungi Metazoa Argonaute-PIWI-like Dicer-like RdRP Argonaute PIWI Arabidopsis thaliana 10 (AGO1-10) - 4 (DCL 1-4) 6 Oryza sativa Saccharomyces cerevisiae Schizosaccharomyces pombe Neurospora crassa Aspergillus nidulans Caenorhabditis elegans (Dicer + Drosha) 4 Drosophila melanogaster (2 Dicers + Drosha) - Danio rerio (Dicer + Drosha) - Homo sapiens (Dicer + Drosha) - 9
10 U roślin w biogenezie mirna i sirna uczestniczą różne białka DCL AtDCL1 mirna DCL1 AtDCL2-4 sirna DCL4 Rośliny mają 4 (i więcej) białek DCL: większa niż u innych organizmów liczba białek DCL umożliwia roślinom bardziej precyzyjną i skuteczną obronę przed patogenami. 10 Margis, R., Fusaro, A.F., Smith, N.A., Curtin, S.J., Watson, J.M., Finnegan, E.J., and Waterhouse, P.M. (2006) FEBS Lett.
11 U roślin w biogenezie mirna i sirna uczestniczą różne białka DCL AtDCL1 mirna DCL1 Arabidopsis thaliana: DCL1 21nt mirna AGO1/7/10 DCL2 22nt sirna DCL3 24nt sirna AGO4/6 DCL4 21nt sirna (tasirna) AGO1 AtDCL2-4 sirna DCL4 11 Bologna N.G., Voinnet O. ( ) Annu. Rev. Plant Biol.
12 microrna u roślin microrna działaja poprzez cięcie mrna lub inhibicję translacji gen MIR AGO Inhibicja translacji cięcie mrna DCL AAAn AGO AGO AAA RNAP II AAAn n RNAP II AAAn mrna mirna są kodowane przez specyficzne geny MIR, ale wpływają na ekspresję innych genów są cząsteczkami regulatorowymi działającymi in trans mirna u roślin (również u zwierząt) regulują procesy rozwojowe i fizjologiczne uważa się, że mirna wyewoluowały z sirna powstają i dojrzewają w podobny (do pewnego stopnia) sposób 12
13 microrna u zwierząt aktywna translacja inhibicja inicjacji translacji degradacja mrna inhibicja translacji 13 Stefani G., Slack F. J., (2008 (2008) Mol Cell Biol
14 microrna - mirna aktywna translacja degradacja mrna 14 Stefani G., Slack F. J., (2008 (2008) Mol Cell Biol
15 Destabilization of target mrna is the predominant reason for reduced protein output. Step 1. Initial effect of mirnas: inhibition of translation at the initiation step without mrna decay. Step 2. mrna deadenylation by PAN2 PAN3 and CCR4 NOT complexes recruited by mirisc as a consequence of translation inhibition that makes poly(a) tail more accessible. Step3. Stimulated deadenylation potentiates the effect on translational inhibition and leads to decay of target mrnas through the recruitment of the decapping 15 machinery.
16 Geny MIR: transkrypcja długich cząsteczek pri-mirna z których powstają mirna MIR gene mirna są kodowane przez geny MIR pierwotne transkrypty mirna (pri-mirna) tworzą drugorzędowe, dwuniciowe struktury, które są rozpoznawane i cięte przez białka Dicer (u roślin DCL1) pri-mirna 5' 3' DCL1 nić mirna* jest degradowana mirna mirna* 5' 3' mirna mrna target 16
17 Biogeneza mirna u roślin DNA transkrypcja pri-mirna HYL1: cięcie oddziaływanie z DCL1 HEN1: mirna mirna* metylacja metylotransferaza, metylacja mirna/mirna* eksport HST (HASTY): eksport mirna/mirna* do cytoplazmy, homolog eksportyny 5 jądro komórkowe cytoplazma tworzenie kompleksu RISC mrna cięcie mrna Mallory A., Vaucheret H. (2006 (2006) Nature Genet. 17
18 Biogeneza mirna DNA u zwierząt transkrypcja pri-mirna Drosha+DGCR8 (Pasha): cięcie cięcie pri-mirna pre-mirna jądro komórkowe pre-mirna eksport EXP5 (eksportyna 5): eksport pre-mirna do cytoplazmy Dicer: cięcie pre-mirna mirna/mirna* cytoplazma pre-mirna cięcie mirna/mirna* tworzenie kompleksu RISC 18 Wg: Ding X.C., Weiler J., Grosshans H. (2009 (2009) Trends in Biotechnology
19 Biogeneza mirna u roślin i zwierząt eksport z jądra komórkowego do cytoplazmy pri-mirna pri-mirna MIRTRONY 19 Carthew R. W., Sontheimer E. J., (2009 (2009) Cell
20 Mirtrony występują u D. melanogaster, C. elegans, ssaków lariat powstaja z intronów wyciętych z pre-mrna podczas składania mrna (splicing) niezależne od Drosha rozcięcie struktury lariatu (debranching) prowadzi do powstania pre-mirna pre-mirna biogeneza mirna 20 Kim V. N., Han J., Siomi M.C. (2009) Mol Cell Biol
21 rodzina mirna rodzina genów regulowanych przez mirna funkcja 156 czynniki transkrypcyjne SPL Synchronizacja procesów rozwojowych 160 czynniki transkrypcyjne ARF Odpowiedź na auksyny, procesy rozwojowe 165 czynniki transkrypcyjne HD-ZIPIII Rozwój, polaryzacja 172 czynniki transkrypcyjne AP2 Synchronizacja procesów rozwojowych, floral organ identity 390 TAS3 (tasirna regulują ekspresję czynników transkrypcyjnych ARF) Odpowiedź na auksyny, procesy rozwojowe 395 Transport siarczanów Asymilacja siarki 399 Ubikwitynacja białek Asymilacja fosforu Factors Factors Blisko połowa spośród genów regulowanych przez mirna to czynniki transkrypcyjne 21 Fahlgren, N., Howell, M.D., Kasschau, K.D., Chapman, E.J., Sullivan, C.M., Cumbie, J.S., Givan, S.A., Law, T.F., Grant, S.R., Dangl, J.L., and Carrington, J.C. (2007) PLoS ONE. Wg Willmann, M.R., and Poethig, R.S. (2007) Curr. Opin. Plant Biol. Przykłady genów regulowanych przez mirna u roślin
22 mirna - podsumowanie Uważa się, że mirna regulują większość procesów biologicznych zarówno u roślin jak i zwierząt, kontrolując ekspresję specyficznych genów działając in trans mirna regulują procesy rozwojowe: np. u A. thaliana mir156 i mir172 regulują procesy kwitnienia; u C. elegans wyciszenie lin-14 przez lin-4 jest potrzebne do prawidłowego rozwoju mirna działają głównie poprzez obniżenie poziomu mrna (cięcie, degradacja), ale również poprzez inhibicję translacji MIR DCL RNAP AGO AAAn AGO AGO AAA n AAAn AAAn RNAP mrna 22
23 sirna ochrona i utrzymywanie stabilności genomu ochrona genomu przed obcym materiałem genetycznym (exo-sirna): transgenicznym wirusowym (VIGS viral induced gene silencing ) endo-sirna: wyciszanie transpozonów i sekwencji powtórzonych utrzymywanie niektórych genów w stanie epigenetycznie nieaktywnym 23 Lam, E., Kato, N., and Lawton, M. (2001) (2001). Nature
24 Exo-siRNA: wyciszanie transgenów Transgeny wprowadzane sztucznie są często wyciszane przez sirna Wyciszenie może być wywołane: bardzo wysokim poziomem ekspresji transgenu dwuniciowym RNA pochodzącym z ekspresji transgenu nieprawidłowymi RNA pochodzącymi z ekspresji transgenu Transgeny są wyciszane post-transkrypcyjnie i transkrypcyjnie AGO AGO AAA n AGO DCL RNA Pol 24
25 Post-transkrypcyjne wyciszanie genów u roślin transgene-induced post-transcriptional silencing Eksperymenty modyfikacji koloru kwiatów petunii (Petunia hybrida) - odkrycie mechanizmu wyciszania genów jądro komórkowe komórka roślinna DNA Agrobacterium tumefaciens na powierzchni komórki roślinnej Martha Hawes, University of Arizona 25
26 Manipulacja ekspresją genu syntazy chalkonowej: zmiana pigmentacji kwiatów petunii CHS Dzikie kwiaty petunii zawierają antocyjaniny nadające purpurową barwę syntaza chalkonowa (CHS) enzym szlaku biosyntezy antocyjanin antocyjaniny 26 Aksamit-Stachurska et al. BMC Biotechnology 2008 Foto: Richard Jorgensen
27 Oczekiwanie synteza RNA o prawidłowej orientacji pogłębi barwę kwiatów... gen PRO ORF mrna translacja mrna transgen konstrukt o orientacji sens mrna dodatkowa translacja mrna mrna 27
28 a a synteza RNA o odwróconej orientacji zablokuje syntezę barwnika gen PRO ORF mrna translacja mrna transgen konstrukt o orientacji sens mrna dodatkowa translacja mrna mrna transgen konstrukt o orientacji antysens RNA antysensowny tworzenie dupleksów RNA sens-antysens inhibicja translacji 28
29 Nieoczekiwanie, wprowadzenie zarówno konstruktów sens jak i antysens prowadzi do inhibicji syntezy barwnika rośliny zawierające transgen CHS CaMV 35S pro : CHS lub CaMV 35S pro : sens antysens CHS 29 Foto: Richard Jorgensen
30 W modyfikowanych roślinach nie dochodzi do syntezy ani endogennej ani transgenicznej CHS purpurowe kwiaty białe kwiaty Zjawisko wyciszania zarówno sztucznie wprowadzonego genu, jak i jego endogennego odpowiednika nazywamy kosupresją transgeniczny RNA endogenny RNA RNase protection 30 Napoli, C., Lemieux, C., and Jorgensen, R. R. (1990) Plant Cell
31 Późniejsze badania wykazały, że kosupresja jest wynikiem produkcji sirna typ dziki PRO gen ORF mrna translacja mrna roślina transgeniczna kosupresja mrna AGO AGO AAAA konstrukt sens PRO gen ORF mrna produkcja sirna AGO AAAA De Paoli, E., Dorantes-Acosta, A., Zhai, J., Accerbi, M., Jeong, D.-H., Park, S., Meyers, B.C., Jorgensen, R.A., and Green, P.J. (2009). RNA 31
32 Exo-siRNA u zwierząt: dsrna najsilniejszy inicjator wyciszania modyfikacje genetyczne nicienia Caenorhabditis elegans: RNA sens bez zmian fenotypowych RNA antysens bez zmian fenotypowych dsrna fenotyp twitching Wprowadzanie do organizmów nicieni C. elegans RNA o prawidłowej lub odwróconej orientacji, oraz dwuniciowych RNA (dsrna), odpowiadających sekwencji genu unc-22, kodującego miofilamentowe białko komórek mięśniowych. Wyciszenie unc-22 powoduje fenotyp kurczenia ciała (twitching) 32 Fire, A. et al., (1998) Nature
33 Exo-siRNA u zwierząt: U ssaków i C. elegans tylko jedno białko Dicer,, odpowiada za biogenezę zarówno sirna, jak i mirna Drosophila melanogaster: Dcr1 mirna Dcr2 sirna, wiązane przez AGO2 obrona przeciwwirusowa egzogenny dsrna wirusowy dsrna cięcie RNA obrona przeciwwirusowa 33 Okamura K. & Lai E.C. (2008) Mol Cell Biol
34 VIGS - viral induced gene silencing mechanizm obrony roślin przed wirusami wirusowa polimeraza RNA zależna od RNA wirusowy ssrna Większość roślinnych wirusów to wirusy RNA, których replikacja odbywa się poprzez dsrna wirusowy dsrna dsrna jest cięty przez DCL4 powstają sirna które wiążą się z AGO1 wyciszenie replikacji wirusa AGO1 AGO1 Wyciszanie ekspresji genów za pośrednictwem sirna jest ważnym mechanizmem obrony roślin przed patogenami wirusami i bakteriami sirna hamują replikację wirusową u roślin (również u zwierząt - Drosophila melanogaster) Większość wirusów wytwarza białka supresorowe, hamujące szlak wyciszania 34
35 VIGS - viral induced gene silencing mechanizm obrony roślin przed wirusami Obrona przeciwwirusowa u roślin: głównie na poziomie wyciszania RNA TRV: 21-nt (DCL4), 24-nt sirna (DCL3) TCV (Turnip Crinkle Virus): 22-nt sirna (DCL2) degradacja wirusowego RNA: 21-nt i 24-nt sirna WT Arabidopsis inokulowany TRV Waterhouse, P.M. and Fusaro, A.F. (2006) Science. Wyciszanie wirusa TRV Tobacco Rattle Virus (wirus nekrotycznej kędzierzawki tytoniu) w roślinach A. thaliana dzikiego typu zapobiega objawom choroby. Mutanty dcl są niezdolne do zahamowania infekcji. Podwójny mutant dcl2-dcl4 inokulowany TRV 35 Mutanty biogenezy sirna są mniej odporne na choroby wirusowe Deleris, A., Gallego-Bartolome, J., Bao, J., Kasschau, K., Carrington, J.C., and Voinnet, O. (2006) Science
36 Infekcja wirusowa powoduje akumulację sirna Małe RNA komplementarne do wirusowego RNA są obecne zarówno w liściach inokulowanych, jak i w młodszych dystalnych liściach (ale nie w liściach kontrolnych) liść liść inokulowany dystalny dni po inokulacji liść inokulowany AGO DCL sirna liść inokulowany Northern blot Hamilton, A.J., and Baulcombe, D.C. (1999) Science 36
37 Efekt wyciszenia jest wzmacniany przez amplifikację sirna RdRP polimeraza RNA zależna od RNA (RNA-dependent RNA Polymerase) DCL RdRP 1-rzędowy sirna Wyciszenie może się rozprzestrzeniać poza miejsce infekcji wirusowej dzięki aktywności RdRP (RNA-dependent RNA polymerase) i biogenezie 2-rzędowych sirna. DCL 2-rzędowy sirna 37
38 Efekt wyciszenia jest wzmacniany przez amplifikację sirna 1 sirna 1 sirna primary Argonaute 2 sirna 2 sirna 38 Ghildiyal & Zamore (2009 (2009) Nat Rev Genet
39 Małe RNA działają ogólnoustrojowo - u roślin mogą rozprzestrzeniać się poprzez wiązki przewodzące wyciszenie inokulowany liść Voinnet, O., and Baulcombe, D. (1997) Nature egzogenne sirna 21 i 24nt (PTGS) wyciszanie transgenu GFP endogenne 24nt sirna (TGS poprzez przebudowę chromatyny, pochodzą z transpozonów i innych zmetylowanych rejonów genomu) Sarkies P., Miska E.A. (2014) Nat. Rev. MCB mirna (PTGS) 39
40 Endo-siRNA: pochodzenie endogenne 40 Ghildiyal & Zamore (2009 (2009) Nat Rev Genet
41 Endo-siRNA u roślin: cis-acting sirna trans-acting sirna natural antisense sirna (casirna, hc-sirna) (tasirna) (natsirna) 41 Ghildiyal & Zamore (2009 (2009) Nat Rev Genet
42 hc-sirna: roślinne endogenne sirna Z biogenezą i funkcją hc-sirna związane są dwie specyficzne dla roślin polimerazy RNA P IV RNA Polimeraza RNA IV uczestniczy w biogenezie sirna P RNA modyfikacja histonów metylacja DNA V Niekodujące transkrypty polimerazy RNA V nakierowują maszynerię wyciszającą do odpowiednich sekwencji DNA => mechanizm metylacji DNA zależnej od RNA (RNA-directed DNA Methylation, RdDM) Ten rodzaj wyciszenia jest często związany ze stale nieaktywnym transkrypcyjnie DNA, włączając rejony centromerowe i transpozony, ale również zachodzi w genach. 42
43 Większość endogennych sirna powstaje z transpozonów i powtórzeń sekwencji DNA Wysoko-przepustowe sekwencjonowanie małych RNA (Arabidopsis thaliana) Chromosom Centromer małe RNA transpoz ranspozony ony retrotranspozony retrotranspozony U Arabidopsis thaliana duże zagęszczenie tego typu sekwencji występuje w rejonach centromerowych chromosomów. 43 Kasschau, K.D., Fahlgren, N., Chapman, E.J., Sullivan, C.M., Cumbie, J.S., Givan, S.A., and Carrington, J.C. (2007) PLoS Biol
44 tasirna: roślinne endogenne sirna gen TAS tasirna trans-acting sirna RNA Pol II transkrypcja locus TAS przez polimerazę RNA II specyficzne dla roślin kodowane przez geny TAS obróbka pierwotnego transkryptu jest inicjowana przez mirna AGO wiązanie przez mirna/risc i cięcie rekrutacja RDR6 RDR6 synteza drugiej nici RNA przez RDR6 (RNA-dependent RNA polymerase) dsrna jest cięty przez DCL4 na serię krótszych dsrna, uwalniając wiele cząsteczek tasirna z jednego genu TAS. 44
45 Z jednego genu TAS powstaje wiele cząsteczek tasirna miejsce cięcia pierwotnego transkryptu przy udziale mirna kluczowe dla zapewnienia specyficzności tasirna; DCL4 zaczyna ciąć prekursor dokładnie w tym miejscu i tnie w odstępach 21nt tasirna mogą powstawać z obu nici RNA DCL4 przesuwa się wzdłuż dsrna, odmierzając i tnąc 45 Allen, E., Xie, Z., Gustafson, A M., and Carrington, J.C. (2005) Cell
46 Zaburzenia biogenezy tasirna zaburzenia rozwoju mutacja rdr6-15: brak tasirna Arabidopsis 4 rodziny genów TAS TAS1 i TAS2 tasirna PPR TAS3 tasirna czynniki transkrypcyjne ARF zip-1 (AGO7): brak TAS3 tasirna TAS4 tasirnas czynniki transkrypcyjne MYB Mutacje rdr6 i zip, podobnie jak dcl4 i tas3, przyspieszają zmiany rozwojowe Northern przyspieszone przejście z fazy juwenilnej do dorosłej: wydłużone liście, wywinięte pod spód brzegi blaszek liściowych 46 Fahlgren, N., Montgomery, T.A., Howell, M.D., Allen, E., Dvorak, S.K., Alexander, A.L., and Carrington, J.C. (2006) Curr. Biol.
47 natsirna: roślinne endogenne sirna natsirna natural antisense-transcript derived sirna cis-acting syntetyzowane w odpowiedzi na stres np. wysokie zasolenie gleby zachodzące na siebie sekwencje sąsiadujących genów (związanych z odpowiedzią na stres) A. thaliana: thaliana: lsirna (long (long sirna; 30-40nt) 30-40nt) również powstają z transkryptów NAT, inne białka uczestniczą w biogenezie komplementarne względem siebie transkrypty NAT (natural antisense) tworzą dsrna AGO wyciszenie AGO biogeneza: DCL2 i/lub DCL1 RDR6 (polimeraza (polimeraza RNA zależna od RNA) RNA) SGS3 (białko wiążące RNA) RNA) i polimeraza RNA IV 47 Wg Katiyar-Agarwal, S., Morgan, R., Dahlbeck, D., Borsani, O., Villegas Jr. A., Zhu, J.-K., Staskawicz, B.J., and Jin, H. (2006) Proc. Natl. Acad. Sci. USA
48 Małe RNA niezależne od Dicer: pirna ~25-30 nt, 2 -O-metylowane końce 3 występują u zwierząt, zidentyfikowane w liniach komórek rozrodczych D. melanogaster wiążą się z białkami PIWI: Piwi, Aubergine, Ago3 D. melanogaster MILI, MIWI, MIWI2 mysie HILI, HIWI1, HIWI2 ludzkie C. elegans 21U RNA 21 nt wiąże PRG-1 (Piwi-related gene 1) metylacja końca 3 wyciszanie transpozonów i powtórzeń DNA; uważa się, że mogą działać na różnych poziomach: posttranskrypcyjnie degradacja transkryptu u ssaków metylacja DNA sekwencji transpozonowych 48 Ghildiyal & Zamore (2009 (2009) Nat Rev Genet
49 Małe RNA niezależne od Dicer: prirna prirna primal small RNAs zidentyfikowane u S.pombe tworzenie/utrzymywanie heterochromatyny w rejonach centromerowych Triman: 3-5 egzorybonukleaza obróbka prekursorów prirna i sirna 49
50 sirna - podsumowanie Szlak sirna wycisza egzogenny, obcy DNA, transpozony oraz sekwencje powtórzone sirna powstają dzięki aktywności białek typu Dicer, które tną dsrna sirna są wiązane przez białka z rodziny AGO i tworzą kompleksy wyciszające (RISC) Kompleksy wyciszające mogą działać posttranskrypcyjnie, poprzez cięcie mrna lub inhibicję translacji Kompleksy wyciszające mogą zmieniać strukturę chromatyny poprzez metylację DNA lub modyfikację białek histonowych transkrypcyjne wyciszanie ekspresji AGO AGO AAA n AGO DCL RNA Pol 50
51 Transkrypcyjne wyciszanie genów (TGS) małe RNA mogą hamować transkrypcję określonych genów (wyciszać DNA) za pośrednictwem enzymów metylujących cytozyny w DNA lub modyfikujących białka histonowe NH2 N O AGO NH2 N N ~ O CH3 transkrypcja N metylotransferaza DNA ~ białka histonowe wyciszenie DNA przebudowa chromatyny modyfikacja metylacja DNA histonów EPIGENETYCZNA REGULACJA EKSPRESJI GENÓW 51
52 Co oznacza epigenetyczna? Epigenetyczna regulacja ekspresji genów = zmiana ekspresji genu, która zachodzi bez zmiany sekwencji DNA Dosłownie, słowo epigenetyka oznacza powyżej genetyki Jest to informacja pozagenowa, nie dotycząca samej sekwencji, ale kowalencyjnych modyfikacji DNA i zmian struktury chromatyny Różne epigenetyczne modyfikacje prowadzą do różnych wzorów ekspresji genów komórki (organizmy) identyczne genetycznie różne fenotypy W praktyce, epigenetyka opisuje zjawiska, dzięki którym w identycznych genetycznie komórkach lub organizmach dochodzi do różnego sposobu ekspresji genów czego efektem są różnice fenotypowe. 52
53 Struktura chromatyny ~147 bp DNA jest owinięty wokół oktameru białek histonowych:: 2x struktury 3 (oddziaływania między włóknami chromatyny) H2A H2B H3 H4 + 50bp DNA łącznikowego + histon H1 struktury 2 maksymalnie upakowane (np. włókno 30nm) H4 struktury 2 H2A nukleosomy H3 H2B DNA 53 Caterino & Hayes (2007) Nature
54 Struktura chromatyny W mitozie cały DNA występuje jako heterochromatyna heterochromatyna konstytutywna stale obecna w komórce, nie zawiera genów (obszary centromerów i telomerów) fakultatywna CENTROMER pojawia się w jądrze okresowo i tylko w niektórych komórkach, prawdopodobnie zawiera geny nieaktywne w czasie niektórych faz cyklu komórkowego euchromatyna luźno upakowana forma chromatyny, zawierająca geny aktywne transkrypcyjnie 54
55 Epigenetyczne mechanizmy regulacji ekspresji genów metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature 55
56 Metylacja DNA metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature Rola metylacji DNA imprinting, inaktywacja chromosomu X, rozwój embrionalny, represja sekwencji powtórzonych i transpozonów 56
57 Metylacja DNA NH2 N O m N ylo et tra a az r fe ns NH2 N O ~ cytozyna CH3 DNA może być kowalencyjnie modyfikowany w reakcji metylacji cytozyny u ssaków i roślin, ale nie u niższych zwierząt czy drożdży N ~ 5-metylocytozyna 5-metylocytozyna TTCGCCGACTAA metylotransferaza DNA 1 5'-CG-3 5'-CG-3 i 5 -CNG-3 wyciszanie transpozonów, powtórzeń DNA, piętnowanie niektórych genów de novo: 5'-CHG-3' (H= A, C lub T) specyficzna dla roślin, może być rekrutowana przez metylotransferazę histonową SUVH4 (KYP), a więc odpowiadać na modyfikację białek histonowych metylotransferaza DNA 3A metylotransferaza DNA 3B 5'-CHH-3' metylacja powtórzeń DNA wyciszanych przez sirna 57
58 Metylacja CG (symetryczna)) może być przenoszona podczas replikacji DNA 5 A T G C G T A C T REPLI REPLIKACJA KACJA A T G C G T A C T T A C G C A T G A MET1 A T G C G T A C T T A C G C A T G A 3 T A C G C A T G A A T G C G T A C T METYLACJA ZACHOWAWCZA A T G C G T A C T T A C G C A T G A T A C G C A T G A 58
59 Asymetryczne miejsca metylacji: CHH (H= A, C lub T) 5 A T G C A A A C T REPLI REPLIKACJA KACJA A T G C A A A C T T A C G T T T G A 3 T A C G T T T G A A T G C A A A C T T A C G T T T G A } konieczna konieczna jest dodatkowa informacja do ponownej metylacji DNA 59
60 5 A T G C A A A C T RE PL IK AC JA Asymetryczne miejsca metylacji: CHH (H= A, C lub T) A T G C A A A C T T A C G T T T G A 3 T A C G T T T G A A T G C A A A C T A T G C A A A C T T A C G T T T G A T A C G T T T G A sirna DRM2 Metylacje w miejscach asymetrycznych są utrzymywane (i inicjowane) dzięki informacji zawartej w odpowiednich modyfikacjach białek histonowych, na drodze mechanizmu metylacji DNA zależnej od RNA (RNA-directed DNA Methylation, RdDM) 60
61 Model mechanizmu metylacji DNA zależnej od RNA (RdDM- RNA-directed DNA methylation) chromatin remodelling GW/WG chromatin remodelling DDR elongation factor dsrna-binding protein 61
62 Głównym celem metylacji cytozyn jest wyciszenie transpozonów i powtórzeń DNA Nie wszystkie transpozony są wyciszane na drodze mechanizmu RNAi GENY A. thaliana TRANSPOZONY demetylaza H3K9 KYP (SUVH4) H3K9 metylotransferaza DDM1 ATPaza z rodziny SNF2; przebudowa chromatyny Do zmetylowanego DNA przyłączają się białka z domeną MBD (methyl-cpg binding domain), do których z kolei wiąże się kompleks deacetylazy histonowej, co prowadzi do kondensacji chromatyny i represji ekspresji genów; mogą się również przyłączać metylotransferazy histonowe 62 Texeira & Colot (2009 (2009) EMBO J.
63 Epigenetyczne programowanie pomaga kontrolować zmiany faz rozwojowych u roślin zmiana fazy rozwojowej zmiana fazy rozwojowej rozwój zarodkowy rozwój wegetatywny rozwój generatywny Ekspresja FLC jest regulowana przez RdDM regulacja ekspresji FLC: antysensowny RNA komplementarny do rejonu 3 genu FLC transkrypcja antysens z 3 UTR prawdopodobnie przez polimerazę RNA IV regulacja ekspresji FLC: wymaga obecności DCL3, RDR2 i polimerazy RNA IV, transkrypcja przez polimerazę IV substrat dla DCL3 do produkcji sirna, które rekrutują kompleksy modyfikujące histony wyciszenie ekspresji genu FLC 63
64 Potranslacyjne modyfikacje białek histonowych metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature Końce N białek histonowych (tzw. ogony histonowe) wystają poza nukleosom, są dostępne dla enzymów modyfikujących 64
65 Modyfikacje białek histonowych ludzkich i drożdżowych (*) 65 Latham J. A., Dent S. Y. R. (2007) Nat. Struct. Mol. Biol.
66 Modyfikacje białek histonowych wpływają na zmiany struktury chromatyny W zależności od miejsca modyfikacje mogą przyczyniać się do aktywacji lub inaktywacji transkrypcji S/T kinazy fosfatazy acetylotransferazy histonowe (HAT) K K/R deacetylazy histonowe (HDAC) metylotransferazy demetylazy -P S/T -COCH3 K -CH3 K/R fosforylacja acetylacja metylacja 66
67 Acetylacja lizyny białek histonowych seria acetylo-lizyn (bardziej obojętne niż dodatnio naładowane lizyny) na ogonach histonów osłabia interakcje elektrostatyczne miedzy histonami a DNA, co pozwala na rozluźnienie struktury chromatyny inne funkcje: regulacja naprawy DNA poprzez przebudowę chromatyny; acetylowane lizyny są wtedy miejscami przyłączenia dla białek przebudowujących chromatynę (poprzez bromodomenę) + NH3 lizyna (K) N O CH3 acetylowana lizyna (KAc) za acetylację odpowiedzialne sa acetylotransferazy (HAT), a donorem grupy acetylowej jest acetylo-coa acetylacja jest odwracalna; deacetylację przeprowadzaja deacetylazy (HDAC) K acetylotransferazy histonowe (HAT) deacetylazy histonowe (HDAC) 67 -COCH3 K
68 Metylacja białek histonowych metylacja lizyny powoduje zwiekszenie hydrofobowego i kationowego charakteru tej reszty aminokwasowej; w zależnosci od enzymu lizyna może byc mono, di lub trimetylowana. metylowana lizyna Mono (Kme1) Di (Kme2) + NH2 + NH CH3 CH3 CH3 za metylację odpowiedzialne są metylotransferazy (HMT) zawierające domenę SET, a donorem grupy metylowej jest S-adenozylometionina (SAM) lub S- adenozylohomocysteina (AdoHcy); metylacja H3K79 katalizowana jest przez Dot1 spoza rodziny Set Tri (Kme3) + N CH3 CH3 CH3 usuniecie grup metylowych: wymiana nukleosomów, modyfikacje chemiczne zmetylowanych reszt lub enzymatyczna demetylacja K/R metylotransferazy demetylazy -CH3 K/R 68
69 Fosforylacja białek histonowych Fosforylacje seryn H3S10 i H3S28 niezbedne są do kondensacji chromosomów i prawidłowej mitozy; także pozytywna rola w aktywacji transkrypcji: hamuje metylację H3K9 i promuje acetylację lizyn położonych w jej sąsiedztwie Zidentyfikowano ufosforylowane seryny na wszystkich histonach (fosforylacja wariantu H2A niezbedna jest w aktywacji naprawy DNA i regulacji cyklu komórkowego po uszkodzeniu DNA) S/T kinazy fosfatazy 69 -P S/T
70 Przykład modyfikacje H3 Me Me P Ac Me Ac Ac Me Me P H3 A R T K Q T A R K S T G G K A P R K Q L A T K A A R K S Koniec N histonu H3 jest często modyfikowany (w jednym lub kilku miejscach), co przyczynia się do aktywacji lub inhibicji transkrypcji. Modyfikacje białek histonowych zmieniają strukturę chromatyny H3 Me P Ac K4 S10 K14 H3 Me K9 Me P K27 S28 70
71 Mechanizm działania modyfikacji potranslacyjnych białek histonowych Działanie bezpośrednie: zmiany w oddziaływaniach histon-dna i histon-histon Działanie pośrednie: rekrutacja białek rozpoznających określone modyfikacje histonów Kozaurides
72 Inne modyfikacje białek histonowych występują w sekwencjach genów kodujących białka, inne w sekwencjach transpozonowych Analiza typu ChIP-chip gen mrna H3K4me metylacja H3K4 występuje w genach aktywnie transkrybowanych H3K9me Me-C transpozon metylacja H3K9 jest związana z metylowanym DNA (Me-C) i transpozonami czerwony czerwony == silna silna korelacja korelacja zielony = słaba korelacja zielony = słaba korelacja 72 Lippman, Z., Gendrel, A.-V., Black, M., Vaughn, M.W., Dedhia, N., McCombie, W.R., Lavine, K., Mittal, V., May, B., Kasschau, K.D., Carrington, J.C.,Doerge, R.W., Colot, V., Martienssen, R. (2004) Nature
73 Rozmieszczenie modyfikacji histonów w genach aktywnych i nieaktywnych transkrypcyjnie Domena CTD transkrybującej RNAPII może oddziaływać z czynnikami modyfikującymi histony, np. SET2, który metyluje H3K36 Nukleosomy w promotorach aktywnie transkrybowanych genów posiadają modyfikacje aktywujące tj. acetylacje i metylacje H3K4; w miejscu startu transkrypcji znajduje się region NDR (nucleosome depleted region) Modyfikacje aktywujące tj. H3K79 rozmieszczone są wzdłuż aktywnego transkrypcyjnie genu W genach nieaktywnych znajdują się modyfikacje wyciszające, tj. metylacja H3K9 i H4K20, podczas gdy metylacja H3K27 jest obecna w promotorze. Takie modyfikacje są rozpoznawane przez kompleksy przebudowujące chromatynę (PRC1, HP1) tworzenie heterochromatyny. 73 Barth T. K., Imhof A. (2010) Trends in Biochemical Science
74 H3K27me3: w genach kodujących białka Analiza typu ChIP-chip niebieski = geny czerwony = powtórzenia DNA H3K27me3 u A. thaliana występuje w rejonach bogatych w sekwencje kodujące zielony = H3K27me3 fioletowy = metylocytozyna 74 Zhang, X., Clarenz, O., Cokus, S., Bernatavichute, Y.V., Pellegrini, M., Goodrich, J., Jacobsen, S.E. (2007) PLoS Biol.
75 Metylacja H3K27me3: kompleks PRC2 (Polycomb Repressive Complex 2) Polycomb Repressive Complex 2 H3K27me3 geny aktywne geny wyciszone 75 Simon J. A., Kingston R. E Mol Cell
76 Białka rdzenia kompleksu PRC2 u Arabidopsis Drosophila PRC2 E(Z) (methylase) ESC SU(Z)12 NURF55 Arabidopsis PRC2 CURLY LEAF (CLF) MEDEA (MEA) SWINGER (SWN) FERTILIZATION INDEPENDENT ENDOSPERM (FIE) FERTILIZATION-INDEPENDENT SEED 2 (FIS2) EMBRYONIC FLOWER 2 (EMF2) VERNALIZATION 2 (VRN2) MULTICOPY SUPPRESSOR OF IRA1 (MSI1,2,3,4,5) U roślin: różne kompleksy PRC2 odgrywają różne role MEA + FIS2 kiełkowanie CLF/SWN + VRN2 indukcja kwitnienia CLF/SWN + EMF2 rozwój kwiatów 76
77 Metylacja H3K27me3 u zwierząt jest utrzymywana przez PRC1 Polycomb Repressive Complex 2 Polycomb Repressive Complex 1 H3K27me3 H3K27me3 geny aktywne geny wyciszone geny stabilnie wyciszone 77 Simon J. A., Kingston R. E Mol Cell
78 PRC1-like u roślin działa podobnie Polycomb Repressive Complex 2 PRC1 - like LHP1 wiąże specyficznie H3K27me3 H3K27me3 LHP1 H3K27me3 geny aktywne geny wyciszone geny stabilnie wyciszone 78
79 LHP1 występuje razem z metylacją H3K27me3 Analiza typu ChIP-chip silna silna korelacja korelacja występowania występowania LHP1 LHP1 ii H3K27me3 H3K27me3 79 Turck F, Roudier F, Farrona S, Martin-Magniette M-L, Guillaume E, et al PLoS Genet
80 LHP1 występuje razem z metylacją H3K27me3 Analiza typu ChIP-chip transpo transpozon zon metylowany metylowany H3K9me2! H3K9me2! 80 Turck F, Roudier F, Farrona S, Martin-Magniette M-L, Guillaume E, et al PLoS Genet
81 Przebudowa chromatyny zależna od ATP (chromatin remodelling) metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature Aktywność kompleksów przebudowujących chromatynę zależy od ATP, w wyniku ich działania zmienia się sposób oddziaływania histon-dna. Kompleksy remodelujące zaangażowane są zarówno w aktywację, jak i represję transkrypcji. 81
82 Przebudowa chromatyny: przesunięcie oktameru histonowego usunięcie oktameru histonowego odsłonięcie DNA rozwinięcie nici DNA zamiana dimeru H2A-H2B na H2A.Z-H2B (Htz1 u S. cerevisiae) usunięcie dimerów H2A-H2B zmiana składu oktameru histonowego 82 Clapier C. R., Cairns B. R Annu Rev Biochem
83 Wyróżniamy cztery rodziny kompleksów odpowiedzialnych za przebudowę chromatyny: SWI2: zawieraja bromodomenę, wszystkie rodzaje przebudowy chromatyny ISWI: przesuwanie nukleosomów CHD: zawieraja chromodomene, regulacja transkrypcji INO80/SWR: wymiana histonów 83 Clapier C. R., Cairns B. R Annu Rev Biochem
84 Kompleksy przebudowujące chromatynę składają się z wielu białkowych podjednostek Drożdżowy SWI/SNF: 11 białek potrzebny do ekspresji genów decydujących o typie koniugacyjnym drożdży (switching) switching), oraz ekspresji genów regulujących metabolizm sacharozy (sucrose non-fermenting) non-fermenting) 84
85 DDM1 (decrease in DNA methylation1) : ATPaza z rodziny SWI/SNF u A. thaliana DDM1 jest specyficznie zaangażowana w metylację transpozonów GENY A. thaliana TRANSPOZONY demetylacja H3K9 KYP (SUVH4) H3K9 metylotransferaza DDM1 ATPaza z rodziny SNF2; remodeling chromatyny DDM1 jest kluczowym czynnikiem łączącym przebudowę chromatyny i wprowadzanie/utrzymywanie metylacji DNA 85 Texeira & Colot (2009 (2009) EMBO J.
86 Warianty histonów metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature Za wymianę różnych wariantów histonów w oktamerze histonowym odpowiadają kompleksy przebudowujące chromatynę z rodziny INO80/SWR 86
87 Warianty histonów: X-inactivation 87 Talbert & Henikoff (20 10) Nat Rev Mol Cell Biol (2010)
88 Histon H2A.Z: aktywacja transkrypcji gen nieaktywny gen aktywny kompleks SWR1/ SRCAP H2A.Z H2A Obecność odmiany histonu H2 - H2A.Z sprzyja transkrypcji. Kompleks SWR1/SRCAP zamienia histon H2A na H2A.Z 88
89 Histon CENH3: : centromery CENH3 H3 nukleosomy w centromerach zawierają wariant histonu H3: CENH3 (CENP-A u zwierząt) centromery zawierające CENH3 są otoczone obszarem bogatym w metylacje H3K9me2 (heterochromatyna przycentromerowa) 89 Jiang, J., Birchler, J.A., Parrott, W.A., and Dawe, R.K. (2003) Trends Plant Sci. Elsevier. Zhang, W., Lee, H.-R., Koo, D.-H., and Jiang, J. (2008) Plant Cell
90 Epigenetyczna regulacja ekspresji genów przez ncrna metylacja DNA potranslacyjne modyfikacje histonów przebudowa chromatyny zależna od ATP warianty histonów ncrna histony chromatyna DNA Dulac C. (2010 (2010)) Nature RNA jest jedynym jak dotąd poznanym czynnikiem inicjującym dziedziczenie epigenetyczne i odróżniającym sekwencje, które mają zostać wyciszone lub aktywowane 1. wyciszanie transkrypcyjne przez sirna (TGS) 2. regulacja ekspresji przez długie niekodujące RNA (lncrna) 90
91 Epigenetyczna regulacja ekspresji genów przez lncrna u ssaków niektóre niektóre lncrna lncrna (transkrypty (transkrypty polimerazy polimerazy RNA RNA II) II) rekrutują rekrutują kompleksy kompleksy wyciszające wyciszające transkrypcję transkrypcję do do odpowiednich odpowiednich rejonów rejonów genomu, genomu, zarówno zarówno in in cis cis,, jak jak in in trans trans PcG- Polycomb group proteins G9a- metylotransferazy histonowe /H3K9/H3K27 XIST inaktywacja chromosomu X u ssaków (dosage compensation: wyrównanie poziomu ekspresji genów chromosomów X) 91 Chen & Carmichael (20 10) Wiley Interdisciplinary Reviews: RNA (2010)
92 Inaktywacja chromosomu X: wyciszanie epigenetyczne X X XX X X X X W każdej komórce ssaków płci żeńskiej, jedna kopia chromosomu X jest inaktywowana epigenetycznie. dosage compensation: wyrównanie poziomu ekspresji genów chromosomów X X X X X X X X X X X X X X X X X X X X X X X Kolor futra u kotów jest częściowo determinowany przez gen orange, zlokalizowany na chromosomie X. Heterozygotyczna kotka posiada mozaikowe zabarwienie futra: zależnie od chromosomu X podlegającego inaktywacji, w melanocytach dochodzi do ekspresji określonej formy melaniny: eumelanina czarno-brązowa feomelanina żółto-czerwona Photo credit: DrL 92
93 Inaktywacja chromosomu X: wyciszanie epigenetyczne Mus musculus: u samic od wczesnego etapu rozwoju zarodkowego na aktywnym chromosomie X ekspresja Tsix, na nieaktywnym ekspresja Xist i RepA John E. Froberg, Lin Yang, Jeannie T. Lee (2013) Journal of Molecular Biology 17kb (u myszy; ludzki 19kb) ncrna XIST opłaszcza chromosom X RepA 1,6kb ncrna zawierający sekwencje rejonu 5 transkryptu XIST bezpośrednio wiąże kompleks PRC2 tzw. ciałko Barra: skondensowana forma chromosomu X, głównie w postaci heterochromatyny 93
94 Inaktywacja chromosomu X: wyciszanie epigenetyczne XIST ncrna uruchamia zmiany epigenetyczne, które zapewniają pamięć komórkową stanu nieaktywnego: zamiana histonu H2A na makroh2a metylacja histonu H3: H3K9 H3K27 deacetylacja histonu H4 (?) metylacja DNA /już po inaktywacji chromosomu 94 Ferrari F., Alekseyenko A.A., Park P.J., Kuroda M.I. (2013) Nat. Struct. Mol. Biol.
95 Epigenetyczna regulacja ekspresji genów przez ncrna kompensacja dawki chromosomów płciowych (dosage compensation) u Drosophila melanogaster rox rox1/rox2 ncrna inicjują modyfikacje histonów u samców Drosophila zwiększenie aktywności chromosomu X acetylacja histonów demetylacja H3K9 95 Ferrari F., Alekseyenko A.A., Park P.J., Kuroda M.I. (2013) Nat. Struct. Mol. Biol.
96 96
Świat małych RNA. Monika Zakrzewska-Płaczek
 Świat małych RNA Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne wyciszanie genów
Świat małych RNA Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne wyciszanie genów
Endo-siRNA: 32 Ghildiyal & Zamore (2009) Nat Rev Genet
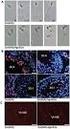 Endo-siRNA sirna: 32 Ghildiyal & Zamore (2009) Nat Rev Genet Większość endogennych sirna powstaje z transpozonów i powtórzeń sekwencji DNA Chromosom Centromer małe RNA transpozony retrotranspozony Wysoko-przepustowe
Endo-siRNA sirna: 32 Ghildiyal & Zamore (2009) Nat Rev Genet Większość endogennych sirna powstaje z transpozonów i powtórzeń sekwencji DNA Chromosom Centromer małe RNA transpozony retrotranspozony Wysoko-przepustowe
Rola chromatyny w regulacji ekspresji genów. Monika Zakrzewska-Płaczek
 Rola chromatyny w regulacji ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Co oznacza epigenetyka? Epigenetyczna regulacja ekspresji genów = zmiana ekspresji genu, która zachodzi bez zmiany
Rola chromatyny w regulacji ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Co oznacza epigenetyka? Epigenetyczna regulacja ekspresji genów = zmiana ekspresji genu, która zachodzi bez zmiany
Rola chromatyny w regulacji ekspresji genów. Monika Zakrzewska-Płaczek
 Rola chromatyny w regulacji ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Epigenetyczna etyczna regulacja ekspresji genów zmiana ekspresji genu, która zachodzi bez zmiany sekwencji DNA
Rola chromatyny w regulacji ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Epigenetyczna etyczna regulacja ekspresji genów zmiana ekspresji genu, która zachodzi bez zmiany sekwencji DNA
Małe RNA.
 Małe RNA Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne wyciszanie genów (post-transcriptional
Małe RNA Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne wyciszanie genów (post-transcriptional
Małe RNA i epigenetyczna regulacja ekspresji genów
 Małe RNA i epigenetyczna regulacja ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne
Małe RNA i epigenetyczna regulacja ekspresji genów Monika Zakrzewska-Płaczek monika.z@ibb.waw.pl Małe RNA (small RNAs, srnas) srna 21-30 nt wyciszanie ekspresji genów: (gene silencing, RNA silencing) post-transkrypcyjne
TRANSLACJA II etap ekspresji genów
 TRANSLACJA II etap ekspresji genów Tłumaczenie informacji genetycznej zawartej w mrna (po transkrypcji z DNA) na aminokwasy budujące konkretne białko. trna Operon (wg. Jacob i Monod) Zgrupowane w jednym
TRANSLACJA II etap ekspresji genów Tłumaczenie informacji genetycznej zawartej w mrna (po transkrypcji z DNA) na aminokwasy budujące konkretne białko. trna Operon (wg. Jacob i Monod) Zgrupowane w jednym
Wykład 3. Organizacja jądra komórkowego struktura chromatyny
 Wykład 3 Organizacja jądra komórkowego struktura chromatyny Struktura jądra komórkowego Matriks jądrowa - jądro komórkowe pozbawione chromatyny Nukleoplazma Heterochromatyna Euchromatyna Jąderko Otoczka
Wykład 3 Organizacja jądra komórkowego struktura chromatyny Struktura jądra komórkowego Matriks jądrowa - jądro komórkowe pozbawione chromatyny Nukleoplazma Heterochromatyna Euchromatyna Jąderko Otoczka
Wykład 5. Remodeling chromatyny
 Wykład 5 Remodeling chromatyny 1 Plan wykładu: 1. Przebudowa chromatyny 2. Struktura, funkcje oraz mechanizm działania kompleksów remodelujących chromatynę 3. Charakterystyka kompleksów typu SWI/SNF 4.
Wykład 5 Remodeling chromatyny 1 Plan wykładu: 1. Przebudowa chromatyny 2. Struktura, funkcje oraz mechanizm działania kompleksów remodelujących chromatynę 3. Charakterystyka kompleksów typu SWI/SNF 4.
INICJACJA ELONGACJA TERMINACJA
 INICJACJA ELONGACJA TERMINACJA 2007 by National Academy of Sciences Kornberg R D PNAS 2007;104:12955-12961 Struktura chromatyny pozwala na różny sposób odczytania informacji zawartej w DNA. Możliwe staje
INICJACJA ELONGACJA TERMINACJA 2007 by National Academy of Sciences Kornberg R D PNAS 2007;104:12955-12961 Struktura chromatyny pozwala na różny sposób odczytania informacji zawartej w DNA. Możliwe staje
wykład dla studentów II roku biotechnologii Andrzej Wierzbicki
 Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ 1. Gen to odcinek DNA odpowiedzialny
Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ 1. Gen to odcinek DNA odpowiedzialny
Mechanizmy kontroli rozwoju roślin. Rafał Archacki
 Mechanizmy kontroli rozwoju roślin Rafał Archacki Drzewo życia pozycja roślin i zwierząt http://5e.plantphys.net/article.php?ch=t&id=399 Ewolucja roślin ewolucja procesu rozmnażania i rozwoju http://5e.plantphys.net/article.php?ch=t&id=399
Mechanizmy kontroli rozwoju roślin Rafał Archacki Drzewo życia pozycja roślin i zwierząt http://5e.plantphys.net/article.php?ch=t&id=399 Ewolucja roślin ewolucja procesu rozmnażania i rozwoju http://5e.plantphys.net/article.php?ch=t&id=399
Epigenetyczna regulacja ekspresji genów w trakcie rozwoju zwierząt i roślin
 Epigenetyczna regulacja ekspresji genów w trakcie rozwoju zwierząt i roślin Rozwój jest z natury epigenetyczny te same geny w różnych tkankach i komórkach utrzymywane są w stanie aktywnym lub wyciszonym
Epigenetyczna regulacja ekspresji genów w trakcie rozwoju zwierząt i roślin Rozwój jest z natury epigenetyczny te same geny w różnych tkankach i komórkach utrzymywane są w stanie aktywnym lub wyciszonym
Dr. habil. Anna Salek International Bio-Consulting 1 Germany
 1 2 3 Drożdże są najprostszymi Eukariontami 4 Eucaryota Procaryota 5 6 Informacja genetyczna dla każdej komórki drożdży jest identyczna A zatem każda komórka koduje w DNA wszystkie swoje substancje 7 Przy
1 2 3 Drożdże są najprostszymi Eukariontami 4 Eucaryota Procaryota 5 6 Informacja genetyczna dla każdej komórki drożdży jest identyczna A zatem każda komórka koduje w DNA wszystkie swoje substancje 7 Przy
ODKRYCIE POLIMERAZY RNA IV
 ODKRYCIE POLIMERAZY RNA IV Ewa Róg-ZieliR Zielińska POLIMERAZY RNA U eukariota występuj pują trzy podstawowe rodzaje polimeraz RNA zależnych od DNA Wszystkie te polimerazy są złożone one z około o 12-17
ODKRYCIE POLIMERAZY RNA IV Ewa Róg-ZieliR Zielińska POLIMERAZY RNA U eukariota występuj pują trzy podstawowe rodzaje polimeraz RNA zależnych od DNA Wszystkie te polimerazy są złożone one z około o 12-17
Badanie funkcji genu
 Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
Chromatyna struktura i funkcja
 Chromatyna struktura i funkcja dr hab. Marta Koblowska dr Rafał Archacki http://www.accessexcellence.org/ab/gg/nucleosome.html GENETYKA FRIEDRICH MIESCHER (1844-1895) W 1869 roku wyizolował z jąder komórkowych
Chromatyna struktura i funkcja dr hab. Marta Koblowska dr Rafał Archacki http://www.accessexcellence.org/ab/gg/nucleosome.html GENETYKA FRIEDRICH MIESCHER (1844-1895) W 1869 roku wyizolował z jąder komórkowych
Arabidopsis thaliana jako organizm modelowy
 Arabidopsis thaliana jako organizm modelowy Arabidopsis thaliana mały jednoroczny chwast z rodziny Brassicaceae (krzyżowe) odkryty w XVI w przez Johannesa Thala thaliana w 1873 zidentyfikowano pierwszego
Arabidopsis thaliana jako organizm modelowy Arabidopsis thaliana mały jednoroczny chwast z rodziny Brassicaceae (krzyżowe) odkryty w XVI w przez Johannesa Thala thaliana w 1873 zidentyfikowano pierwszego
Badanie funkcji genu
 Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
Regulacja ekspresji genów. Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego.
 Regulacja ekspresji genów Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego. Problem: jak sprawić aby z jednej komórki powstał wielokomórkowy
Regulacja ekspresji genów Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego. Problem: jak sprawić aby z jednej komórki powstał wielokomórkowy
Budowa histonów rdzeniowych
 Histony rdzeniowe Budowa histonów rdzeniowych Histon H4 Silnie dodatnio naładowany N-koniec białka Globularna hydrofobowa domena odpowiedzialna za oddziaływania histon-histon oraz histon-dna Domena histonowa
Histony rdzeniowe Budowa histonów rdzeniowych Histon H4 Silnie dodatnio naładowany N-koniec białka Globularna hydrofobowa domena odpowiedzialna za oddziaływania histon-histon oraz histon-dna Domena histonowa
Komórka eukariotyczna
 Komórka eukariotyczna http://pl.wikipedia.org/w/index.php?title=plik:hela_cells_stained_with_hoechst_33258.jpg cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii,
Komórka eukariotyczna http://pl.wikipedia.org/w/index.php?title=plik:hela_cells_stained_with_hoechst_33258.jpg cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii,
wykład dla studentów II roku biotechnologii Andrzej Wierzbicki
 Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ Budowa rybosomu Translacja
Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ Budowa rybosomu Translacja
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. Zawiera całą funkcjonalną podjednostkę wraz
Regulacja transkrypcji genów eukariotycznych Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. Zawiera całą funkcjonalną podjednostkę wraz
wykład dla studentów II roku biotechnologii Andrzej Wierzbicki
 Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ Wykład 5 Droga od genu do
Genetyka ogólna wykład dla studentów II roku biotechnologii Andrzej Wierzbicki Uniwersytet Warszawski Wydział Biologii andw@ibb.waw.pl http://arete.ibb.waw.pl/private/genetyka/ Wykład 5 Droga od genu do
The Role of Maf1 Protein in trna Processing and Stabilization / Rola białka Maf1 w dojrzewaniu i kontroli stabilności trna
 Streszczenie rozprawy doktorskiej pt. The Role of Maf1 Protein in trna Processing and Stabilization / Rola białka Maf1 w dojrzewaniu i kontroli stabilności trna mgr Tomasz Turowski, promotor prof. dr hab.
Streszczenie rozprawy doktorskiej pt. The Role of Maf1 Protein in trna Processing and Stabilization / Rola białka Maf1 w dojrzewaniu i kontroli stabilności trna mgr Tomasz Turowski, promotor prof. dr hab.
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. Zawiera całą funkcjonalną
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. Zawiera całą funkcjonalną
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Literatura Allison, r. 13 Brown, r. 12.2 Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Literatura Allison, r. 13 Brown, r. 12.2 Definicja genu Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze
października 2013: Elementarz biologii molekularnej. Wykład nr 2 BIOINFORMATYKA rok II
 10 października 2013: Elementarz biologii molekularnej www.bioalgorithms.info Wykład nr 2 BIOINFORMATYKA rok II Komórka: strukturalna i funkcjonalne jednostka organizmu żywego Jądro komórkowe: chroniona
10 października 2013: Elementarz biologii molekularnej www.bioalgorithms.info Wykład nr 2 BIOINFORMATYKA rok II Komórka: strukturalna i funkcjonalne jednostka organizmu żywego Jądro komórkowe: chroniona
Wykład 14 Biosynteza białek
 BIOCHEMIA Kierunek: Technologia Żywności i Żywienie Człowieka semestr III Wykład 14 Biosynteza białek WYDZIAŁ NAUK O ŻYWNOŚCI I RYBACTWA CENTRUM BIOIMMOBILIZACJI I INNOWACYJNYCH MATERIAŁÓW OPAKOWANIOWYCH
BIOCHEMIA Kierunek: Technologia Żywności i Żywienie Człowieka semestr III Wykład 14 Biosynteza białek WYDZIAŁ NAUK O ŻYWNOŚCI I RYBACTWA CENTRUM BIOIMMOBILIZACJI I INNOWACYJNYCH MATERIAŁÓW OPAKOWANIOWYCH
TRANSKRYPCJA - I etap ekspresji genów
 Eksparesja genów TRANSKRYPCJA - I etap ekspresji genów Przepisywanie informacji genetycznej z makrocząsteczki DNA na mniejsze i bardziej funkcjonalne cząsteczki pre-mrna Polimeraza RNA ETAP I Inicjacja
Eksparesja genów TRANSKRYPCJA - I etap ekspresji genów Przepisywanie informacji genetycznej z makrocząsteczki DNA na mniejsze i bardziej funkcjonalne cząsteczki pre-mrna Polimeraza RNA ETAP I Inicjacja
Drzewo życia pozycja roślin. Ewolucja genetycznych narzędzi kontroli rozwoju roślin
 Chlorophytes Charophytes Bryophytes Lycophytes Ferns Gymnosperms Angiosperms 2014-02-05 Ewolucja genetycznych narzędzi kontroli rozwoju roślin Drzewo życia pozycja roślin Rafał Archacki http://5e.plantphys.net/article.php?ch=t&id=399
Chlorophytes Charophytes Bryophytes Lycophytes Ferns Gymnosperms Angiosperms 2014-02-05 Ewolucja genetycznych narzędzi kontroli rozwoju roślin Drzewo życia pozycja roślin Rafał Archacki http://5e.plantphys.net/article.php?ch=t&id=399
Komórka stuktura i funkcje. Bogusław Nedoszytko. WSZPIZU Wydział w Gdyni
 Komórka stuktura i funkcje Bogusław Nedoszytko WSZPIZU Wydział w Gdyni Jądro komórkowe Struktura i funkcje Podziały komórkowe Jądro komórkowe 46 chromosomów 2,6 metra DNA 3 miliardy par nukleotydów (A,T,G,C)
Komórka stuktura i funkcje Bogusław Nedoszytko WSZPIZU Wydział w Gdyni Jądro komórkowe Struktura i funkcje Podziały komórkowe Jądro komórkowe 46 chromosomów 2,6 metra DNA 3 miliardy par nukleotydów (A,T,G,C)
Heterochromatyna i epigenetyczne wyciszanie ekspresji genów
 Heterochromatyna i epigenetyczne wyciszanie ekspresji genów 1 Plan wykładu: 1. Charakterystyka heterochromatyny 2. Wyciszanie transpozonów 3. Przebudowa chromatyny rola białek Polycomb 4. Funkcje białek
Heterochromatyna i epigenetyczne wyciszanie ekspresji genów 1 Plan wykładu: 1. Charakterystyka heterochromatyny 2. Wyciszanie transpozonów 3. Przebudowa chromatyny rola białek Polycomb 4. Funkcje białek
Zmiany epigenetyczne a dieta
 GENO-centryczne teorie mają ograniczony zasięg Klasyczna genetyka nie może wytłumaczyć na przykład : Zmiany epigenetyczne a dieta 1. różnorodności fenotypowej w obrębie populacji; 2. dlaczego bliźniaki
GENO-centryczne teorie mają ograniczony zasięg Klasyczna genetyka nie może wytłumaczyć na przykład : Zmiany epigenetyczne a dieta 1. różnorodności fenotypowej w obrębie populacji; 2. dlaczego bliźniaki
TATA box. Enhancery. CGCG ekson intron ekson intron ekson CZĘŚĆ KODUJĄCA GENU TERMINATOR. Elementy regulatorowe
 Promotory genu Promotor bliski leży w odległości do 40 pz od miejsca startu transkrypcji, zawiera kasetę TATA. Kaseta TATA to silnie konserwowana sekwencja TATAAAA, występująca w większości promotorów
Promotory genu Promotor bliski leży w odległości do 40 pz od miejsca startu transkrypcji, zawiera kasetę TATA. Kaseta TATA to silnie konserwowana sekwencja TATAAAA, występująca w większości promotorów
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Literatura Allison, r. 13 Brown, r. 12.2 Poziom RNA w komórce dojrzewanie/obróbka synteza degradacja Rys. dr Monika Zakrzewska-Płaczek,
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne Literatura Allison, r. 13 Brown, r. 12.2 Poziom RNA w komórce dojrzewanie/obróbka synteza degradacja Rys. dr Monika Zakrzewska-Płaczek,
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Klasyczne wyobrażenie genu fragment DNA, który koduje funkcjonalny mrna Wszystkie transkrypty mrna mają niekodujące fragmenty 5 i 3 końcowe
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Klasyczne wyobrażenie genu fragment DNA, który koduje funkcjonalny mrna Wszystkie transkrypty mrna mają niekodujące fragmenty 5 i 3 końcowe
Analizy wielkoskalowe w badaniach chromatyny
 Analizy wielkoskalowe w badaniach chromatyny Analizy wielkoskalowe wykorzystujące mikromacierze DNA Genotypowanie: zróżnicowane wewnątrz genów RNA Komórka eukariotyczna Ekspresja genów: Które geny? Poziom
Analizy wielkoskalowe w badaniach chromatyny Analizy wielkoskalowe wykorzystujące mikromacierze DNA Genotypowanie: zróżnicowane wewnątrz genów RNA Komórka eukariotyczna Ekspresja genów: Które geny? Poziom
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Definicja genu } Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. } Zawiera całą funkcjonalną
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Definicja genu } Region DNA, który określa dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko lub RNA. } Zawiera całą funkcjonalną
Plan wykładu: Budowa chromatyny - nukleosomy. Wpływ nukleosomów na replikację i transkrypcję
 Nukleosomy 1 Plan wykładu: Budowa chromatyny - nukleosomy Wpływ nukleosomów na replikację i transkrypcję Metody pozwalające na wyznaczanie miejsc wiązania nukleosomów Charakterystyka obsadzenia nukleosomów
Nukleosomy 1 Plan wykładu: Budowa chromatyny - nukleosomy Wpływ nukleosomów na replikację i transkrypcję Metody pozwalające na wyznaczanie miejsc wiązania nukleosomów Charakterystyka obsadzenia nukleosomów
Badanie funkcji genu
 Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
Badanie funkcji genu Funkcję genu można zbadać różnymi sposobami Przypadkowa analizy funkcji genu MUTACJA FENOTYP GEN Strategia ukierunkowanej analizy funkcji genu GEN 1. wprowadzenie mutacji w genie 2.
WARUNKI ZALICZENIA PRZEDMIOTU- 5 ECTS
 WARUNKI ZALICZENIA PRZEDMIOTU- 5 ECTS KOLOKWIA; 15% KOLOKWIA-MIN; 21% WEJŚCIÓWKI; 6% WEJŚCIÓWKI-MIN; 5% EGZAMIN; 27% EGZAMIN-MIN; 26% WARUNKI ZALICZENIA PRZEDMIOTU- 5 ECTS kolokwium I 12% poprawa kolokwium
WARUNKI ZALICZENIA PRZEDMIOTU- 5 ECTS KOLOKWIA; 15% KOLOKWIA-MIN; 21% WEJŚCIÓWKI; 6% WEJŚCIÓWKI-MIN; 5% EGZAMIN; 27% EGZAMIN-MIN; 26% WARUNKI ZALICZENIA PRZEDMIOTU- 5 ECTS kolokwium I 12% poprawa kolokwium
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu - klasyczna GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu - klasyczna GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
Składniki diety a stabilność struktury DNA
 Składniki diety a stabilność struktury DNA 1 DNA jedyna makrocząsteczka, której synteza jest ściśle kontrolowana, a powstałe błędy są naprawiane DNA jedyna makrocząsteczka naprawiana in vivo Replikacja
Składniki diety a stabilność struktury DNA 1 DNA jedyna makrocząsteczka, której synteza jest ściśle kontrolowana, a powstałe błędy są naprawiane DNA jedyna makrocząsteczka naprawiana in vivo Replikacja
Zgodnie z tzw. modelem interpunkcji trna, cząsteczki mt-trna wyznaczają miejsca
 Tytuł pracy: Autor: Promotor rozprawy: Recenzenci: Funkcje białek ELAC2 i SUV3 u ssaków i ryb Danio rerio. Praca doktorska wykonana w Instytucie Genetyki i Biotechnologii, Wydział Biologii UW Lien Brzeźniak
Tytuł pracy: Autor: Promotor rozprawy: Recenzenci: Funkcje białek ELAC2 i SUV3 u ssaków i ryb Danio rerio. Praca doktorska wykonana w Instytucie Genetyki i Biotechnologii, Wydział Biologii UW Lien Brzeźniak
Zmiany epigenetyczne a dieta
 Zmiany epigenetyczne a dieta Prof. dr hab. n. med. Małgorzata Milkiewicz Zmiany epigenetyczne a dieta 1 Chromatyna ulega kondensacji i dekondensacji podczas cyklu komórkowego stopień jej kondensacji wpływa
Zmiany epigenetyczne a dieta Prof. dr hab. n. med. Małgorzata Milkiewicz Zmiany epigenetyczne a dieta 1 Chromatyna ulega kondensacji i dekondensacji podczas cyklu komórkowego stopień jej kondensacji wpływa
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
Badanie dynamiki białek jądrowych w żywych komórkach metodą mikroskopii konfokalnej
 Badanie dynamiki białek jądrowych w żywych komórkach metodą mikroskopii konfokalnej PRAKTIKUM Z BIOLOGII KOMÓRKI () ćwiczenie prowadzone we współpracy z Pracownią Biofizyki Komórki Badanie dynamiki białek
Badanie dynamiki białek jądrowych w żywych komórkach metodą mikroskopii konfokalnej PRAKTIKUM Z BIOLOGII KOMÓRKI () ćwiczenie prowadzone we współpracy z Pracownią Biofizyki Komórki Badanie dynamiki białek
Gen eukariotyczny. Działanie i regulacja etapy posttranskrypcyjne
 Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Geny eukariotyczne Procesy transkrypcji i translacji są rozdzielone w przestrzeni i czasie Każdy gen ma własny promotor, nie występują
Gen eukariotyczny Działanie i regulacja etapy posttranskrypcyjne 1 Geny eukariotyczne Procesy transkrypcji i translacji są rozdzielone w przestrzeni i czasie Każdy gen ma własny promotor, nie występują
THE UNFOLDED PROTEIN RESPONSE
 THE UNFOLDED PROTEIN RESPONSE Anna Czarnecka Źródło: Intercellular signaling from the endoplasmatic reticulum to the nucleus: the unfolded protein response in yeast and mammals Ch. Patil & P. Walter The
THE UNFOLDED PROTEIN RESPONSE Anna Czarnecka Źródło: Intercellular signaling from the endoplasmatic reticulum to the nucleus: the unfolded protein response in yeast and mammals Ch. Patil & P. Walter The
DNA musi współdziałać z białkami!
 DNA musi współdziałać z białkami! Specyficzność oddziaływań między DNA a białkami wiążącymi DNA zależy od: zmian konformacyjnych wzdłuż cząsteczki DNA zróżnicowania struktury DNA wynikającego z sekwencji
DNA musi współdziałać z białkami! Specyficzność oddziaływań między DNA a białkami wiążącymi DNA zależy od: zmian konformacyjnych wzdłuż cząsteczki DNA zróżnicowania struktury DNA wynikającego z sekwencji
Marek Figlerowicz 1, Agata Tyczewska 1, Magdalena Figlerowicz 2
 PRZEGL EPIDEMIOL 2006; 60: 693 700 Marek Figlerowicz 1, Agata Tyczewska 1, Magdalena Figlerowicz 2 Wpływ małych regulatorowych RNA na przebieg zakażeń wirusowych nowe strategie leczenia zakażeń HCV 1 Zespół
PRZEGL EPIDEMIOL 2006; 60: 693 700 Marek Figlerowicz 1, Agata Tyczewska 1, Magdalena Figlerowicz 2 Wpływ małych regulatorowych RNA na przebieg zakażeń wirusowych nowe strategie leczenia zakażeń HCV 1 Zespół
mirna i zmiany faz wzrostu wegetatywnego
 mirna i zmiany faz wzrostu wegetatywnego mir156 reguluje ekspresję genów SPL (SQUAMOSA PROMOTER BINDING PROTEIN-LIKE) Defekty morfologiczne wywołane nadekspresją mirna w Arabidopsis" mirna156 mirna166
mirna i zmiany faz wzrostu wegetatywnego mir156 reguluje ekspresję genów SPL (SQUAMOSA PROMOTER BINDING PROTEIN-LIKE) Defekty morfologiczne wywołane nadekspresją mirna w Arabidopsis" mirna156 mirna166
NUTRIGENOMIKA na co mają geny apetyt. Ewa Róg - Zielińska
 NUTRIGENOMIKA na co mają geny apetyt Ewa Róg - Zielińska NUTRIGENOMIKA badanie zależności między żywieniem a odpowiedzią organizmu na poziomie ekspresji genów dieta ma wpływ na każdy etap ekspresji - na
NUTRIGENOMIKA na co mają geny apetyt Ewa Róg - Zielińska NUTRIGENOMIKA badanie zależności między żywieniem a odpowiedzią organizmu na poziomie ekspresji genów dieta ma wpływ na każdy etap ekspresji - na
TECHNIKI ANALIZY RNA TECHNIKI ANALIZY RNA TECHNIKI ANALIZY RNA
 DNA 28SRNA 18/16S RNA 5SRNA mrna Ilościowa analiza mrna aktywność genów w zależności od wybranych czynników: o rodzaju tkanki o rodzaju czynnika zewnętrznego o rodzaju upośledzenia szlaku metabolicznego
DNA 28SRNA 18/16S RNA 5SRNA mrna Ilościowa analiza mrna aktywność genów w zależności od wybranych czynników: o rodzaju tkanki o rodzaju czynnika zewnętrznego o rodzaju upośledzenia szlaku metabolicznego
cytoplazma + jądro komórkowe = protoplazma Jądro komórkowe
 Komórka eukariotyczna http://pl.wikipedia.org/w/index.php?title=plik:hela_cells_stained_with_hoechst_33258.jpg cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii,
Komórka eukariotyczna http://pl.wikipedia.org/w/index.php?title=plik:hela_cells_stained_with_hoechst_33258.jpg cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii,
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko
Regulacja transkrypcji genów eukariotycznych Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną dziedziczoną cechę organizmu; zwykle koduje pojedyncze białko
BUDOWA I FUNKCJA GENOMU LUDZKIEGO
 BUDOWA I FUNKCJA GENOMU LUDZKIEGO Magdalena Mayer Katedra i Zakład Genetyki Medycznej UM w Poznaniu 1. Projekt poznania genomu człowieka: Cele programu: - skonstruowanie szczegółowych map fizycznych i
BUDOWA I FUNKCJA GENOMU LUDZKIEGO Magdalena Mayer Katedra i Zakład Genetyki Medycznej UM w Poznaniu 1. Projekt poznania genomu człowieka: Cele programu: - skonstruowanie szczegółowych map fizycznych i
DNA superhelikalny eukariota DNA kolisty bakterie plazmidy mitochondria DNA liniowy wirusy otrzymywany in vitro
 DNA- kwas deoksyrybonukleinowy: DNA superhelikalny eukariota DNA kolisty bakterie plazmidy mitochondria DNA liniowy wirusy otrzymywany in vitro RNA- kwasy rybonukleinowe: RNA matrycowy (mrna) transkrybowany
DNA- kwas deoksyrybonukleinowy: DNA superhelikalny eukariota DNA kolisty bakterie plazmidy mitochondria DNA liniowy wirusy otrzymywany in vitro RNA- kwasy rybonukleinowe: RNA matrycowy (mrna) transkrybowany
Nowoczesne systemy ekspresji genów
 Nowoczesne systemy ekspresji genów Ekspresja genów w organizmach żywych GEN - pojęcia podstawowe promotor sekwencja kodująca RNA terminator gen Gen - odcinek DNA zawierający zakodowaną informację wystarczającą
Nowoczesne systemy ekspresji genów Ekspresja genów w organizmach żywych GEN - pojęcia podstawowe promotor sekwencja kodująca RNA terminator gen Gen - odcinek DNA zawierający zakodowaną informację wystarczającą
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
Regulacja transkrypcji genów eukariotycznych Klasyczne wyobrażenie genu fragment DNA, który koduje mrna Definicja genu GEN- podstawowa jednostka dziedziczenia Region DNA, który określa charakterystyczną
GENOM I JEGO STRUKTURA
 GENOM I JEGO STRUKTURA GENOM Ogół materiału genetycznego (kwasu nukleinowego niosącego informację genetyczną) zawartego w pojedynczej części składowej (komórce, cząstce wirusa) organizmu 1 Genom eukariotyczny
GENOM I JEGO STRUKTURA GENOM Ogół materiału genetycznego (kwasu nukleinowego niosącego informację genetyczną) zawartego w pojedynczej części składowej (komórce, cząstce wirusa) organizmu 1 Genom eukariotyczny
Jak działają geny. Podstawy biologii molekularnej genu
 Jak działają geny Podstawy biologii molekularnej genu Uniwersalność życia Podstawowe mechanizmy są takie same u wszystkich znanych organizmów budowa DNA i RNA kod genetyczny repertuar aminokwasów budujących
Jak działają geny Podstawy biologii molekularnej genu Uniwersalność życia Podstawowe mechanizmy są takie same u wszystkich znanych organizmów budowa DNA i RNA kod genetyczny repertuar aminokwasów budujących
Transport makrocząsteczek
 Komórka eukariotyczna cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii, dzięki której organizm uzyskuje energię biosynteza białka i innych związków Transport
Komórka eukariotyczna cytoplazma + jądro komórkowe = protoplazma W cytoplazmie odbywa się: cała przemiana materii, dzięki której organizm uzyskuje energię biosynteza białka i innych związków Transport
Dr hab. Anna Bębenek Warszawa,
 Dr hab. Anna Bębenek Warszawa, 14.01. 2018 Instytut Biochemii i Biofizyki PAN Ul. Pawińskiego 5a 02-106 Warszawa Recenzja pracy doktorskiej Pana mgr Michała Płachty Pod Tytułem Regulacja funkcjonowania
Dr hab. Anna Bębenek Warszawa, 14.01. 2018 Instytut Biochemii i Biofizyki PAN Ul. Pawińskiego 5a 02-106 Warszawa Recenzja pracy doktorskiej Pana mgr Michała Płachty Pod Tytułem Regulacja funkcjonowania
Zarówno u organizmów eukariotycznych, jak i prokariotycznych proces replikacji ma charakter semikonserwatywny.
 HIPTEZY WYJAŚIAJĄCE MECHAIZM REPLIKACJI C. Model replikacji semikonserwatywnej zakłada on, że obie nici macierzystej cząsteczki DA są matrycą dla nowych, dosyntetyzowywanych nici REPLIKACJA każda z dwóch
HIPTEZY WYJAŚIAJĄCE MECHAIZM REPLIKACJI C. Model replikacji semikonserwatywnej zakłada on, że obie nici macierzystej cząsteczki DA są matrycą dla nowych, dosyntetyzowywanych nici REPLIKACJA każda z dwóch
Rzęski, wici - budowa Mikrotubule. rozmieszczenie organelli. Stabilne mikrotubule szkielet rzęsek i wici
 Mikrotubule dynamiczna niestabilność - stabilizacja rozmieszczenie organelli ER Golgi organizują wnętrze komórki - polaryzacja komórki Mt Mt organizacja ER, aparatu Golgiego przemieszczanie mitochondriów
Mikrotubule dynamiczna niestabilność - stabilizacja rozmieszczenie organelli ER Golgi organizują wnętrze komórki - polaryzacja komórki Mt Mt organizacja ER, aparatu Golgiego przemieszczanie mitochondriów
Prokariota i Eukariota
 Prokariota i Eukariota W komórkach organizmów żywych ilość DNA jest zazwyczaj stała i charakterystyczna dla danego gatunku. ILOŚĆ DNA PRZYPADAJĄCA NA APARAT GENETYCZNY WZRASTA WRAZ Z BARDZIEJ FILOGENETYCZNIE
Prokariota i Eukariota W komórkach organizmów żywych ilość DNA jest zazwyczaj stała i charakterystyczna dla danego gatunku. ILOŚĆ DNA PRZYPADAJĄCA NA APARAT GENETYCZNY WZRASTA WRAZ Z BARDZIEJ FILOGENETYCZNIE
Wykład 13. Regulacja cyklu komórkowego w odpowiedzi na uszkodzenia DNA. Mechanizmy powstawania nowotworów
 Wykład 13 Regulacja cyklu komórkowego w odpowiedzi na uszkodzenia DNA Mechanizmy powstawania nowotworów Uszkodzenie DNA Wykrycie uszkodzenia Naprawa DNA Zatrzymanie cyklu kom. Apoptoza Źródła uszkodzeń
Wykład 13 Regulacja cyklu komórkowego w odpowiedzi na uszkodzenia DNA Mechanizmy powstawania nowotworów Uszkodzenie DNA Wykrycie uszkodzenia Naprawa DNA Zatrzymanie cyklu kom. Apoptoza Źródła uszkodzeń
Fragment cząsteczki DNA stanowiący matrycę dla syntezy cząsteczki lub podjednostki białka nazywamy GENEM
 KONTROLA EKSPRESJI GENU PRZEKAZYWANIE INFORMACJI GENETYCZNEJ Informacja genetyczna - instrukcje kierujące wszystkimi funkcjami komórki lub organizmu zapisane jako określone, swoiste sekwencje nukleotydów
KONTROLA EKSPRESJI GENU PRZEKAZYWANIE INFORMACJI GENETYCZNEJ Informacja genetyczna - instrukcje kierujące wszystkimi funkcjami komórki lub organizmu zapisane jako określone, swoiste sekwencje nukleotydów
Ekspresja informacji genetycznej
 Ekspresja informacji genetycznej Informacja o budowie i funkcjonowaniu organizmu jest zakodowana w sekwencji nukleotydów cząsteczek DNA i podzielona na dużą liczbę genów. Gen jest odcinkiem DNA kodującym
Ekspresja informacji genetycznej Informacja o budowie i funkcjonowaniu organizmu jest zakodowana w sekwencji nukleotydów cząsteczek DNA i podzielona na dużą liczbę genów. Gen jest odcinkiem DNA kodującym
Transport makrocząsteczek (białek)
 Transport makrocząsteczek (białek) Transport makrocząsteczek sortowanie białek - sekwencje sygnałowe lata 70-te XX w. - Günter Blobel - hipoteza sygnałowa; 1999r - nagroda Nobla Sekwencja sygnałowa: A
Transport makrocząsteczek (białek) Transport makrocząsteczek sortowanie białek - sekwencje sygnałowe lata 70-te XX w. - Günter Blobel - hipoteza sygnałowa; 1999r - nagroda Nobla Sekwencja sygnałowa: A
BIOINFORMATYKA. edycja 2016 / wykład 11 RNA. dr Jacek Śmietański
 BIOINFORMATYKA edycja 2016 / 2017 wykład 11 RNA dr Jacek Śmietański jacek.smietanski@ii.uj.edu.pl http://jaceksmietanski.net Plan wykładu 1. Rola i rodzaje RNA 2. Oddziaływania wewnątrzcząsteczkowe i struktury
BIOINFORMATYKA edycja 2016 / 2017 wykład 11 RNA dr Jacek Śmietański jacek.smietanski@ii.uj.edu.pl http://jaceksmietanski.net Plan wykładu 1. Rola i rodzaje RNA 2. Oddziaływania wewnątrzcząsteczkowe i struktury
srna: małe cząsteczki o dużych możliwościach
 Plan srna: małe cząsteczki o dużych możliwościach Marek Daniel Koter, Marcin Filipecki Katedra Genetyki, Hodowli i Biotechnologii Roślin Wydział Ogrodnictwa, Biotechnologii i Architektury Krajobrazu Szkoła
Plan srna: małe cząsteczki o dużych możliwościach Marek Daniel Koter, Marcin Filipecki Katedra Genetyki, Hodowli i Biotechnologii Roślin Wydział Ogrodnictwa, Biotechnologii i Architektury Krajobrazu Szkoła
transkrypcja chromatyny
 transkrypcja chromatyny problem: Jak to może e działać: dysocjacja histonów? kompleks pol II RNA >500 kd skip: split: nukleosom: 145 bp DNA = 100 kd rdzeń histonowy = 100 kd strip: + Skip czy Split czy
transkrypcja chromatyny problem: Jak to może e działać: dysocjacja histonów? kompleks pol II RNA >500 kd skip: split: nukleosom: 145 bp DNA = 100 kd rdzeń histonowy = 100 kd strip: + Skip czy Split czy
Ewolucja genetycznych narzędzi kontroli rozwoju roślin
 Ewolucja genetycznych narzędzi kontroli rozwoju roślin Rafał Archacki Zakład Biologii Systemów Drzewo życia pozycja roślin http://5e.plantphys.net/article.php?ch=t&id=399 Chlorophytes Charophytes Bryophytes
Ewolucja genetycznych narzędzi kontroli rozwoju roślin Rafał Archacki Zakład Biologii Systemów Drzewo życia pozycja roślin http://5e.plantphys.net/article.php?ch=t&id=399 Chlorophytes Charophytes Bryophytes
WYKŁAD: Klasyczny przepływ informacji ( Dogmat) Klasyczny przepływ informacji. Ekspresja genów realizacja informacji zawartej w genach
 WYKŁAD: Ekspresja genów realizacja informacji zawartej w genach Prof. hab. n. med. Małgorzata Milkiewicz Zakład Biologii Medycznej Klasyczny przepływ informacji ( Dogmat) Białka Retrowirusy Białka Klasyczny
WYKŁAD: Ekspresja genów realizacja informacji zawartej w genach Prof. hab. n. med. Małgorzata Milkiewicz Zakład Biologii Medycznej Klasyczny przepływ informacji ( Dogmat) Białka Retrowirusy Białka Klasyczny
Regulacja transkrypcji genów eukariotycznych
 Regulacja transkrypcji genów eukariotycznych Dr hab. Marta Koblowska, prof. UW Zakład Biologii Systemów, Wydział Biologii UW Pracownia Analiz Mikromacierzy i Sekwencjonowania UW/IBB PAN Klasyczne wyobrażenie
Regulacja transkrypcji genów eukariotycznych Dr hab. Marta Koblowska, prof. UW Zakład Biologii Systemów, Wydział Biologii UW Pracownia Analiz Mikromacierzy i Sekwencjonowania UW/IBB PAN Klasyczne wyobrażenie
Podstawy genetyki molekularnej
 Podstawy genetyki molekularnej Materiał genetyczny Materiałem genetycznym są kwasy nukleinowe Materiałem genetycznym organizmów komórkowych jest kwas deoksyrybonukleinowy (DNA) 5 DNA zbudowany jest z nukleotydów
Podstawy genetyki molekularnej Materiał genetyczny Materiałem genetycznym są kwasy nukleinowe Materiałem genetycznym organizmów komórkowych jest kwas deoksyrybonukleinowy (DNA) 5 DNA zbudowany jest z nukleotydów
Metody bioinformatyki. Ekspresja genów. prof. dr hab. Jan Mulawka
 Metody bioinformatyki Ekspresja genów prof. dr hab. Jan Mulawka Genetyczny skład prawie wszystkich komórek somatycznych organizmów wielokomórkowych jest identyczny. Fenotyp (swoistość tkankowa lub komórkowa)
Metody bioinformatyki Ekspresja genów prof. dr hab. Jan Mulawka Genetyczny skład prawie wszystkich komórek somatycznych organizmów wielokomórkowych jest identyczny. Fenotyp (swoistość tkankowa lub komórkowa)
WPROWADZENIE DO GENETYKI MOLEKULARNEJ
 WPROWADZENIE DO GENETYKI MOLEKULARNEJ Replikacja organizacja widełek replikacyjnych Transkrypcja i biosynteza białek Operon regulacja ekspresji genów Prowadzący wykład: prof. dr hab. Jarosław Burczyk REPLIKACJA
WPROWADZENIE DO GENETYKI MOLEKULARNEJ Replikacja organizacja widełek replikacyjnych Transkrypcja i biosynteza białek Operon regulacja ekspresji genów Prowadzący wykład: prof. dr hab. Jarosław Burczyk REPLIKACJA
WPROWADZENIE DO GENETYKI MOLEKULARNEJ
 WPROWADZENIE DO GENETYKI MOLEKULARNEJ Replikacja organizacja widełek replikacyjnych Transkrypcja i biosynteza białek Operon regulacja ekspresji genów Prowadzący wykład: prof. dr hab. Jarosław Burczyk REPLIKACJA
WPROWADZENIE DO GENETYKI MOLEKULARNEJ Replikacja organizacja widełek replikacyjnych Transkrypcja i biosynteza białek Operon regulacja ekspresji genów Prowadzący wykład: prof. dr hab. Jarosław Burczyk REPLIKACJA
Regulacja Ekspresji Genów
 Regulacja Ekspresji Genów Wprowadzenie o Ekspresja genu jest to złożony proces jego transkrypcji do mrna, o Obróbki tego mrna, a następnie o Translacji do białka. 4/17/2019 2 4/17/2019 3 E 1 GEN 3 Promotor
Regulacja Ekspresji Genów Wprowadzenie o Ekspresja genu jest to złożony proces jego transkrypcji do mrna, o Obróbki tego mrna, a następnie o Translacji do białka. 4/17/2019 2 4/17/2019 3 E 1 GEN 3 Promotor
Historia informacji genetycznej. Jak ewolucja tworzy nową informację (z ma ą dygresją).
 Historia informacji genetycznej. Jak ewolucja tworzy nową informację (z ma ą dygresją). Czym jest życie? metabolizm + informacja (replikacja) 2 Cząsteczki organiczne mog y powstać w atmosferze pierwotnej
Historia informacji genetycznej. Jak ewolucja tworzy nową informację (z ma ą dygresją). Czym jest życie? metabolizm + informacja (replikacja) 2 Cząsteczki organiczne mog y powstać w atmosferze pierwotnej
Ocena rozprawy doktorskiej mgr Justyny Kowalczyk
 Dr hab. Paweł Bednarek, prof. IChB PAN Instytut Chemii Bioorganicznej PAN ul. Noskowskiego 12/14 61-704 Poznań Ocena rozprawy doktorskiej mgr Justyny Kowalczyk Identyfikacja i charakterystyka nowego regulatora
Dr hab. Paweł Bednarek, prof. IChB PAN Instytut Chemii Bioorganicznej PAN ul. Noskowskiego 12/14 61-704 Poznań Ocena rozprawy doktorskiej mgr Justyny Kowalczyk Identyfikacja i charakterystyka nowego regulatora
Modyfikacje epigenetyczne w czasie wzrostu oocytów związane z rozszerzeniem rozwoju partenogenetycznego u myszy. Małgorzata Karney
 Modyfikacje epigenetyczne w czasie wzrostu oocytów związane z rozszerzeniem rozwoju partenogenetycznego u myszy. Małgorzata Karney Epigenetyka Epigenetyka zwykle definiowana jest jako nauka o dziedzicznych
Modyfikacje epigenetyczne w czasie wzrostu oocytów związane z rozszerzeniem rozwoju partenogenetycznego u myszy. Małgorzata Karney Epigenetyka Epigenetyka zwykle definiowana jest jako nauka o dziedzicznych
Kwasy nukleinowe. Replikacja
 Kwasy nukleinowe Replikacja Białko Helikaza Prymaza SSB Funkcja w replikacji DNA Rozplata podwójną helisę Syntetyzuje starterowy odcinek RNA Stabilizuje regiony jednoniciowe Gyraza DNA Wprowadza ujemne
Kwasy nukleinowe Replikacja Białko Helikaza Prymaza SSB Funkcja w replikacji DNA Rozplata podwójną helisę Syntetyzuje starterowy odcinek RNA Stabilizuje regiony jednoniciowe Gyraza DNA Wprowadza ujemne
Modyfikacje histonów rdzeniowych
 Modyfikacje histonów rdzeniowych Fosforylacja (seryna, treonina) Acetylacja (lizyna) Modyfikacje histonów rdzeniowych Metylacja (lizyna, arginina) ADP-rybozylacja Ubikwitynylacja (lizyna) Sumoilacja (lizyna)
Modyfikacje histonów rdzeniowych Fosforylacja (seryna, treonina) Acetylacja (lizyna) Modyfikacje histonów rdzeniowych Metylacja (lizyna, arginina) ADP-rybozylacja Ubikwitynylacja (lizyna) Sumoilacja (lizyna)
białka wiążące specyficzne sekwencje DNA czynniki transkrypcyjne
 białka wiążące specyficzne sekwencje DNA czynniki transkrypcyjne http://www.umass.edu/molvis/bme3d/materials/jtat_080510/exploringdna/ch_flex/chapter.htm czynniki transkrypcyjne (aktywatory/represory)
białka wiążące specyficzne sekwencje DNA czynniki transkrypcyjne http://www.umass.edu/molvis/bme3d/materials/jtat_080510/exploringdna/ch_flex/chapter.htm czynniki transkrypcyjne (aktywatory/represory)
mikrosatelitarne, minisatelitarne i polimorfizm liczby kopii
 Zawartość 139371 1. Wstęp zarys historii genetyki, czyli od genetyki klasycznej do genomiki 2. Chromosomy i podziały jądra komórkowego 2.1. Budowa chromosomu 2.2. Barwienie prążkowe chromosomów 2.3. Mitoza
Zawartość 139371 1. Wstęp zarys historii genetyki, czyli od genetyki klasycznej do genomiki 2. Chromosomy i podziały jądra komórkowego 2.1. Budowa chromosomu 2.2. Barwienie prążkowe chromosomów 2.3. Mitoza
Translacja i proteom komórki
 Translacja i proteom komórki 1. Kod genetyczny 2. Budowa rybosomów 3. Inicjacja translacji 4. Elongacja translacji 5. Terminacja translacji 6. Potranslacyjne zmiany polipeptydów 7. Translacja a retikulum
Translacja i proteom komórki 1. Kod genetyczny 2. Budowa rybosomów 3. Inicjacja translacji 4. Elongacja translacji 5. Terminacja translacji 6. Potranslacyjne zmiany polipeptydów 7. Translacja a retikulum
Alchemia epigenetycznej regulacji pluripotencji
 Alchemia epigenetycznej regulacji pluripotencji Joanna Bem Iwona Grabowska * Zakład Cytologii, Wydział Biologii, Uniwersytet Warszawski, Warszawa * Zakład Cytologii, Wydział Biologii, Uniwersytet Warszawski,
Alchemia epigenetycznej regulacji pluripotencji Joanna Bem Iwona Grabowska * Zakład Cytologii, Wydział Biologii, Uniwersytet Warszawski, Warszawa * Zakład Cytologii, Wydział Biologii, Uniwersytet Warszawski,
Nowe oblicze świata RNA
 NAUKA 2/2009 93-109 AGATA TYCZEWSKA 1, MAREK FIGLEROWICZ 2 Nowe oblicze świata RNA Wstęp Jednym z najistotniejszych osiągnięć biologii w drugiej połowie XX wieku było poznanie podstaw molekularnych procesu
NAUKA 2/2009 93-109 AGATA TYCZEWSKA 1, MAREK FIGLEROWICZ 2 Nowe oblicze świata RNA Wstęp Jednym z najistotniejszych osiągnięć biologii w drugiej połowie XX wieku było poznanie podstaw molekularnych procesu
Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej
 Seminarium 1 część 1 Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej Genom człowieka Genomem nazywamy całkowitą ilość DNA jaka
Seminarium 1 część 1 Konspekt do zajęć z przedmiotu Genetyka dla kierunku Położnictwo dr Anna Skorczyk-Werner Katedra i Zakład Genetyki Medycznej Genom człowieka Genomem nazywamy całkowitą ilość DNA jaka
Wybrane techniki badania białek -proteomika funkcjonalna
 Wybrane techniki badania białek -proteomika funkcjonalna Proteomika: umożliwia badanie zestawu wszystkich (lub prawie wszystkich) białek komórkowych Zalety analizy proteomu np. w porównaniu z analizą trankryptomu:
Wybrane techniki badania białek -proteomika funkcjonalna Proteomika: umożliwia badanie zestawu wszystkich (lub prawie wszystkich) białek komórkowych Zalety analizy proteomu np. w porównaniu z analizą trankryptomu:
Całogenomowa analiza niskocząsteczkowych RNA, pochodzących z trna w Arabidopsis thaliana
 UNIWERSYTET IM. ADAMA MICKIEWICZA Wydział Biologii Całogenomowa analiza niskocząsteczkowych RNA, pochodzących z trna w Arabidopsis thaliana Agnieszka Thompson Instytut Biologii Molekularnej i Biotechnologii
UNIWERSYTET IM. ADAMA MICKIEWICZA Wydział Biologii Całogenomowa analiza niskocząsteczkowych RNA, pochodzących z trna w Arabidopsis thaliana Agnieszka Thompson Instytut Biologii Molekularnej i Biotechnologii
Prof. dr.hab. Andrzej Kaczanowski Instytut Zoologii Wydział Biologii Uniwersytetu Warszawskiego
 1 Prof. dr.hab. Andrzej Kaczanowski 26.10. 2017 Instytut Zoologii Wydział Biologii Uniwersytetu Warszawskiego kaczan@biol.uw.edu.pl Recenzja rozprawy doktorskiej Pani mgr. Julity Gruchoty p.t. Proces rearanżacji
1 Prof. dr.hab. Andrzej Kaczanowski 26.10. 2017 Instytut Zoologii Wydział Biologii Uniwersytetu Warszawskiego kaczan@biol.uw.edu.pl Recenzja rozprawy doktorskiej Pani mgr. Julity Gruchoty p.t. Proces rearanżacji
Replikacja DNA. Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego.
 Replikacja DNA Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego. Replikacja DNA jest bardzo złożonym procesem, w którym biorą udział setki
Replikacja DNA Materiały dydaktyczne współfinansowane ze środków Unii Europejskiej w ramach Europejskiego Funduszu Społecznego. Replikacja DNA jest bardzo złożonym procesem, w którym biorą udział setki
ANDRZEJ T. WIERZBICKI Zakład Biologii Molekularnej Roślin Uniwersytet Warszawski Pawińskiego 5a, Warszawa
 Tom 53, 2004 Numer 3 4 (264 265) Strony 271 280 ANDRZEJ T. WIERZBICKI Zakład Biologii Molekularnej Roślin Uniwersytet Warszawski Pawińskiego 5a, 02-106 Warszawa e-mail: andw@ibb.waw.pl DZIEDZICZENIE EPIGENETYCZNE
Tom 53, 2004 Numer 3 4 (264 265) Strony 271 280 ANDRZEJ T. WIERZBICKI Zakład Biologii Molekularnej Roślin Uniwersytet Warszawski Pawińskiego 5a, 02-106 Warszawa e-mail: andw@ibb.waw.pl DZIEDZICZENIE EPIGENETYCZNE
