Prowadzący: dr Lidia Boss znacznik fluorescencyjny (np. SYBR Green II)
|
|
|
- Bogusław Tomczyk
- 6 lat temu
- Przeglądów:
Transkrypt
1 Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią ============================================================================ Ćwiczenia 6 i 7 Analiza liczby kopii plazmidu z wykorzystaniem ilościowej reakcji łańcuchowej polimerazy Prowadzący: dr Lidia Boss UWAGA: Po zakończeniu ćwiczeń nr 6 i nr 7 proszę o przygotowanie jednego sprawozdania. W trakcie ćwiczeń numer 6 i 7 odbędą się dwa kolokwia (po jednym na każdym ćwiczeniu). Ilościowa reakcja łańcuchowa polimerazy (ang. quantitative polymerase chain reaction qpcr) jest techniką, która umożliwia określenie ilości matrycowego DNA w badanej próbce. Skład mieszaniny reakcyjnej w przypadku qpcr jest zbliżony do standardowej reakcji PCR (tabela 1). Główną różnicę pomiędzy tymi technikami stanowi zastosowanie znaczników fluorescencyjnych, które umożliwiają obserwację przyrostu produktu reakcji w czasie rzeczywistym. Rodzaj stosowanych w reakcji qpcr znaczników fluorescencyjnych może różnić się w zależności od celu eksperymentu. W ramach niniejszych zajęć omówimy szczegółowo technikę qpcr z zastosowaniem barwnika fluorescencyjnego SYBR Green II. Informacje na temat innych znaczników fluorescencyjnych można znaleźć w materiałach wymienionych w spisie literatury. Tabela 1. Porównanie składu mieszaniny reakcyjnej stosowanej do reakcji PCR i qpcr. Łańcuchowa reakcja polimerazy (PCR) Ilościowa łańcuchowa reakcja polimerazy (qpcr) Woda Woda bufor dostosowany do rodzaju polimerazy bufor dostosowany do rodzaju polimerazy jony magnezu jony magnezu mieszanina deoksynukleotydów (datp, dctp, dgtp, dttp) mieszanina deoksynukleotydów (datp, dctp, dgtp, dttp) termostabilna polimeraza termostabilna polimeraza Startery Startery matrycowy DNA matrycowy DNA znacznik fluorescencyjny (np. SYBR Green II) 1. Technika qpcr z zastosowaniem barwnika SYBR Green II. Cykl reakcji w technice qpcr składa się z trzech etapów: 1) Denaturacja DNA; etap ten polega na zerwaniu pod wpływem temperatury (95 C) wiązań wodorowych matrycowej helisy DNA i rozdzieleniu jej na dwie nici. 2) Hybrydyzacja starterów i poszczególnych nici DNA; w temperaturze 50 C komplementarne do sekwencji DNA startery przyłączają się do matrycowej nici DNA. 3) Wydłużanie starterów (elongacja); w temperaturze 60 C polimeraza DNA wydłuża startery przyłączone do matrycowej nici DNA. Powyższe etapy składają się na jeden cykl reakcji qpcr, który powtarzany jest zwykle 45 razy. W wyniku każdego cyklu z jednej cząsteczki matrycowego DNA powstają dwie cząsteczki potomne (ryc. 1). Rycina 1. Schemat przedstawiający proces amplifikacji DNA w przebiegu reakcji PCR.
2 Obecny w mieszaninie reakcyjnej, barwnik SYBR Green II ma zdolność wiązania się z dwuniciowym DNA (ryc. 2). SYBR Green II w roztworze (niezwiązany z DNA) charakteryzuje się stosunkowo niskim poziomem fluorescencji, natomiast po związaniu z DNA, poziom fluorescencji wzrasta nawet 1000-krotnie. Termocykler wykorzystywany do amplifikacji DNA metodą qpcr wyposażony jest w detektor, który wykonuje pomiar fluorescencji na etapie wydłużania starterów w każdym cyklu. Ilość barwnika związanego z DNA rośnie wraz z przyrostem produktów reakcji (DNA), zatem poziom fluorescencji jest wprost proporcjonalny do ilości DNA w próbce w danym momencie. 1. Denaturacja 2. Hybrydyzacja 3. Elongacja Rycina 2. Detekcja DNA z wykorzystaniem barwnika SYBR Green II. Barwnik wiąże się z dwuniciowym DNA, powstającym w przebiegu reakcji qpcr. Związanie SYBR Green II z DNA powoduje wzrost poziomu fluorescencji proporcjonalny do ilości DNA w próbce w danym momencie. Ostatnim etapem reakcji qpcr z wykorzystaniem znacznika SYBR Green II jest określenie temperatury topnienia (ang. melting temperature Tm) produktów reakcji qpcr. Etap ten ma miejsce po zakończeniu amplifikacji DNA, czyli po przeprowadzeniu ostatniego, czterdziestego piątego, cyklu PCR. Wartość Tm DNA zależy od ilości poszczególnych deoksyrybonukleotydów tworzących DNA (im więcej par G:C, tym wyższa temperatura topnienia DNA) oraz od długości cząsteczki DNA (im dłuższa helisa DNA, tym wyższa temperatura topnienia). Określenie wartości Tm DNA powstałego w wyniku reakcji qpcr pozwala na oszacowanie, czy w mieszaninie obecne są cząsteczki DNA o tej samej długości i kompozycji nukleotydowej, czy też w wyniku reakcji powstały produkty niejednorodne cząsteczki DNA różniące się składem i długością. W tym celu mieszanina reakcyjna zostaje schłodzona do 4 C, a następnie jest stopniowo ogrzewana aż do temperatury 95 C (ryc.3). Wyniki pomiaru fluorescencji prowadzonego podczas stopniowego ogrzewania mieszaniny umożliwiają wykonanie tzw. krzywej topnienia (krzywej dysocjacji) oraz określenie temperatury, w której dochodzi do denaturacji (topnienia) DNA (ryc. 4). Dla jednorodnych pod względem długości i składu cząsteczek DNA wymienione parametry będą takie same. Temperatura Cykl 1 Cykl 2 Badanie Tm produktów reakcji Etapy amplifikacji DNA 95 C Etap 1: Denaturacja 60 C Etap 3: Wydłużanie 50 C Etap 2: Hybrydyzacja 4 C
3 Rycina 3. Schemat przedstawiający zmiany temperatury w przebiegu reakcji qpcr oraz odpowiadające im etapy reakcji. Reakcję qpcr, podobnie jak standardową technikę PCR, można podzielić na 3 etapy: 1. Denaturację DNA. 2. Hybrydyzację starterów i poszczególnych nici DNA 3. Wydłużanie starterów Powyższe etapy składają się na jeden cykl reakcji qpcr, który powtarzany jest zwykle 45 razy. W wyniku każdego cyklu z jednej cząsteczki matrycowego DNA powstają dwie cząsteczki potomne. Barwnik SYBR Green II wiąże się z dwuniciowym DNA, co powoduje wzrost poziomu fluorescencji próbki. Kolorem zielonym oznaczono momenty, w których wykonywany jest pomiar poziomu fluorescencji. Zielona linia oznacza pomiar poziomu fluorescencji podczas stopniowego ogrzewania mieszaniny reakcyjnej, w celu określenia temperatury topnienia (Tm) produktów reakcji. Rycina 4. Krzywa dysocjacji produktów reakcji qpcr. 2. Interpretacja wyników reakcji qpcr z wykorzystaniem SYBR Green II. Wynikiem reakcji qpcr z wykorzystaniem barwnika SYBR Green II jest wykres obrazujący zmiany poziomu fluorescencji w zależności od czasu (numeru cyklu) (ryc. 5). Podstawową informacją, którą można uzyskać na podstawie takiego wykresu jest numer cyklu progowego (ang. treshold cycle Ct). Cykl progowy, to ten cykl reakcji qpcr, w którym dochodzi do akumulacji DNA w ilości wystarczającej, aby poziom fluorescencji barwnika przekroczył poziom podstawowy ( poziom tła ). Moment ten zostanie uzyskany szybciej w próbkach, które zawierają więcej matrycowego DNA, niż w próbkach, które zawierają matrycowego DNA mniej, zatem numer cyklu progowego jest odwrotnie proporcjonalny do ilości DNA w próbce. Zależność ta umożliwia oszacowanie początkowej ilości matrycowego DNA w badanej próbce na podstawie tzw. krzywej wzorcowej. W celu przygotowania krzywej wzorcowej należy wykonać szereg reakcji qpcr z wykorzystaniem znanych ilości matrycowego DNA, następnie określić wartość Ct dla poszczególnych próbek o znanej ilości matrycowego DNA. Na podstawie uzyskanych wyników zostaje wykreślona krzywa wzorcowa, czyli wykres zależności numeru cyklu progowego od ilości DNA w próbce (ryc. 6). Nachylenie wykresu (ang. slope) umożliwia określenie wydajności reakcji i powinno mieścić się w zakresie między -3.2 a -3.6.
4 Poziom fluorescencji Podstawowy poziom fluorescencji (barwnik niezwiązany z DNA) Poziom fluorescencji przekraczający poziom podstawowy (ang. threshold) Minimalny poziom fluorescencji wykrywany przez detektor Numer cyklu Rycina 5. Wykres zmian poziomu fluorescencji w zależności od numeru cyklu reakcji. Rycina 6. Krzywa standardowa dla reakcji qpcr z wykorzystaniem barwnika SYBR Green II. Na osi Y zaznaczono numery cykli reakcji qpcr, natomiast na osi X umieszczono wartości określające ilość matrycowego DNA (np. liczbę kopii plazmidu lub masę DNA wyrażoną w nanogramach). Poszczególne punkty widoczne na wykresie oznaczają wynik reakcji dla próbek zawierających znaną ilość matrycowego DNA, czyli numer cyklu progowego dla prób zawierających np. 1, 10, 100 i 1000 kopii plazmidu. Można zauważyć, że numer cyklu progowego wzrasta wraz ze spadkiem ilości matrycowego DNA w próbce. Na podstawie nachylenie wykreślonej krzywej (ang. slope) oszacowano wydajność (ang. efficiency) przeprowadzonej reakcji qpcr. 3. Zastosowanie qpcr w diagnostyce. Technika qpcr jest coraz częściej stosowaną metodą diagnostyczną. Metodę tę stosuje się w diagnostyce medycznej m.in. w celu wykrycia i identyfikacji lekoopornych mutantów patogennych bakterii (np. wankomycynoopornych szczepów Enterococcus faecium VRE) w próbkach moczu, krwi itp., co ułatwia szybkie zastosowanie odpowiedniej antybiotykoterapii. Technika ta umożliwia także określenie tzw. polimorfizmu SNP, co jest pomocne przy diagnostyce chorób genetycznych. Ilościowa łańcuchowa reakcja polimerazy umożliwia również oszacowanie ilości patogenów w badanej próbce. Możliwość ta wykorzystywana jest np. w diagnostyce prowadzonej u nosicieli HIV. Określenie metodą qpcr ilości cząstek cytomegalowirusa we krwi tych osób pozwala na oszacowanie ryzyka zachorowania u pacjentów o obniżonej odporności oraz monitorowanie skuteczności zastosowanej terapii antywirusowej. Przykładem zastosowania techniki qpcr w diagnostyce środowiskowej może być detekcja i określanie ilości bakterii indykatorowych w próbkach wody morskiej, w celu określenia klasy czystości wody. Metoda ta znajduje również zastosowanie w badaniach próbek żywności i wody pitnej w celu wykrycia patogennych bakterii (np. E. coli O157:H7). W porównaniu ze standardową metodą PCR, ilościowa reakcja łańcuchowa polimerazy jest metodą znacznie szybszą (wynik uzyskiwany jest po około 1 godzinie), stąd można się również spotkać z określeniem tej metody jako rapid PCR. Zarówno czułość detekcji badanego czynnika (np. patogennych bakterii), jak i specyficzność w stosunku do danego DNA w przypadku obu metod jest porównywalna. Ze względu na fakt, że w przypadku qpcr zarówno amplifikacja DNA, jak i jego detekcja prowadzone są w tej samej probówce, metoda ta jest obarczona niższym ryzykiem zanieczyszczenia próbek niż standardowa technika PCR.
5 4. Określenie relatywnej liczby kopii plazmidu z wykorzystaniem techniki qpcr Bakterie Escherichia coli niosące toksynę Shiga (Shiga toxin-producing Escherichia coli STEC) są przyczyną zakażeń, które mogą prowadzić do krwawej biegunki oraz poważnych powikłań, takich jak zespół hemolityczno-mocznicowy. Według raportu Centrum Zapobiegania i Kontroli Chorób CDC, szczepy STEC tylko w USA powodują około zachorowań rocznie, z czego około 90 kończy się śmiercią pacjenta. Geny kodujące toksynę Shiga w szczepach STEC znajdują się w DNA lizogenizującego faga, wbudowanym w chromosom bakteryjny. Indukcja profaga i rozpoczęcie cyklu litycznego jest bezpośrednio związana z syntezą i uwolnieniem toksyny Shiga. Poważnym problemem w terapii tego typu zakażeń jest fakt, że niektóre antybiotyki stosowane w terapii zakażeń bakteryjnych powodują indukcję profaga, a tym samym zaostrzenie objawów choroby. W związku z tym niezwykle istotnym etapem w leczeniu zakażeń szczepami STEC jest szybka diagnostyka, w celu zastosowania odpowiedniej strategii leczenia. Metoda qpcr jest jedną z metod diagnostycznych zalecanych przez CDC w przypadkach, w których podejrzewa się zakażenie szczepami STEC. Umożliwia ona szybkie (wynik otrzymujemy po około godzinie) określenie czy dany przypadek infekcji jest spowodowany przez szczep Escherichia coli, niosący geny toksyny Shiga. Celem niniejszych zajęć będzie określenie względnej liczby kopii plazmidów zawierających fragment genomu faga kodującego toksyny Shiga w odniesieniu do liczby komórek bakteryjnych obecnych w badanej próbce. Ze względów bezpieczeństwa, hodowle bakterii wykorzystane w czasie ćwiczeń zawierają mikroorganizmy pozbawione genów kodujących toksyny. Należy przeprowadzić następujące kroki: 1. Oszacowanie liczby komórek bakteryjnych w badanej próbce hodowli na podstawie odczytu absorbancji przy długości fali 600 nm: - Wykonujemy pomiar absorbancji hodowli bakteryjnej przy długości fali 600 nm - Na podstawie uzyskanego wyniku określamy ilość komórek bakteryjnych w 1ml hodowli zakładając, że 1ml hodowli o gęstości optycznej OD 600 =0,1 zawiera 10 8 komórek bakteryjnych 2. Przygotowanie matrycy do reakcji qpcr: - 1 ml hodowli bakteryjnej inkubujemy przez 5 minut w temperaturze 95 C - Przygotowujemy seryjne rozcieńczenia hodowli bakteryjnej poprzez dodanie 10 µl zawiesiny bakterii do 90 µl wody 3. Przygotowanie krzywej wzorcowej z wykorzystaniem próbek zawierających znaną ilość plazmidowego DNA (przygotowuje osoba prowadząca zajęcia). 4. Przygotowanie mieszaniny do reakcji qpcr: 5. Literatura: Mieszanina na 5 reakcji : - Woda - 7,5 µl - 2 x SYBR - 25 µl - Starter I - 2,5 µl - Starter II - 2,5 µl 37.5 µl, mieszaninę rozdzielić po 7,5 µl do odpowiednich studzienek na płytce 96-cio dołkowej Do każdej studzienki nałożyć 2,5 µl rozcieńczonej próbki ( ) 5. Analiza uzyskanych wyników oraz elektroforeza agarozowa produktów reakcji. 1. Introduction to quatitative PCR. Methods and Applications Guide. (Agilent Technologies) 2. Brzozowska E., Bazan J., Gamian A. (2010) Funkcje białek bakteriofagowych. Postepy Hig Med Dosw 65: Węgrzyn G., Węgrzyn A. (2006) Replikacja DNA bakteriofaga λ nowe odkrycia dokonane przy użyciu starego modelu badawczego. Postępy Biochemii 52: Zagadnienia do samodzielnego przygotowania: 1. Charakterystyka bakteriofagów (fagi łagodne i zjadliwe) na przykładzie bakteriofagów: λ, M13, P1, T4. 2. Cykle rozwojowe bakteriofagów (cykl lityczny, lizogenia, pseudolizogenia, infekcja przewlekła, etapy rozwoju bakteriofagów, inhibicja lizy). 3. Wyjaśnić pojęcia: profag, adsorpcja, latencja, eklipsa, liza od zewnątrz. 4. Replikacja DNA faga λ (etapy replikacji DNA, etapy inicjacji replikacji DNA, rola białek fagowych i białek gospodarza, białko inicjatorowe, helikaza, białka opiekuńcze, replikacja według modelu sigma, replikacja według modelu theta). Zadania: 1. Seryjne rozcieńczenie roztworu DNA plazmidowego: W probówce nr 1 znajduje się 100 µl roztworu plazmidowego DNA o stężeniu 200 ng/µl. 10 µl roztworu plazmidowego DNA z probówki nr 1, przeniesiono do probówki nr 2 zawierającej 90 µl wody. Jakie będzie stężenie DNA w probówce nr 2? Procedurę
6 powtórzono w ten sam sposób dodając 10 µl roztworu z probówki nr 2 do probówki nr 3, z probówki nr 3 do probówki nr 4 itd. (rycina 7.) Jakie będzie stężenie DNA w pozostałych probówkach? Rycina 6. Seryjne rozcieńczanie roztworu DNA plazmidowego. 2. Wykreślenie krzywej standardowej: W celu wykonania krzywej standardowej przeprowadzono reakcję qpcr z wykorzystaniem 1000, 100, 10 i 1 kopii plazmidowego DNA. Uzyskano następujące wyniki: Nr próbki Liczba kopii plazmidu użytego jako matryca do reakcji qpcr Wynik reakcji (numer cyklu progowego dla danej próbki) Na podstawie danych z tabeli wykreśl krzywą standardową:
7 Ct liczba kopii plazmidu 3. Określenie liczby kopii plazmidu w badanej próbce na podstawie krzywej standardowej. Przeprowadzono analizę liczby kopii plazmidu w próbce hodowli A z wykorzystaniem techniki qpcr. Hodowlę A rozcieńczono 1000 razy, a następnie do reakcji qpcr wykorzystano 2,5 µl rozcieńczonej hodowli. Poziom fluorescencji podczas reakcji qpcr przekroczył poziom progowy w 18 cyklu reakcji (Ct A =18). Na podstawie krzywej standardowej (ryc. 7) oszacuj liczbę kopii plazmidu w nie rozcieńczonej próbce A. Pamiętaj, że badana próbka była 1000 razy rozcieńczona. Ct liczba kopii plazmidu Rycina 7. Przykładowa krzywa standardowa. 4. Określenie relatywnej liczby kopii plazmidu w odniesieniu do liczby komórek bakteryjnych w badanej hodowli. Na podstawie wyniku poprzedniego zadania oszacuj przybliżona liczbę kopii plazmidu w przeliczeniu na 1 komórkę bakteryjną, wiedząc, że hodowla A miała gęstość optyczną OD 600 ~0,2. (Przyjmij, że w 1ml hodowli bakteryjnej o OD 600 ~0,1 znajduje się 10 8 komórek bakteryjnych )
Powodzenie reakcji PCR wymaga właściwego doboru szeregu parametrów:
 Powodzenie reakcji PCR wymaga właściwego doboru szeregu parametrów: dobór warunków samej reakcji PCR (temperatury, czas trwania cykli, ilości cykli itp.) dobór odpowiednich starterów do reakcji amplifikacji
Powodzenie reakcji PCR wymaga właściwego doboru szeregu parametrów: dobór warunków samej reakcji PCR (temperatury, czas trwania cykli, ilości cykli itp.) dobór odpowiednich starterów do reakcji amplifikacji
Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu
 Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu
 Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Ćwiczenie 4 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6: wykrywanie liczby kopii genu Wstęp CYP2D6 kodowany przez gen występujący w co najmniej w 78 allelicznych formach związanych ze zmniejszoną
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA
 Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa tel. 22 572 0735, 606448502
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa tel. 22 572 0735, 606448502
TaqNova-RED. Polimeraza DNA RP20R, RP100R
 TaqNova-RED Polimeraza DNA RP20R, RP100R RP20R, RP100R TaqNova-RED Polimeraza DNA Rekombinowana termostabilna polimeraza DNA Taq zawierająca czerwony barwnik, izolowana z Thermus aquaticus, o przybliżonej
TaqNova-RED Polimeraza DNA RP20R, RP100R RP20R, RP100R TaqNova-RED Polimeraza DNA Rekombinowana termostabilna polimeraza DNA Taq zawierająca czerwony barwnik, izolowana z Thermus aquaticus, o przybliżonej
PCR - ang. polymerase chain reaction
 PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
Biologia medyczna, materiały dla studentów
 Zasada reakcji PCR Reakcja PCR (replikacja in vitro) obejmuje denaturację DNA, przyłączanie starterów (annealing) i syntezę nowych nici DNA (elongacja). 1. Denaturacja: rozplecenie nici DNA, temp. 94 o
Zasada reakcji PCR Reakcja PCR (replikacja in vitro) obejmuje denaturację DNA, przyłączanie starterów (annealing) i syntezę nowych nici DNA (elongacja). 1. Denaturacja: rozplecenie nici DNA, temp. 94 o
SCENARIUSZ LEKCJI BIOLOGII Z WYKORZYSTANIEM FILMU PCR sposób na DNA.
 SCENARIUSZ LEKCJI BIOLOGII Z WYKORZYSTANIEM FILMU PCR sposób na DNA. SPIS TREŚCI: 1. Wprowadzenie. 2. Części lekcji. 1. Część wstępna. 2. Część realizacji. 3. Część podsumowująca. 3. Karty pracy. 1. Karta
SCENARIUSZ LEKCJI BIOLOGII Z WYKORZYSTANIEM FILMU PCR sposób na DNA. SPIS TREŚCI: 1. Wprowadzenie. 2. Części lekcji. 1. Część wstępna. 2. Część realizacji. 3. Część podsumowująca. 3. Karty pracy. 1. Karta
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA
 Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa IZOLACJA DNA Z HODOWLI KOMÓRKOWEJ.
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa IZOLACJA DNA Z HODOWLI KOMÓRKOWEJ.
TaqNovaHS. Polimeraza DNA RP902A, RP905A, RP910A, RP925A RP902, RP905, RP910, RP925
 TaqNovaHS RP902A, RP905A, RP910A, RP925A RP902, RP905, RP910, RP925 RP902A, RP905A, RP910A, RP925A RP902, RP905, RP910, RP925 TaqNovaHS Polimeraza TaqNovaHS jest mieszaniną termostabilnej polimerazy DNA
TaqNovaHS RP902A, RP905A, RP910A, RP925A RP902, RP905, RP910, RP925 RP902A, RP905A, RP910A, RP925A RP902, RP905, RP910, RP925 TaqNovaHS Polimeraza TaqNovaHS jest mieszaniną termostabilnej polimerazy DNA
Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16
 Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16 Ćwiczenie 3 Identyfikacja genetycznie modyfikowanych roślin w produktach spożywczych - jakościowe badanie obecności
Genetyczne modyfikowanie organizmów Kierunek OCHRONA ŚRODOWISKA, II rok semestr letni 2015/16 Ćwiczenie 3 Identyfikacja genetycznie modyfikowanych roślin w produktach spożywczych - jakościowe badanie obecności
Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan
 Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan Klasyczna metoda PCR jest metodą jakościową, nie ilościową co np.
Ćwiczenie 3 Oznaczenie polimorfizmu genetycznego cytochromu CYP2D6 metodą PCR w czasie rzeczywistym (rtpcr) przy użyciu sond typu TaqMan Klasyczna metoda PCR jest metodą jakościową, nie ilościową co np.
AmpliTest Babesia spp. (PCR)
 AmpliTest Babesia spp. (PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla pierwotniaków z rodzaju Babesia techniką PCR Nr kat.: BAC21-100 Wielkość zestawu: 100 oznaczeń Objętość pojedynczej reakcji:
AmpliTest Babesia spp. (PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla pierwotniaków z rodzaju Babesia techniką PCR Nr kat.: BAC21-100 Wielkość zestawu: 100 oznaczeń Objętość pojedynczej reakcji:
Biologia Molekularna z Biotechnologią ===============================================================================================
 Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Przedmiot: Katedra Biologii Molekularnej Biologia
Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Przedmiot: Katedra Biologii Molekularnej Biologia
PCR - ang. polymerase chain reaction
 PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR łańcuchowa reakcja polimerazy
 PCR łańcuchowa reakcja polimerazy PCR - ang. polymerase chain reaction Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR łańcuchowa reakcja polimerazy PCR - ang. polymerase chain reaction Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
Genetyka, materiały dla studentów Pielęgniarstwa
 Markery genetyczne: definicja Marker genetyczny jest to cecha, która może być wykorzystana do identyfikacji osobników lub gatunków. Cechy markerów genetycznych Monogeniczny: warunkowany przez jeden gen
Markery genetyczne: definicja Marker genetyczny jest to cecha, która może być wykorzystana do identyfikacji osobników lub gatunków. Cechy markerów genetycznych Monogeniczny: warunkowany przez jeden gen
AmpliTest Salmonella spp. (Real Time PCR)
 AmpliTest Salmonella spp. (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii z rodzaju Salmonella techniką Real Time PCR Nr kat.: BAC01-50 Wielkość zestawu: 50 oznaczeń Objętość
AmpliTest Salmonella spp. (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii z rodzaju Salmonella techniką Real Time PCR Nr kat.: BAC01-50 Wielkość zestawu: 50 oznaczeń Objętość
PCR - ang. polymerase chain reaction
 PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
PCR - ang. polymerase chain reaction łańcuchowa (cykliczna) reakcja polimerazy Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu
Ampli-LAMP Babesia canis
 Novazym Products Zestaw do identyfikacji materiału genetycznego pierwotniaka Babesia canis canis techniką Loop-mediated Isothermal AMPlification (LAMP) Numery katalogowe produktu: AML-Bc-200 AML-Bc-400
Novazym Products Zestaw do identyfikacji materiału genetycznego pierwotniaka Babesia canis canis techniką Loop-mediated Isothermal AMPlification (LAMP) Numery katalogowe produktu: AML-Bc-200 AML-Bc-400
Zestaw do wykrywania Chlamydia trachomatis w moczu lub w kulturach komórkowych
 Nr kat. PK15 Wersja zestawu: 1.2016 Zestaw do wykrywania w moczu lub w kulturach komórkowych na 50 reakcji PCR (50µl), włączając w to kontrole Detekcja oparta jest na amplifikacji fragmentu genu crp (cysteine
Nr kat. PK15 Wersja zestawu: 1.2016 Zestaw do wykrywania w moczu lub w kulturach komórkowych na 50 reakcji PCR (50µl), włączając w to kontrole Detekcja oparta jest na amplifikacji fragmentu genu crp (cysteine
Hybrydyzacja kwasów nukleinowych
 Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
AmpliTest GMO screening-nos (Real Time PCR)
 AmpliTest GMO screening-nos (Real Time PCR) Zestaw do wykrywania sekwencji DNA terminatora NOS techniką Real Time PCR Nr kat.: GMO03-50 GMO03-100 Wielkość zestawu: 50 reakcji 100 reakcji Objętość pojedynczej
AmpliTest GMO screening-nos (Real Time PCR) Zestaw do wykrywania sekwencji DNA terminatora NOS techniką Real Time PCR Nr kat.: GMO03-50 GMO03-100 Wielkość zestawu: 50 reakcji 100 reakcji Objętość pojedynczej
Definicje. Białka rekombinowane (ang. recombinant proteins, r-proteins) Ukierunkowana mutageneza (ang. site-directed/site-specific mutagenesis)
 Definicje Białka rekombinowane (ang. recombinant proteins, r-proteins) Białka, które powstały w żywych organizmach (lub liniach komórkowych) w wyniku ekspresji rekombinowanego DNA. Rekombinowany DNA jest
Definicje Białka rekombinowane (ang. recombinant proteins, r-proteins) Białka, które powstały w żywych organizmach (lub liniach komórkowych) w wyniku ekspresji rekombinowanego DNA. Rekombinowany DNA jest
Klonowanie molekularne Kurs doskonalący. Zakład Geriatrii i Gerontologii CMKP
 Klonowanie molekularne Kurs doskonalący Zakład Geriatrii i Gerontologii CMKP Etapy klonowania molekularnego 1. Wybór wektora i organizmu gospodarza Po co klonuję (do namnożenia DNA [czy ma być metylowane
Klonowanie molekularne Kurs doskonalący Zakład Geriatrii i Gerontologii CMKP Etapy klonowania molekularnego 1. Wybór wektora i organizmu gospodarza Po co klonuję (do namnożenia DNA [czy ma być metylowane
ĆWICZENIE 1 i 2 Modyfikacja geu wołowej beta-laktoglobuliny przy użyciu metody Overlap Extension PCR (wydłużania nakładających się odcinków)
 ĆWICZENIE 1 i 2 Modyfikacja geu wołowej beta-laktoglobuliny przy użyciu metody Overlap Extension PCR (wydłużania nakładających się odcinków) Celem ćwiczenia jest wprowadzenie mutacji punktowej do genu
ĆWICZENIE 1 i 2 Modyfikacja geu wołowej beta-laktoglobuliny przy użyciu metody Overlap Extension PCR (wydłużania nakładających się odcinków) Celem ćwiczenia jest wprowadzenie mutacji punktowej do genu
Zestaw do wykrywania Babesia spp. i Theileria spp. w kleszczach, krwi i hodowlach komórkowych
 Nr kat. PK25N Wersja zestawu: 1.2012 Zestaw do wykrywania spp. i Theileria spp. w kleszczach, krwi i hodowlach komórkowych dwie oddzielne reakcje PCR 2x50 reakcji PCR (50 µl), włączając w to kontrole Zestaw
Nr kat. PK25N Wersja zestawu: 1.2012 Zestaw do wykrywania spp. i Theileria spp. w kleszczach, krwi i hodowlach komórkowych dwie oddzielne reakcje PCR 2x50 reakcji PCR (50 µl), włączając w to kontrole Zestaw
Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych
 Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych Wstęp teoretyczny Technika RAPD (ang. Random Amplification of Polymorphic DNA) opiera się na prostej reakcji PCR, przeprowadzanej na genomowym
Zastosowanie metody RAPD do różnicowania szczepów bakteryjnych Wstęp teoretyczny Technika RAPD (ang. Random Amplification of Polymorphic DNA) opiera się na prostej reakcji PCR, przeprowadzanej na genomowym
Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV
 Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV Cel ćwiczenia Określenie podatności na zakażenie wirusem HIV poprzez detekcję homo lub heterozygotyczności
Ćwiczenie 3. Amplifikacja genu ccr5 Homo sapiens wykrywanie delecji Δ32pz warunkującej oporność na wirusa HIV Cel ćwiczenia Określenie podatności na zakażenie wirusem HIV poprzez detekcję homo lub heterozygotyczności
Zestaw do wykrywania Anaplasma phagocytophilum w kleszczach, krwi i hodowlach komórkowych
 Nr kat. PK24N Wersja zestawu: 1.2016 Zestaw do wykrywania phagocytophilum w kleszczach, krwi i hodowlach komórkowych dwie oddzielne reakcje PCR 2x50 reakcji PCR (50 µl), włączając w to kontrole Detekcja
Nr kat. PK24N Wersja zestawu: 1.2016 Zestaw do wykrywania phagocytophilum w kleszczach, krwi i hodowlach komórkowych dwie oddzielne reakcje PCR 2x50 reakcji PCR (50 µl), włączając w to kontrole Detekcja
Applied Biosystems 7500 Fast Real Time PCR System, czyli Mercedes wśród termocyklerów do analizy PCR w czasie rzeczywistym
 Applied Biosystems 7500 Fast Real Time PCR System, czyli Mercedes wśród termocyklerów do analizy PCR w czasie rzeczywistym Rynek aparatury laboratoryjnej pęka w szwach od ilości różnych aparatów przeznaczonych
Applied Biosystems 7500 Fast Real Time PCR System, czyli Mercedes wśród termocyklerów do analizy PCR w czasie rzeczywistym Rynek aparatury laboratoryjnej pęka w szwach od ilości różnych aparatów przeznaczonych
2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy
 Metody analizy DNA 1. Budowa DNA. 2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy 3. Klonowanie in vivo a. w bakteriach, wektory plazmidowe b. w fagach, kosmidy c. w drożdżach,
Metody analizy DNA 1. Budowa DNA. 2. Enzymy pozwalające na manipulację DNA a. Polimerazy DNA b. Nukleazy c. Ligazy 3. Klonowanie in vivo a. w bakteriach, wektory plazmidowe b. w fagach, kosmidy c. w drożdżach,
Platforma Genie II. innowacyjne narzędzie do identyfikacji materiału genetycznego patogenów techniką LAMP Loop-mediated Isothermal AMPlification
 1 Platforma Genie II innowacyjne narzędzie do identyfikacji materiału genetycznego patogenów techniką LAMP Loop-mediated Isothermal AMPlification 1 2 Charakterystyka platformy Genie II Genie II jest innowacyjnym
1 Platforma Genie II innowacyjne narzędzie do identyfikacji materiału genetycznego patogenów techniką LAMP Loop-mediated Isothermal AMPlification 1 2 Charakterystyka platformy Genie II Genie II jest innowacyjnym
AmpliTest Chlamydia/Chlamydophila (Real Time PCR)
 AmpliTest Chlamydia/Chlamydophila (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii z rodzajów Chlamydia i Chlamydophila techniką Real Time PCR Nr kat.: BAC18-50 BAC18-100 Wielkość
AmpliTest Chlamydia/Chlamydophila (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii z rodzajów Chlamydia i Chlamydophila techniką Real Time PCR Nr kat.: BAC18-50 BAC18-100 Wielkość
Bożena Nejman-Faleńczyk
 Kontrola replikacji fagów lambdoidalnych niosących geny toksyn Shiga w świetle potencjalnych nowych metod ich wykrywania i terapii zakażeń enterokrwotocznymi szczepami Escherichia coli Bożena Nejman-Faleńczyk
Kontrola replikacji fagów lambdoidalnych niosących geny toksyn Shiga w świetle potencjalnych nowych metod ich wykrywania i terapii zakażeń enterokrwotocznymi szczepami Escherichia coli Bożena Nejman-Faleńczyk
Parametr Wymagany parametr Oferowany parametr 1. 2. 3. a) z wbudowaną pompą membranową PTEE, b) kondensorem par, System
 Załącznik nr 1A do SIWZ. PARAMETRY TECHNICZNE PRZEDMIOTU ZAMÓWIENIA Zadanie nr 1. TERMOSTAT CYRKULACYJNY Termostat cyrkulacyjny Z grzaniem i chłodzeniem Zakres temperatury roboczej 25 o C do + 200 o C
Załącznik nr 1A do SIWZ. PARAMETRY TECHNICZNE PRZEDMIOTU ZAMÓWIENIA Zadanie nr 1. TERMOSTAT CYRKULACYJNY Termostat cyrkulacyjny Z grzaniem i chłodzeniem Zakres temperatury roboczej 25 o C do + 200 o C
Hybrydyzacja kwasów nukleinowych
 Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja tego genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Hybrydyzacja kwasów nukleinowych Jaka jest lokalizacja tego genu na chromosomie? Jakie jest jego sąsiedztwo? Hybrydyzacja - powstawanie stabilnych struktur dwuniciowych z cząsteczek jednoniciowych o komplementarnych
Farmakogenetyka Biotechnologia Medyczna I o
 ĆWICZENIE 2 Oznaczanie polimorfizmu cytochromu CYP2D6 za pomocą tradycyjnych metod biologii molekularnej: PCR-RFLP I. Łańcuchowa reakcja polimerazy PCR (polymerase chain reaction) Technika PCR rozwinęła
ĆWICZENIE 2 Oznaczanie polimorfizmu cytochromu CYP2D6 za pomocą tradycyjnych metod biologii molekularnej: PCR-RFLP I. Łańcuchowa reakcja polimerazy PCR (polymerase chain reaction) Technika PCR rozwinęła
PL 217144 B1. Sposób amplifikacji DNA w łańcuchowej reakcji polimerazy za pomocą starterów specyficznych dla genu receptora 2-adrenergicznego
 PL 217144 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 217144 (13) B1 Urząd Patentowy Rzeczypospolitej Polskiej (21) Numer zgłoszenia: 391926 (22) Data zgłoszenia: 23.07.2010 (51) Int.Cl.
PL 217144 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 217144 (13) B1 Urząd Patentowy Rzeczypospolitej Polskiej (21) Numer zgłoszenia: 391926 (22) Data zgłoszenia: 23.07.2010 (51) Int.Cl.
Zestaw dydaktyczny. genotypowanie szczepów 5taphy/ococcus aureus metodą PCR-RFLP
 2014-07-17 Zestaw dydaktyczny EasyGenotyping PCR-RFLP - S. aureus genotypowanie szczepów 5taphy/ococcus aureus metodą PCR-RFLP Celem ćwiczenia jest przeprowadzenie typowania genetycznego dostarczonych
2014-07-17 Zestaw dydaktyczny EasyGenotyping PCR-RFLP - S. aureus genotypowanie szczepów 5taphy/ococcus aureus metodą PCR-RFLP Celem ćwiczenia jest przeprowadzenie typowania genetycznego dostarczonych
Ćwiczenia 1 Wirtualne Klonowanie Prowadzący: mgr inż. Joanna Tymeck-Mulik i mgr Lidia Gaffke. Część teoretyczna:
 Uniwersytet Gdański, Wydział Biologii Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią Biologia II rok ===============================================================================================
Uniwersytet Gdański, Wydział Biologii Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią Biologia II rok ===============================================================================================
PCR - ang. polymerase chain reaction
 PCR - ang. polymerase chain reaction Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu DNA) Jest to reakcja powielania (replikacji)
PCR - ang. polymerase chain reaction Technika PCR umożliwia otrzymywanie dużej liczby kopii specyficznych fragmentów DNA (czyli amplifikację zwielokrotnienie fragmentu DNA) Jest to reakcja powielania (replikacji)
Ćwiczenie 3 PCR i trawienie DNA enzymami restrykcyjnymi
 Uniwersytet Gdański, Wydział Biologii Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Katedra Biologii Molekularnej Biologia i Biologia Medyczna II rok Przedmiot: Biologia
Uniwersytet Gdański, Wydział Biologii Katedra Genetyki Molekularnej Bakterii Katedra Biologii i Genetyki Medycznej Katedra Biologii Molekularnej Biologia i Biologia Medyczna II rok Przedmiot: Biologia
Mechanizmy kontroli ekspresji genów w regulacji rozwoju bakteriofagów lambdoidalnych
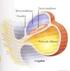 Mechanizmy kontroli ekspresji genów w regulacji rozwoju bakteriofagów lambdoidalnych Sylwia Bloch Bakteriofagi lambdoidalne to grupa wirusów bakteryjnych, zaliczanych do rodziny Siphoviridae, których najlepiej
Mechanizmy kontroli ekspresji genów w regulacji rozwoju bakteriofagów lambdoidalnych Sylwia Bloch Bakteriofagi lambdoidalne to grupa wirusów bakteryjnych, zaliczanych do rodziny Siphoviridae, których najlepiej
Ilość TAK TAK TAK TAK TAK TAK
 Postępowanie WB.2420.6.2013.NG ZAŁĄCZNIK NR 5 L.p. Nazwa asortymentu parametry techniczne Ilość Nazwa wyrobu, nazwa producenta, określenie marki, modelu, znaku towarowego Cena jednostkowa netto (zł) Wartość
Postępowanie WB.2420.6.2013.NG ZAŁĄCZNIK NR 5 L.p. Nazwa asortymentu parametry techniczne Ilość Nazwa wyrobu, nazwa producenta, określenie marki, modelu, znaku towarowego Cena jednostkowa netto (zł) Wartość
SYLABUS. Wydział Biologiczno-Rolniczy. Katedra Biochemii i Biologii Komórki
 SYLABUS 1.1. PODSTAWOWE INFORMACJE O PRZEDMIOCIE/MODULE Nazwa przedmiotu/ modułu Biologia molekularna Kod przedmiotu/ modułu* Wydział (nazwa jednostki prowadzącej kierunek) Nazwa jednostki realizującej
SYLABUS 1.1. PODSTAWOWE INFORMACJE O PRZEDMIOCIE/MODULE Nazwa przedmiotu/ modułu Biologia molekularna Kod przedmiotu/ modułu* Wydział (nazwa jednostki prowadzącej kierunek) Nazwa jednostki realizującej
AmpliTest Panel odkleszczowy (Real Time PCR)
 AmpliTest Panel odkleszczowy (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii Borrelia burgdorferi, Anaplasma, Ehrlichia oraz pierwotniaków rodzaju Babesia (B. canis, B. gibsoni,
AmpliTest Panel odkleszczowy (Real Time PCR) Zestaw do wykrywania sekwencji DNA specyficznych dla bakterii Borrelia burgdorferi, Anaplasma, Ehrlichia oraz pierwotniaków rodzaju Babesia (B. canis, B. gibsoni,
Ćwiczenie numer 6. Analiza próbek spożywczych na obecność markerów GMO
 Ćwiczenie numer 6 Analiza próbek spożywczych na obecność markerów GMO 1. Informacje wstępne -screening GMO -metoda CTAB -qpcr 2. Izolacja DNA z soi metodą CTAB 3. Oznaczenie ilościowe i jakościowe DNA
Ćwiczenie numer 6 Analiza próbek spożywczych na obecność markerów GMO 1. Informacje wstępne -screening GMO -metoda CTAB -qpcr 2. Izolacja DNA z soi metodą CTAB 3. Oznaczenie ilościowe i jakościowe DNA
Metody odczytu kolejności nukleotydów - sekwencjonowania DNA
 Metody odczytu kolejności nukleotydów - sekwencjonowania DNA 1. Metoda chemicznej degradacji DNA (metoda Maxama i Gilberta 1977) 2. Metoda terminacji syntezy łańcucha DNA - klasyczna metoda Sangera (Sanger
Metody odczytu kolejności nukleotydów - sekwencjonowania DNA 1. Metoda chemicznej degradacji DNA (metoda Maxama i Gilberta 1977) 2. Metoda terminacji syntezy łańcucha DNA - klasyczna metoda Sangera (Sanger
Badanie próbek żywności na obecność Genetycznie Zmodyfikowanych Organizmów. Rozdział 9
 Badanie próbek żywności na obecność Genetycznie Zmodyfikowanych Organizmów Rozdział 9 Wykrywanie jakościowe kukurydzy MON810, kukurydzy Bt-176 i soi Roundup Ready metodą PCR M. Querci, M. Maretti, M. Mazzara
Badanie próbek żywności na obecność Genetycznie Zmodyfikowanych Organizmów Rozdział 9 Wykrywanie jakościowe kukurydzy MON810, kukurydzy Bt-176 i soi Roundup Ready metodą PCR M. Querci, M. Maretti, M. Mazzara
Mieszanina trójfosforanów deoksyrybonukleotydów (dntp: datp, dgtp, dctp, dttp) Bufor reakcyjny zapewniający odpowiednie warunki reakcji
 Uniwersytet Gdański, Wydział Biologii Biologia i Biologia medyczna II rok Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią =================================================================
Uniwersytet Gdański, Wydział Biologii Biologia i Biologia medyczna II rok Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią =================================================================
Scenariusz lekcji z biologii w szkole ponadgimnazjalnej
 Scenariusz lekcji z biologii w szkole ponadgimnazjalnej Temat lekcji: Planowanie doświadczeń biologicznych jak prawidłowo zaplanować próbę kontrolną? Cele kształcenia IV etap edukacyjny: 1. Wymagania ogólne:
Scenariusz lekcji z biologii w szkole ponadgimnazjalnej Temat lekcji: Planowanie doświadczeń biologicznych jak prawidłowo zaplanować próbę kontrolną? Cele kształcenia IV etap edukacyjny: 1. Wymagania ogólne:
Polimeraza Taq (1U/ l) 1-2 U 1 polimeraza Taq jako ostatni składniki mieszaniny końcowa objętość
 Ćwiczenie 6 Technika PCR Celem ćwiczenia jest zastosowanie techniki PCR do amplifikacji fragmentu DNA z bakterii R. leguminosarum bv. trifolii TA1 (RtTA1). Studenci przygotowują reakcję PCR wykorzystując
Ćwiczenie 6 Technika PCR Celem ćwiczenia jest zastosowanie techniki PCR do amplifikacji fragmentu DNA z bakterii R. leguminosarum bv. trifolii TA1 (RtTA1). Studenci przygotowują reakcję PCR wykorzystując
SYLABUS. Wydział Biologiczno-Rolniczy. Katedra Biochemii i Biologii Komórki
 SYLABUS 1.1. PODSTAWOWE INFORMACJE O PRZEDMIOCIE/MODULE Nazwa przedmiotu/ modułu Biologia molekularna z elementami inżynierii genetycznej Kod przedmiotu/ modułu* Wydział (nazwa jednostki prowadzącej kierunek)
SYLABUS 1.1. PODSTAWOWE INFORMACJE O PRZEDMIOCIE/MODULE Nazwa przedmiotu/ modułu Biologia molekularna z elementami inżynierii genetycznej Kod przedmiotu/ modułu* Wydział (nazwa jednostki prowadzącej kierunek)
Glimmer umożliwia znalezienie regionów kodujących
 Narzędzia ułatwiające identyfikację właściwych genów GLIMMER TaxPlot Narzędzia ułatwiające amplifikację tych genów techniki PCR Primer3, Primer3plus PrimerBLAST Reverse Complement Narzędzia ułatwiające
Narzędzia ułatwiające identyfikację właściwych genów GLIMMER TaxPlot Narzędzia ułatwiające amplifikację tych genów techniki PCR Primer3, Primer3plus PrimerBLAST Reverse Complement Narzędzia ułatwiające
RT31-020, RT , MgCl 2. , random heksamerów X 6
 RT31-020, RT31-100 RT31-020, RT31-100 Zestaw TRANSCRIPTME RNA zawiera wszystkie niezbędne składniki do przeprowadzenia syntezy pierwszej nici cdna na matrycy mrna lub całkowitego RNA. Uzyskany jednoniciowy
RT31-020, RT31-100 RT31-020, RT31-100 Zestaw TRANSCRIPTME RNA zawiera wszystkie niezbędne składniki do przeprowadzenia syntezy pierwszej nici cdna na matrycy mrna lub całkowitego RNA. Uzyskany jednoniciowy
Inżynieria Genetyczna ćw. 3
 Materiały do ćwiczeń z przedmiotu Genetyka z inżynierią genetyczną D - blok Inżynieria Genetyczna ćw. 3 Instytut Genetyki i Biotechnologii, Wydział Biologii, Uniwersytet Warszawski, rok akad. 2018/2019
Materiały do ćwiczeń z przedmiotu Genetyka z inżynierią genetyczną D - blok Inżynieria Genetyczna ćw. 3 Instytut Genetyki i Biotechnologii, Wydział Biologii, Uniwersytet Warszawski, rok akad. 2018/2019
Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY)
 Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY) Cel ćwiczenia Amplifikacja fragmentu genu amelogeniny, znajdującego się na chromosomach X i Y, jako celu molekularnego przydatnego
Ćwiczenie 2. Identyfikacja płci z wykorzystaniem genu amelogeniny (AMGXY) Cel ćwiczenia Amplifikacja fragmentu genu amelogeniny, znajdującego się na chromosomach X i Y, jako celu molekularnego przydatnego
Ampli-LAMP Goose Parvovirus
 Novazym Products Zestaw do identyfikacji materiału genetycznego parwowirusa GPV u gęsi techniką Loop-mediated Isothermal AMPlification (LAMP) Numery katalogowe produktu: AML-GPV-200 AML-GPV-400 Wydanie
Novazym Products Zestaw do identyfikacji materiału genetycznego parwowirusa GPV u gęsi techniką Loop-mediated Isothermal AMPlification (LAMP) Numery katalogowe produktu: AML-GPV-200 AML-GPV-400 Wydanie
Inżynieria genetyczna- 6 ECTS
 Inżynieria genetyczna- 6 ECTS Część I Badanie ekspresji genów Kolokwium (14pkt) Część II Podstawy klonowania i różnicowania transformantów Klonowanie ekspresyjne Od genu do białka Kolokwium (26pkt) EGZAMIN
Inżynieria genetyczna- 6 ECTS Część I Badanie ekspresji genów Kolokwium (14pkt) Część II Podstawy klonowania i różnicowania transformantów Klonowanie ekspresyjne Od genu do białka Kolokwium (26pkt) EGZAMIN
PCR. Aleksandra Sałagacka
 PCR Aleksandra Sałagacka Reakcja PCR naśladuje proces replikacji DNA in vitro pozwala na amplifikację określonego krótkiego (kilkadziesiąt kilka tys.pz) fragmentu DNA obecnie najważniejsze narzędzie biologii
PCR Aleksandra Sałagacka Reakcja PCR naśladuje proces replikacji DNA in vitro pozwala na amplifikację określonego krótkiego (kilkadziesiąt kilka tys.pz) fragmentu DNA obecnie najważniejsze narzędzie biologii
Instrukcja ćwiczeń Biologia molekularna dla II roku Analityki Medycznej. Reakcja odwrotnej transkrypcji. Projektowanie starterów do reakcji PCR.
 INSTRUKCJA Ćwiczenie nr 5 Odczynniki: Sprzęt: 1. 5xNG cdna Buffer 2. 50 µm oligo(dt)20 3. NG dart RT mix l 4. Probówki typu Eppendorf 0,2 ml 5. Woda wolna od RNaz 6. Lód 1. Miniwirówka 2. Termocykler 3.
INSTRUKCJA Ćwiczenie nr 5 Odczynniki: Sprzęt: 1. 5xNG cdna Buffer 2. 50 µm oligo(dt)20 3. NG dart RT mix l 4. Probówki typu Eppendorf 0,2 ml 5. Woda wolna od RNaz 6. Lód 1. Miniwirówka 2. Termocykler 3.
POLIMERAZY DNA- PROCARYOTA
 Enzymy DNA-zależne, katalizujące syntezę DNA wykazują aktywność polimerazy zawsze w kierunku 5 3 wykazują aktywność polimerazy zawsze wobec jednoniciowej cząsteczki DNA do utworzenia kompleksu z ssdna
Enzymy DNA-zależne, katalizujące syntezę DNA wykazują aktywność polimerazy zawsze w kierunku 5 3 wykazują aktywność polimerazy zawsze wobec jednoniciowej cząsteczki DNA do utworzenia kompleksu z ssdna
Markery klasy II -Polimorfizm fragmentów DNA (na ogół niekodujących): - RFLP - VNTR - RAPD
 Marker genetyczny- polimorficzna cecha jakościowa organizmu, którą charakteryzuje proste dziedziczenie (mendlowskie) oraz którą można dokładnie identyfikować metodami analitycznymi. Markery klasy I - Antygeny
Marker genetyczny- polimorficzna cecha jakościowa organizmu, którą charakteryzuje proste dziedziczenie (mendlowskie) oraz którą można dokładnie identyfikować metodami analitycznymi. Markery klasy I - Antygeny
Walidacja metod wykrywania, identyfikacji i ilościowego oznaczania GMO. Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB
 Walidacja metod wykrywania, identyfikacji i ilościowego oznaczania GMO Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB Walidacja Walidacja jest potwierdzeniem przez zbadanie i przedstawienie
Walidacja metod wykrywania, identyfikacji i ilościowego oznaczania GMO Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB Walidacja Walidacja jest potwierdzeniem przez zbadanie i przedstawienie
Metody: PCR, MLPA, Sekwencjonowanie, PCR-RLFP, PCR-Multiplex, PCR-ASO
 Diagnostyka molekularna Dr n.biol. Anna Wawrocka Strategia diagnostyki genetycznej: Aberracje chromosomowe: Metody:Analiza kariotypu, FISH, acgh, MLPA, QF-PCR Gen(y) znany Metody: PCR, MLPA, Sekwencjonowanie,
Diagnostyka molekularna Dr n.biol. Anna Wawrocka Strategia diagnostyki genetycznej: Aberracje chromosomowe: Metody:Analiza kariotypu, FISH, acgh, MLPA, QF-PCR Gen(y) znany Metody: PCR, MLPA, Sekwencjonowanie,
7. Metody molekularne jako źródło informacji botanicznej i lichenologicznej
 7. Metody molekularne jako źródło informacji botanicznej i lichenologicznej 7.2. Metody biologii molekularnej (technika PCR, sekwencjonowanie DNA) wykorzystywane w taksonomii roślin Autor: Magdalena Dudek
7. Metody molekularne jako źródło informacji botanicznej i lichenologicznej 7.2. Metody biologii molekularnej (technika PCR, sekwencjonowanie DNA) wykorzystywane w taksonomii roślin Autor: Magdalena Dudek
PCR PCR. Model replikacji semikonserwatywnej
 PCR Łańcuchowa reakcja polimerazy (Polymerase Chain Reaction) amplifikacja (namnożenie wielu kopii cząsteczki kwasu nukleinowego) w pierwotnej wersji wykorzystująca model replikacji semikonserwatywnej
PCR Łańcuchowa reakcja polimerazy (Polymerase Chain Reaction) amplifikacja (namnożenie wielu kopii cząsteczki kwasu nukleinowego) w pierwotnej wersji wykorzystująca model replikacji semikonserwatywnej
Ćwiczenie 5 Klonowanie DNA w wektorach plazmidowych
 Ćwiczenie 5 Klonowanie DNA w wektorach plazmidowych Celem ćwiczenia jest sklonowanie fragmentu DNA (powielonego techniką PCR i wyizolowanego z żelu agarozowego na poprzednich zajęciach) do wektora plazmidowego
Ćwiczenie 5 Klonowanie DNA w wektorach plazmidowych Celem ćwiczenia jest sklonowanie fragmentu DNA (powielonego techniką PCR i wyizolowanego z żelu agarozowego na poprzednich zajęciach) do wektora plazmidowego
Diagnostyka molekularna w OIT
 Diagnostyka molekularna w OIT B A R B A R A A D A M I K K A T E D R A I K L I N I K A A N E S T E Z J O L O G I I I I N T E N S Y W N E J T E R A P I I U N I W E R S Y T E T M E D Y C Z N Y W E W R O C
Diagnostyka molekularna w OIT B A R B A R A A D A M I K K A T E D R A I K L I N I K A A N E S T E Z J O L O G I I I I N T E N S Y W N E J T E R A P I I U N I W E R S Y T E T M E D Y C Z N Y W E W R O C
Analiza genetyczna w niepowodzeniach ciąży i badaniach prenatalnych
 Analiza genetyczna w niepowodzeniach ciąży i badaniach prenatalnych Dr n. med. Joanna Walczak- Sztulpa Katedra i Zakład Genetyki Medycznej Uniwersytet Medyczny im. Karola Marcinkowskiego w Poznaniu Diagnostyka
Analiza genetyczna w niepowodzeniach ciąży i badaniach prenatalnych Dr n. med. Joanna Walczak- Sztulpa Katedra i Zakład Genetyki Medycznej Uniwersytet Medyczny im. Karola Marcinkowskiego w Poznaniu Diagnostyka
Nowoczesne systemy ekspresji genów
 Nowoczesne systemy ekspresji genów Ekspresja genów w organizmach żywych GEN - pojęcia podstawowe promotor sekwencja kodująca RNA terminator gen Gen - odcinek DNA zawierający zakodowaną informację wystarczającą
Nowoczesne systemy ekspresji genów Ekspresja genów w organizmach żywych GEN - pojęcia podstawowe promotor sekwencja kodująca RNA terminator gen Gen - odcinek DNA zawierający zakodowaną informację wystarczającą
Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1
 Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1 1 Zakład Genetyki i Hodowli Roślin Korzeniowych, Pracownia Biotechnologii, Instytut Hodowli i Aklimatyzacji
Anna Litwiniec 1, Beata Choińska 1, Aleksander Łukanowski 2, Żaneta Świtalska 1, Maria Gośka 1 1 Zakład Genetyki i Hodowli Roślin Korzeniowych, Pracownia Biotechnologii, Instytut Hodowli i Aklimatyzacji
GENOMIKA FUNKCJONALNA. Jak działają geny i genomy? Poziom I: Analizy transkryptomu
 GENOMIKA FUNKCJONALNA Jak działają geny i genomy? Poziom I: Analizy transkryptomu Adnotacja (ang. annotation) pierwszy etap po uzyskaniu kompletnej sekwencji nukleotydyowej genomu analiza bioinformatyczna
GENOMIKA FUNKCJONALNA Jak działają geny i genomy? Poziom I: Analizy transkryptomu Adnotacja (ang. annotation) pierwszy etap po uzyskaniu kompletnej sekwencji nukleotydyowej genomu analiza bioinformatyczna
(62) Numer zgłoszenia, z którego nastąpiło wydzielenie:
 PL 227091 B1 RZECZPOSPOLITA POLSKA Urząd Patentowy Rzeczypospolitej Polskiej (12) OPIS PATENTOWY (19) PL (11) 227091 (21) Numer zgłoszenia: 419590 (22) Data zgłoszenia: 20.01.2014 (62) Numer zgłoszenia,
PL 227091 B1 RZECZPOSPOLITA POLSKA Urząd Patentowy Rzeczypospolitej Polskiej (12) OPIS PATENTOWY (19) PL (11) 227091 (21) Numer zgłoszenia: 419590 (22) Data zgłoszenia: 20.01.2014 (62) Numer zgłoszenia,
PCR PCR. Model replikacji semikonserwatywnej
 PCR Łańcuchowa reakcja polimerazy (Polymerase Chain Reaction) amplifikacja (namnożenie wielu kopii cząsteczki kwasu nukleinowego) w pierwotnej wersji wykorzystująca model replikacji semikonserwatywnej
PCR Łańcuchowa reakcja polimerazy (Polymerase Chain Reaction) amplifikacja (namnożenie wielu kopii cząsteczki kwasu nukleinowego) w pierwotnej wersji wykorzystująca model replikacji semikonserwatywnej
(wypełnia Wykonawca) (wypełnia Wykonawca) (wypełnia Wykonawca)
 Załącznik nr 1, znak sprawy DZ-2501/192/18 CZĘŚĆ 1: TERMOCYKLER DO REAL-TIME PCR, ILOŚĆ: 1 SZT Określenie przedmiotu zamówienia zgodnie ze Wspólnym Słownikiem Zamówień (CPV): 38500000-0 aparatura kontrolna
Załącznik nr 1, znak sprawy DZ-2501/192/18 CZĘŚĆ 1: TERMOCYKLER DO REAL-TIME PCR, ILOŚĆ: 1 SZT Określenie przedmiotu zamówienia zgodnie ze Wspólnym Słownikiem Zamówień (CPV): 38500000-0 aparatura kontrolna
Biologia Molekularna Podstawy
 Biologia Molekularna Podstawy Budowa DNA Budowa DNA Zasady: Purynowe: adenina i guanina Pirymidynowe: cytozyna i tymina 2 -deoksyryboza Grupy fosforanowe Budowa RNA Budowa RNA Zasady: purynowe: adenina
Biologia Molekularna Podstawy Budowa DNA Budowa DNA Zasady: Purynowe: adenina i guanina Pirymidynowe: cytozyna i tymina 2 -deoksyryboza Grupy fosforanowe Budowa RNA Budowa RNA Zasady: purynowe: adenina
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Analityka Medyczna 2016
 Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Analityka Medyczna 2016 Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa Analiza
Zakład Biologii Molekularnej Materiały do ćwiczeń z przedmiotu: BIOLOGIA MOLEKULARNA Analityka Medyczna 2016 Zakład Biologii Molekularnej Wydział Farmaceutyczny, WUM ul. Banacha 1, 02-097 Warszawa Analiza
KLONOWANIE DNA REKOMBINACJA DNA WEKTORY
 KLONOWANIE DNA Klonowanie DNA jest techniką powielania fragmentów DNA DNA można powielać w komórkach (replikacja in vivo) W probówce (PCR) Do przeniesienia fragmentu DNA do komórek gospodarza potrzebny
KLONOWANIE DNA Klonowanie DNA jest techniką powielania fragmentów DNA DNA można powielać w komórkach (replikacja in vivo) W probówce (PCR) Do przeniesienia fragmentu DNA do komórek gospodarza potrzebny
HODOWLA PERIODYCZNA DROBNOUSTROJÓW
 Cel ćwiczenia: Celem ćwiczenia jest porównanie zdolności rozkładu fenolu lub wybranej jego pochodnej przez szczepy Stenotrophomonas maltophilia KB2 i Pseudomonas sp. CF600 w trakcie prowadzenia hodowli
Cel ćwiczenia: Celem ćwiczenia jest porównanie zdolności rozkładu fenolu lub wybranej jego pochodnej przez szczepy Stenotrophomonas maltophilia KB2 i Pseudomonas sp. CF600 w trakcie prowadzenia hodowli
ĆWICZENIA Z MECHANIZMÓW DZIAŁANIA WYBRANYCH GRUP LEKÓW
 UNIWERSYTET MARII CURIE-SKŁODOWSKIEJ WYDZIAŁ BIOLOGII I BIOTECHNOLOGII ZAKŁAD BIOLOGII MOLEKULARNEJ ĆWICZENIA Z MECHANIZMÓW DZIAŁANIA WYBRANYCH GRUP LEKÓW dla studentów I roku II 0 biotechnologii medycznej
UNIWERSYTET MARII CURIE-SKŁODOWSKIEJ WYDZIAŁ BIOLOGII I BIOTECHNOLOGII ZAKŁAD BIOLOGII MOLEKULARNEJ ĆWICZENIA Z MECHANIZMÓW DZIAŁANIA WYBRANYCH GRUP LEKÓW dla studentów I roku II 0 biotechnologii medycznej
Ampli-LAMP Salmonella species
 Novazym Products Novazym Polska ul. Żywokostowa 23, 61-680 Poznań, tel. +48 0 61 610 39 10, fax +48 0 61 610 39 11, email info@novazym.com Zestaw do identyfikacji materiału genetycznego bakterii z rodzaju
Novazym Products Novazym Polska ul. Żywokostowa 23, 61-680 Poznań, tel. +48 0 61 610 39 10, fax +48 0 61 610 39 11, email info@novazym.com Zestaw do identyfikacji materiału genetycznego bakterii z rodzaju
Dane mikromacierzowe. Mateusz Markowicz Marta Stańska
 Dane mikromacierzowe Mateusz Markowicz Marta Stańska Mikromacierz Mikromacierz DNA (ang. DNA microarray) to szklana lub plastikowa płytka (o maksymalnych wymiarach 2,5 cm x 7,5 cm) z naniesionymi w regularnych
Dane mikromacierzowe Mateusz Markowicz Marta Stańska Mikromacierz Mikromacierz DNA (ang. DNA microarray) to szklana lub plastikowa płytka (o maksymalnych wymiarach 2,5 cm x 7,5 cm) z naniesionymi w regularnych
Instrukcje do ćwiczeń oraz zakres materiału realizowanego na wykładach z przedmiotu Inżynieria bioprocesowa na kierunku biotechnologia
 1 Zakład Mikrobiologii UJK Instrukcje do ćwiczeń oraz zakres materiału realizowanego na wykładach z przedmiotu Inżynieria bioprocesowa na kierunku biotechnologia 2 Zakład Mikrobiologii UJK Zakres materiału
1 Zakład Mikrobiologii UJK Instrukcje do ćwiczeń oraz zakres materiału realizowanego na wykładach z przedmiotu Inżynieria bioprocesowa na kierunku biotechnologia 2 Zakład Mikrobiologii UJK Zakres materiału
SKUTECZNOŚĆ IZOLACJI JAK ZMIERZYĆ ILOŚĆ KWASÓW NUKLEINOWYCH PO IZOLACJI? JAK ZMIERZYĆ ILOŚĆ KWASÓW NUKLEINOWYCH PO IZOLACJI?
 SKUTECZNOŚĆ IZOLACJI Wydajność izolacji- ilość otrzymanego kwasu nukleinowego Efektywność izolacji- jakość otrzymanego kwasu nukleinowego w stosunku do ilości Powtarzalność izolacji- zoptymalizowanie procedury
SKUTECZNOŚĆ IZOLACJI Wydajność izolacji- ilość otrzymanego kwasu nukleinowego Efektywność izolacji- jakość otrzymanego kwasu nukleinowego w stosunku do ilości Powtarzalność izolacji- zoptymalizowanie procedury
CEL ĆWICZENIA: Zapoznanie się z przykładową procedurą odsalania oczyszczanych preparatów enzymatycznych w procesie klasycznej filtracji żelowej.
 LABORATORIUM 3 Filtracja żelowa preparatu oksydazy polifenolowej (PPO) oczyszczanego w procesie wysalania siarczanem amonu z wykorzystaniem złoża Sephadex G-50 CEL ĆWICZENIA: Zapoznanie się z przykładową
LABORATORIUM 3 Filtracja żelowa preparatu oksydazy polifenolowej (PPO) oczyszczanego w procesie wysalania siarczanem amonu z wykorzystaniem złoża Sephadex G-50 CEL ĆWICZENIA: Zapoznanie się z przykładową
Metody badania ekspresji genów
 Metody badania ekspresji genów dr Katarzyna Knapczyk-Stwora Warunki wstępne: Proszę zapoznać się z tematem Metody badania ekspresji genów zamieszczonym w skrypcie pod reakcją A. Lityńskiej i M. Lewandowskiego
Metody badania ekspresji genów dr Katarzyna Knapczyk-Stwora Warunki wstępne: Proszę zapoznać się z tematem Metody badania ekspresji genów zamieszczonym w skrypcie pod reakcją A. Lityńskiej i M. Lewandowskiego
PL B1. UNIWERSYTET PRZYRODNICZY W LUBLINIE, Lublin, PL BUP 26/11
 PL 214501 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 214501 (13) B1 (21) Numer zgłoszenia: 391458 (51) Int.Cl. C12Q 1/68 (2006.01) C12N 15/29 (2006.01) Urząd Patentowy Rzeczypospolitej Polskiej
PL 214501 B1 RZECZPOSPOLITA POLSKA (12) OPIS PATENTOWY (19) PL (11) 214501 (13) B1 (21) Numer zgłoszenia: 391458 (51) Int.Cl. C12Q 1/68 (2006.01) C12N 15/29 (2006.01) Urząd Patentowy Rzeczypospolitej Polskiej
METODY MOLEKULARNE STOSOWANE W TAKSONOMII
 METODY MOLEKULARNE STOSOWANE W TAKSONOMII AUTOR: MAGDALENA DUDEK Taksonomia jest nauką, której głównym celem jest badanie, opisywanie oraz klasyfikacja organizmów. W oparciu o różnice i podobieństwa łączy
METODY MOLEKULARNE STOSOWANE W TAKSONOMII AUTOR: MAGDALENA DUDEK Taksonomia jest nauką, której głównym celem jest badanie, opisywanie oraz klasyfikacja organizmów. W oparciu o różnice i podobieństwa łączy
Informacje dotyczące pracy kontrolnej
 Informacje dotyczące pracy kontrolnej Słuchacze, którzy z przyczyn usprawiedliwionych nie przystąpili do pracy kontrolnej lub otrzymali z niej ocenę negatywną zobowiązani są do dnia 06 grudnia 2015 r.
Informacje dotyczące pracy kontrolnej Słuchacze, którzy z przyczyn usprawiedliwionych nie przystąpili do pracy kontrolnej lub otrzymali z niej ocenę negatywną zobowiązani są do dnia 06 grudnia 2015 r.
POLIMERAZY DNA- PROCARYOTA
 Enzymy DNA-zależne, katalizujące syntezę DNA wykazują aktywność polimerazy zawsze w kierunku 5 3 wykazują aktywność polimerazy zawsze wobec jednoniciowej cząsteczki DNA do utworzenia kompleksu z ssdna
Enzymy DNA-zależne, katalizujące syntezę DNA wykazują aktywność polimerazy zawsze w kierunku 5 3 wykazują aktywność polimerazy zawsze wobec jednoniciowej cząsteczki DNA do utworzenia kompleksu z ssdna
Metody analiz GMO. Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB
 Metody analiz GMO Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB 09.10.2017 GMO Organizm Genetycznie Zmodyfikowany - organizm inny niż organizm człowieka, w którym materiał genetyczny został
Metody analiz GMO Magdalena Żurawska-Zajfert Laboratorium Kontroli GMO IHAR-PIB 09.10.2017 GMO Organizm Genetycznie Zmodyfikowany - organizm inny niż organizm człowieka, w którym materiał genetyczny został
Dr Anna Linkiewicz Instytut Hodowli i Aklimatyzacji Roślin - PIB LAB-GMO Maj 2015
 Genetycznie modyfikowana żywność i pasze Streszczenie zajęć Blisko 50 różnych GMO jest dopuszczonych do stosowania w Unii Europejskiej jako żywność lub pasza. Podczas zajęć wyizolowane zostanie DNA z produktów
Genetycznie modyfikowana żywność i pasze Streszczenie zajęć Blisko 50 różnych GMO jest dopuszczonych do stosowania w Unii Europejskiej jako żywność lub pasza. Podczas zajęć wyizolowane zostanie DNA z produktów
Wstęp. Jak programować w DNA? Idea oraz przykład. Problem FSAT charakterystyka i rozwiązanie za pomocą DNA. Jak w ogólności rozwiązywać problemy
 Ariel Zakrzewski Wstęp. Jak programować w DNA? Idea oraz przykład. Problem FSAT charakterystyka i rozwiązanie za pomocą DNA. Jak w ogólności rozwiązywać problemy matematyczne z użyciem DNA? Gdzie są problemy?
Ariel Zakrzewski Wstęp. Jak programować w DNA? Idea oraz przykład. Problem FSAT charakterystyka i rozwiązanie za pomocą DNA. Jak w ogólności rozwiązywać problemy matematyczne z użyciem DNA? Gdzie są problemy?
Ćwiczenia 1 Wirtualne Klonowanie. Prowadzący: mgr Anna Pawlik i mgr Maciej Dylewski. Część teoretyczna:
 Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią ===============================================================================================
Uniwersytet Gdański, Wydział Biologii Biologia i Biologia Medyczna II rok Katedra Biologii Molekularnej Przedmiot: Biologia Molekularna z Biotechnologią ===============================================================================================
KINETYKA HYDROLIZY SACHAROZY
 Ćwiczenie nr 2 KINETYKA HYDROLIZY SACHAROZY I. Kinetyka hydrolizy sacharozy reakcja chemiczna Zasada: Sacharoza w środowisku kwaśnym ulega hydrolizie z wytworzeniem -D-glukozy i -D-fruktozy. Jest to reakcja
Ćwiczenie nr 2 KINETYKA HYDROLIZY SACHAROZY I. Kinetyka hydrolizy sacharozy reakcja chemiczna Zasada: Sacharoza w środowisku kwaśnym ulega hydrolizie z wytworzeniem -D-glukozy i -D-fruktozy. Jest to reakcja
Technika fluorescencyjnego oznaczania aktywności enzymów. Wstęp:
 Technika fluorescencyjnego oznaczania aktywności enzymów Wstęp: Wśród technik biologii molekularnej jedną z najczęściej stosowanych jest technika fluorescencyjna. Stosując technikę fluorescencyjną można
Technika fluorescencyjnego oznaczania aktywności enzymów Wstęp: Wśród technik biologii molekularnej jedną z najczęściej stosowanych jest technika fluorescencyjna. Stosując technikę fluorescencyjną można
Dr. habil. Anna Salek International Bio-Consulting 1 Germany
 1 2 3 Drożdże są najprostszymi Eukariontami 4 Eucaryota Procaryota 5 6 Informacja genetyczna dla każdej komórki drożdży jest identyczna A zatem każda komórka koduje w DNA wszystkie swoje substancje 7 Przy
1 2 3 Drożdże są najprostszymi Eukariontami 4 Eucaryota Procaryota 5 6 Informacja genetyczna dla każdej komórki drożdży jest identyczna A zatem każda komórka koduje w DNA wszystkie swoje substancje 7 Przy
